蘇山豬和巴克夏豬全基因組ROH檢測和選擇信號分析

摘" 要: 旨在明確蘇山豬群體和巴克夏豬群體的遺傳變異位點和多態信息,本研究首先對43個蘇山豬樣本和21個巴克夏豬樣本進行DNA提取,然后利用“中芯一號”50K SNP芯片對DNA的SNP位點進行檢測;使用 Plink軟件對SNP 位點進行主成分分析;使用 DetectRUNS 軟件包對樣本進行全基因組ROH檢測;選用3種方法(ROH、CLR和iHS)對選擇信號進行分析。本研究總共鑒定到蘇山豬42 282個SNPs 位點和巴克夏豬27 718個SNPs 位點。其中,蘇山豬和巴克夏豬均被劃分為3個家系。本研究在蘇山豬中共檢測到2 071個ROH片段,FROH平均值為0.096。巴克夏豬中共檢測到1 853個ROH片段,FROH平均值為0.199。在蘇山豬和巴克夏豬群體中分別檢測到4個和40個高頻ROH區域,分別注釋到8個和103個基因,通過富集分析鑒定了50個顯著的候選基因。另外,通過ROH、CLR和iHS共3種選擇信號分析方法,對蘇山豬和巴克夏豬的選擇信號區域進行了鑒定,發現有42個基因可能受到選擇。本研究初步揭示了蘇山豬和巴克夏豬的基因組SNP圖譜,并通過高頻ROH分析和選擇信號檢測鑒定到一些可能影響豬的生長發育、肉質、營養和一般抗病力的基因,為蘇山豬和巴克夏豬的選育利用提供了理論基礎。
關鍵詞: 豬;ROH;CLR;iHS;選擇信號
中圖分類號:S828.2
文獻標志碼:A
文章編號:0366-6964(2024)12-5452-12
doi: 10.11843/j.issn.0366-6964.2024.12.012
開放科學(資源服務)標識碼(OSID):
收稿日期:2024-06-18
基金項目:江蘇省種業振興揭榜掛帥項目(JBGS[2021]099);江蘇省青年基金項目(BK20230753);國家生豬產業技術體系(CARS-PIG-35)
作者簡介:戴超輝(1993-),女,湖南新化人,博士,助理研究員,主要從事豬遺傳育種與繁殖研究,E-mail: chdai@jaas.ac.cn
*通信作者:程金花,主要從事豬遺傳育種與繁殖研究,E-mail: jhcheng@jaas.ac.cn;包文斌,主要從事豬抗病育種研究,E-mail: wbbao@yzu.edu.cn
Whole Genome ROH Detection and Selection Signal Analysis in Sushan Pigs and Berkshire Pigs
DAI" Chaohui1, CUI" Lekang2, LInbsp; Hui1, ZHAO" Weimin1, FU" Yanfeng1, LI" Bixia1, WANG" Xuemin1, LIAO" Chao1, CHEN" Yanyu3, BAO" Wenbin2*, CHENG" Jinhua1*
(1.Institute of Animal Science, Jiangsu Academy of Agricultural Sciences, Key Laboratory of Crop and Livestock Integration of Ministry of Agriculture and Rural Affairs, Jiangsu Germplasm Resources Protection and Utilization Platform, Nanjing 210014," China;
2.College of Animal Science and Technology, Yangzhou University, Yangzhou 225009," China;
3.ProNet Biotech Co., Ltd., Nanjing 210033," China)
Abstract: In order to clarify the genetic variation sites and polymorphic information of the Sushan pig population and the Berkshire pig population, the DNA samples from 43 Sushan pigs and 21 Berkshire pigs were extracted and SNP sites were detected by 50K SNP beadchip in this study. Plink software was used for principal component analysis of the SNP sites; The DetectRUNS software package was used for whole-genome ROH detection of the samples; Three methods (ROH, CLR, and iHS) were used to analyze the selection signals. A total of 42 282 SNPs were identified in Sushan pigs and 27 718 SNPs in Berkshire pigs. Both breeds were divided into 3 families. There were 2 071 ROH segments were detected in Sushan pigs with an average FROH value of 0.096, and 1 853 ROH segments were detected in Berkshire pigs with an average FROH value of 0.199. Four and 40 high-frequency ROH regions were detected in the Sushan pig and Berkshire pig populations, respectively, which were annotated to 8 and 103 genes. There were 50 significant candidate genes were identified through enrichment analysis. Additionally, three selection signal analysis methods (ROH, CLR and iHS) were used to identify selection signal regions in Sushan pigs and Berkshire pigs, which illustrated that 42 genes could be under selection. This study preliminarily revealed the genomic SNP pattern of Sushan pigs and Berkshire pigs and excavated some genes that may affect pig growth and development, meat quality, nutrition, and general disease resistance by high-frequency ROH analysis and selection signal detection, which provided a theoretical basis for the breeding and utilization of Sushan pigs and Berkshire pigs.
Key words: pig; ROH; CLR; iHS; selection signal
*Corresponding authors:" CHENG Jinhua, E-mail: jhcheng@jaas.ac.cn; BAO Wenbin, E-mail: wbbao@yzu.edu.cn
單核苷酸多態性(single nucleotide polymorphism, SNP)是基因組研究中的一個重要領域,SNP是指基因組DNA序列中單個核苷酸位點上的變異,這種變異通常表現為二等位性,即在特定位點上只有兩種可能的核苷酸存在[1]。SNP是基因組中最常見的遺傳變異形式,它們在豬基因組中的分布非常廣泛,平均每300~400個堿基對就有一個SNP位點[2]。這種高密度的SNPs分布為豬的遺傳多樣性研究、遺傳圖譜構建、數量性狀位點(QTL)定位以及全基因組關聯分析提供了豐富的遺傳標記。隨著SNP芯片技術的發展,研究人員能夠在全基因組水平上進行高密度的SNP基因分型,這對于開展豬的全基因組關聯研究具有重要意義。目前開發應用的豬SNP芯片主要包括國外研發的PorcineSNP60 Beadchip(Illumina公司)、Porcine SNP 50K Beadchip(Geneseek 公司)和(Neogene)以及國內自主研發設計的KPS Porcine Breeding Chip v2(中芯一號,江西農業大學開發)、PorcineWens55K芯片(溫氏股份研發)、液相 50K 芯片(中國農業大學開發)和64K cGPS液相芯片(湖南農業大學)等[3]。其中,“中芯一號”被廣泛應用于中國地方豬遺傳結構及遺傳多樣性研究,為地方豬品種的保護利用和持續選育提供了有力保障[4-7]。
蘇山豬是江蘇省農業科學院畜牧研究所利用英國大白公豬與蘇鐘豬母豬雜交選育形成的優質高產瘦肉豬新品種,毛色為白色,頭中等大小,嘴筒和臉略凹,耳中等大小,背腰平直,腹線平,腿臀豐滿,四肢健壯,有效乳頭 14 枚以上,具有優質(肉色鮮紅、肌內脂肪含量 2.56%)、高產(產仔數13.6頭、日增重786 g、料重比2.89∶1、胴體瘦肉率59.4%)、抗逆(耐粗纖維可達11.3%、抗喘氣病強)等特點,肉質口感保留了太湖豬的風味特色,產仔數保留了太湖豬的高繁殖力特性,既可純繁生產優質豬肉,又可作為母本與長白或杜洛克二元雜交替代“外三元”[8]。巴克夏豬起源于英國中南部的巴克夏郡和威爾郡,1862年正式確定為一個品種,并于21世紀初引入國內。巴克夏豬典型的品種外貌特點為全身被毛黑色,僅四肢下部、嘴端、尾尖為白色,稱“六白”,頭短、立耳、顏面微凹,嘴筒直,胸寬深,背腰平直,四肢短粗健壯,適應性強,抗病力強,耐粗飼,飼料利用率高,生長快,較為早熟,易肥,因其肉質鮮嫩、肌間脂肪分布均勻的特性一直受到廣大消費者的青睞,是我國地方黑豬雜交生產精品-極品優質肉的最佳終端父本。筆者所在的研究團隊目前正開展巴克夏與蘇山豬選育利用研究,項目在前期品種培育和新品系選育的基礎上,按照優質豬肉生產的需求和育種目標,采用分子標記輔助選擇與BLUP模型相結合的方式重點圍繞生長速度、肉品質和繁殖性能等性狀,培育各具特色的蘇山豬和巴克夏豬專門化品系。因此,對蘇山豬和巴克夏豬群體進行遺傳評估是非常必要的。而基因選擇信號研究對于理解特定物種的遺傳演化和適應性具有重要意義,通過識別基因組中受到正選擇的區域,可以揭示某些特定性狀的關鍵基因,這些性狀可能與生存能力、繁殖成功率或對環境的適應性有關[9]。
為了明確蘇山豬群體和巴克夏豬群體的遺傳變異位點和多態信息,尤其是群體選擇信號信息,本研究利用“中芯一號”對43個蘇山豬樣本和21個巴克夏豬樣本進行檢測,揭示蘇山豬和巴克夏豬ROH及選擇信號的相關遺傳信息,旨在為蘇山豬和巴克夏豬的專門化品系選育及配套系利用奠定理論基礎,也為同行開展雜交選育提供更多的試驗參考和依據。
1" 材料與方法
1.1" 試驗動物
本研究中的蘇山豬群體目前保存在揚州市眾誠生態農業有限公司,巴克夏豬保存在江蘇金洋宇生態農牧有限公司。采集耳組織樣品,保存于含75%酒精的1.5 mL離心管中,然后轉移至-20 ℃冰箱備用。
1.2" DNA提取及SNP芯片分型
利用高效動物基因組DNA提取試劑盒(擎科生物,北京,中國)對43個蘇山豬樣本和21個巴克夏豬耳組織樣進行基因組DNA提取,質檢合格后委托北京康普森生物技術有限公司利用“中芯一號”SNP芯片進行基因分型。利用Plink軟件對芯片數據進行質控:剔除性染色體上的位點;SNP 檢出率≥90%;個體檢出率≥90%;最小等位基因頻率≥0.01;哈迪-溫伯格平衡檢測P值≥0.000 001。
1.3" 群體主成分和進化樹分析
使用 Plink(V1.90)對蘇山豬與巴克夏豬SNP 位點進行主成分分析(principal component analysis,PCA),參數為:--pca 5 header;將得到的 eigenval 文件使用 R(4.1.2)進行可視化。使用Mega(v11.0.9)[10]對IBS距離矩陣以鄰接法(neighbor-joining,NJ)構建進化樹。
1.4" ROH檢測及近交系數計算
基因組上的長純合片段(runs of homozygosity,ROH)是個體內純合基因型的連續片段,它是由親代將同源單倍型完整地傳遞給子代而產生。本研究使用DetectRUNS 軟件包(https://cran.r-project.org/web/packages/detectRUNS/index.html)對蘇山豬與巴克夏豬進行全基因組ROH檢測,檢測參數為windowSize=50,threshold=0.05,minSNP=30,ROHet=FALSE,maxOppWindow=1,maxMissWindow=1,maxGap=250 000,minLengthBps=1 000 000,minDensity=1/100,maxOppRun=NULL,maxMissRun=NULL。通過如下公式計算個體 ROH 的近交系數(FROH),最終使用DetectRUNS軟件包中的summaryRuns()函數進行結果整理:
FROH=∑kLength(ROHk)L
其中,k 是個體的 ROH 數目,L 是該物種常染色體基因組的長度(豬 V10.2 版本的基因組,常染色體長度約2 450 462.292 kb)。
1.5" 高頻ROH區域基因鑒定
統計每個SNP在各自豬群體內參與組成ROH的次數占樣本數的比例,并將ROH頻率高于1%的 SNP 區域作為高頻ROH區域,利用RCircos包繪制2個豬群體ROH頻率在染色體上分布的Circos圖。基于高頻ROH區段的物理位置,利用Ensembl基因組數據庫對捕獲的ROH熱點區域進行基因注釋,挖掘已報道的與豬重要經濟性狀相關的功能基因。利用DAVID數據庫對高頻ROH區域注釋到的基因進行基因本體(gene ontology,GO)功能富集和京都基因與基因組百科全書(kyoto encyclopedia of genes and genomes,KEGG)通路富集分析,當Plt;0.05時,則表示顯著富集。將顯著富集到生物學過程和信號通路的基因與豬數量性狀基因座(quantitative trait locus,QTL)數據進行比對,獲得候選功能基因。
1.6" 選擇信號分析
本研究選用3種互補的方法(ROH、CLR和iHS)來識別可能處于選擇下的基因組區域。ROH是基于群體分化與基因組雜合度的2種選擇信號檢測的方法。使用Vcftools軟件[11]分別對蘇山豬與巴克夏豬進行固定指數(fixation index,Fst)分析與核苷酸多態性比值分析(πA/πB,π-ratio),窗口為1 000 kb,步長100 kb。對2種方法篩選前5%的候選選擇區域取交集作為最終選擇信號區域。使用 ANNOVAR[12]進行基因注釋,利用David 在線軟件對提取到的受選擇區域候選基因進行GO功能和KEGG通路富集分析。
復合似然比(composite likelihood ratio, CLR)可以用來識別基因組中可能受到自然選擇影響的區域。本研究使用SweepFinder2軟件[13]來計算每個位點的CLR值。在每個窗口內,選取了復合似然比(CLR)的最大值作為該窗口的代表性統計量,篩選出了位于前1%的窗口作為候選區域。同樣地,使用 ANNOVAR進行基因注釋,利用David 在線軟件對提取到的受選擇區域候選基因進行GO功能和KEGG通路富集分析。
iHS(integrated haplotype score)是一種用于檢測基因組中正選擇信號的統計方法。本研究采用了R語言的rehh包版本3.0[14]來計算iHS值,然后對所有標準化的iHS值取絕對值,將|iHS|值前1%的所有位點定義為強受選擇位點。同樣地,使用 ANNOVAR進行基因注釋,利用David 在線軟件對提取到的受選擇區域候選基因進行GO功能和KEGG通路富集分析。最后,利用3種分析方法中的至少2種取交集篩選可能的候選基因。
2" 結" 果
2. 1" 芯片數據質控
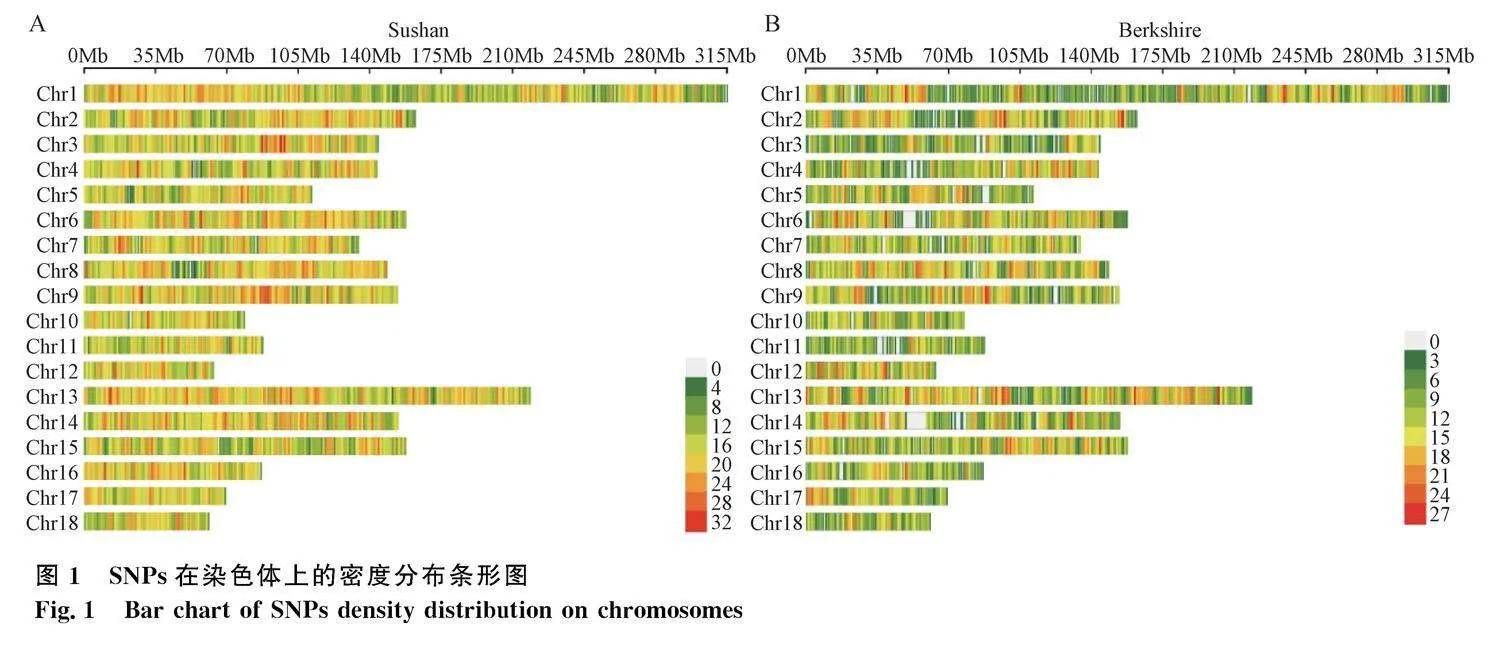
本研究使用的“中芯一號”芯片包括 57 466個位點,檢測的蘇山豬和巴克夏豬SNPs在染色體上分布如圖1所示。由圖可知,這兩個品種基因組SNPs在染色體上的分布基本類似,均表現為比較豐富的遺傳多樣性。利用Plink軟件對數據進行質控,經過SNP缺失率、最小等位基因頻率、哈迪-溫伯格平衡檢驗過濾后蘇山豬得到42 282個有效SNPs位點,巴克夏豬得到27 718個有效SNPs位點,用于后續分析。
2.2" 主成分分析和進化樹分析
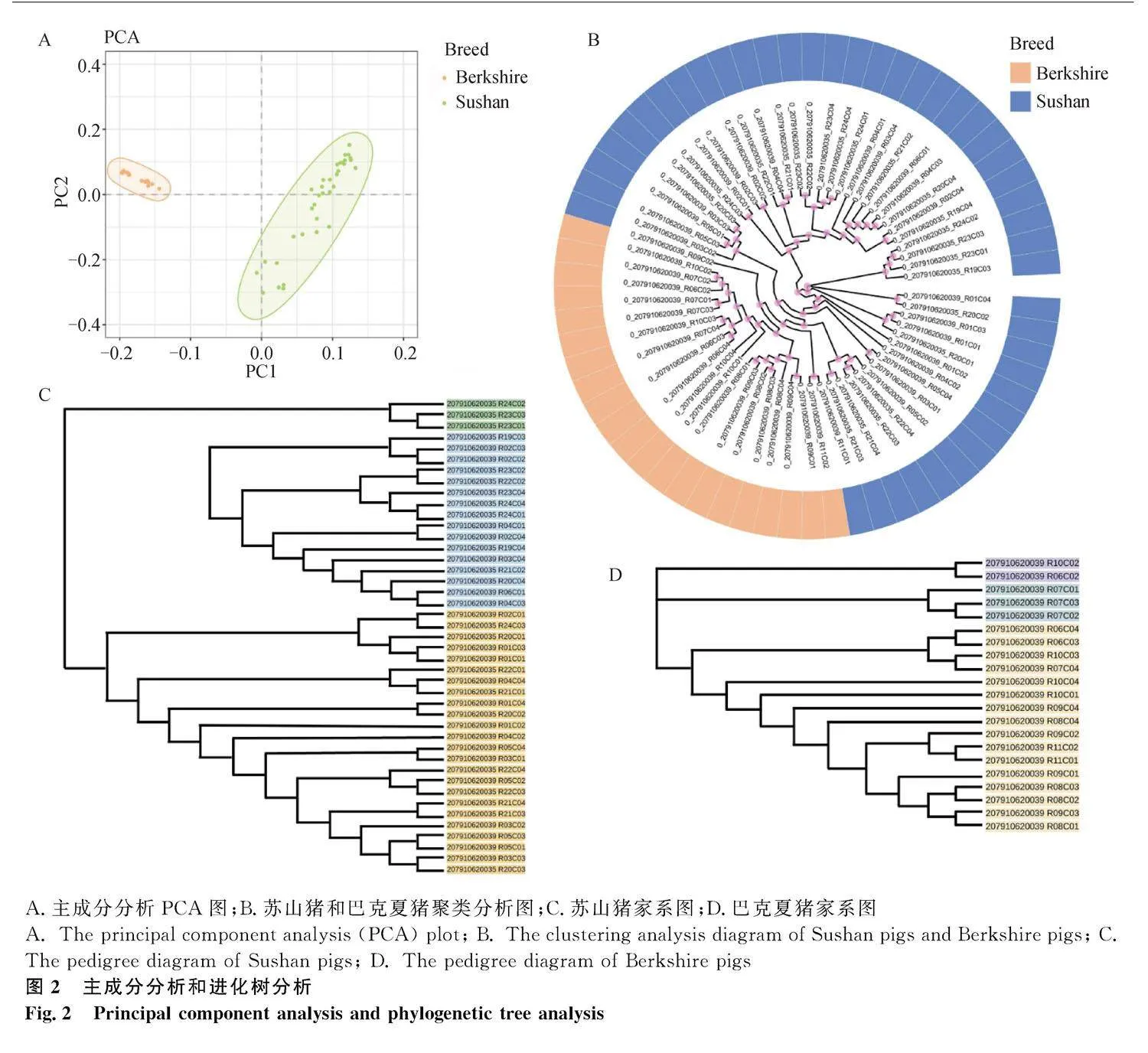
利用主成分(PCA)分析對SNP 芯片分型數據的準確性進行評估,結果發現(圖2A)蘇山豬和巴克夏豬呈現明顯分離,2個群體間具有單獨聚類,其親緣關系相差較遠。說明本研究所選擇的群體是2個獨立的群體,且此次分型結果可靠性較高。對蘇山豬和巴克夏豬進行聚類分析,發現蘇山豬聚為一類,巴克夏豬聚為一類,兩個豬品種區分比較明顯(圖2B)。對蘇山豬和巴克夏豬進行系統發育樹分析,發現本次研究中的蘇山豬和巴克夏豬群體均被劃分為3個家系(圖2C和2D)。
2.3" ROH分析
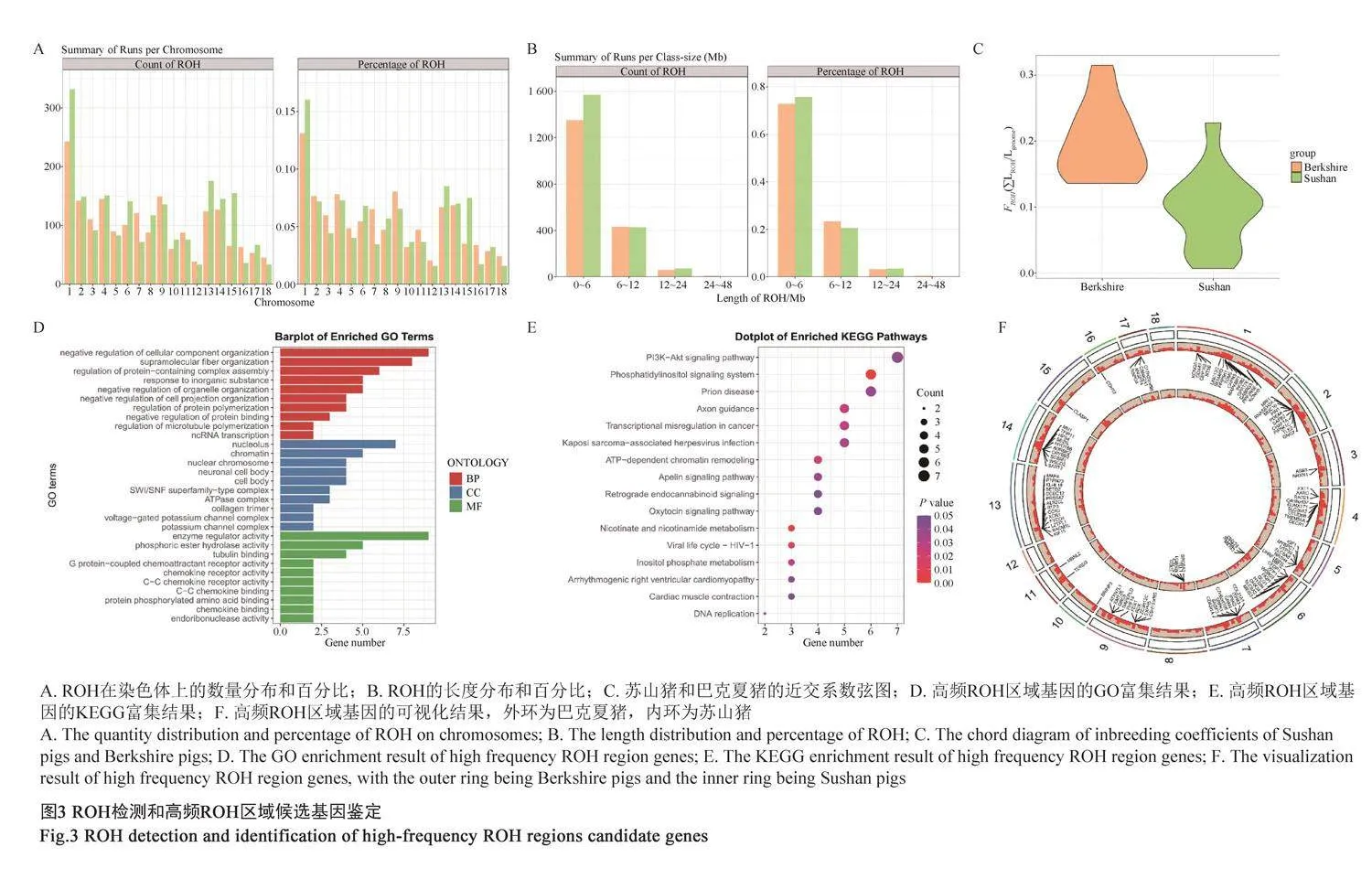
本研究發現,在42頭蘇山豬中共檢測到2 071個ROH片段,在21頭巴克夏豬中共檢測到1 853個ROH片段,且均表現為1號染色體上ROH數量最多,12號染色體上ROH數量最少(圖3A)。另外,兩個豬品種ROH長度在0~6 Mb之間的個體數目最多,百分比均超過70%(圖3B)。對蘇山豬和巴克夏豬進行近交系數分析發現,蘇山豬基因組FROH最大值為0.227,最小值為0.007,平均值為0.096;巴克夏豬基因組FROH最大值為0.315,最小值為0.136,平均值為0.199(圖3C)。
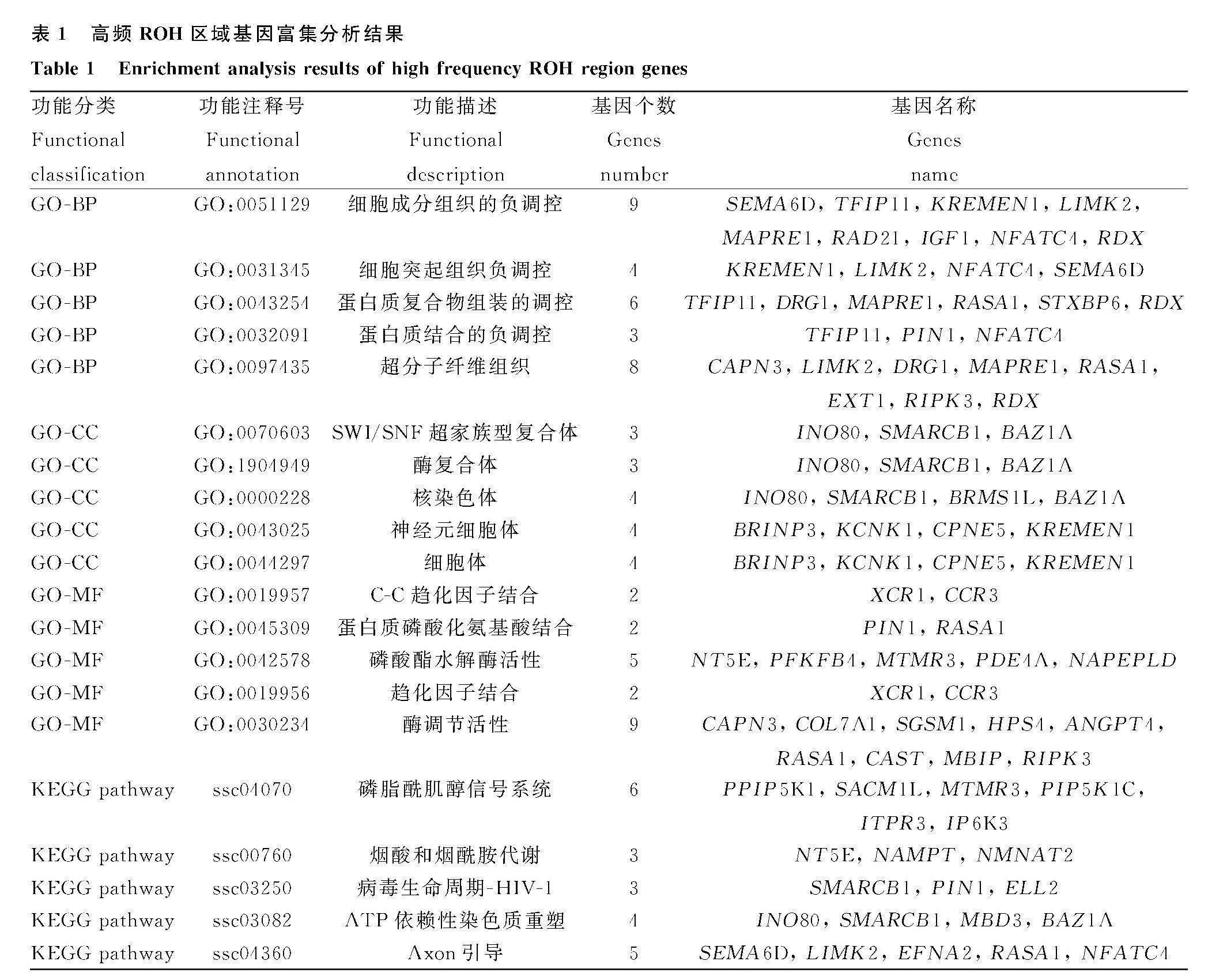
本研究選取ROH頻率大于1%作為高頻ROH區域的閾值,在蘇山豬和巴克夏豬群體中分別檢測到4個和40個高頻ROH區域,分別對應241個和3 186個SNPs,通過對高頻 ROH 區域進行基因注釋,分別注釋到8個和103個基因(圖3D)。富集分析發現,這些基因主要參與細胞成分
A.主成分分析PCA圖;B.蘇山豬和巴克夏豬聚類分析圖;C.蘇山豬家系圖;D.巴克夏豬家系圖
A. The principal component analysis (PCA) plot; B. The clustering analysis diagram of Sushan pigs and Berkshire pigs; C. The pedigree diagram of Sushan pigs; D. The pedigree diagram of Berkshire pigs
組織的負調控和超分子纖維組織等生物過程,核仁和染色質等細胞組分,酶調節活性和磷酸酯水解酶活性等分子功能(圖3E)。這些基因主要參與PI3K-Akt 信號通路、磷脂酰肌醇信號通路和催產素信號通路(圖3F)。部分顯著富集的基因信息如表1所示。
2.4" 選擇信號分析
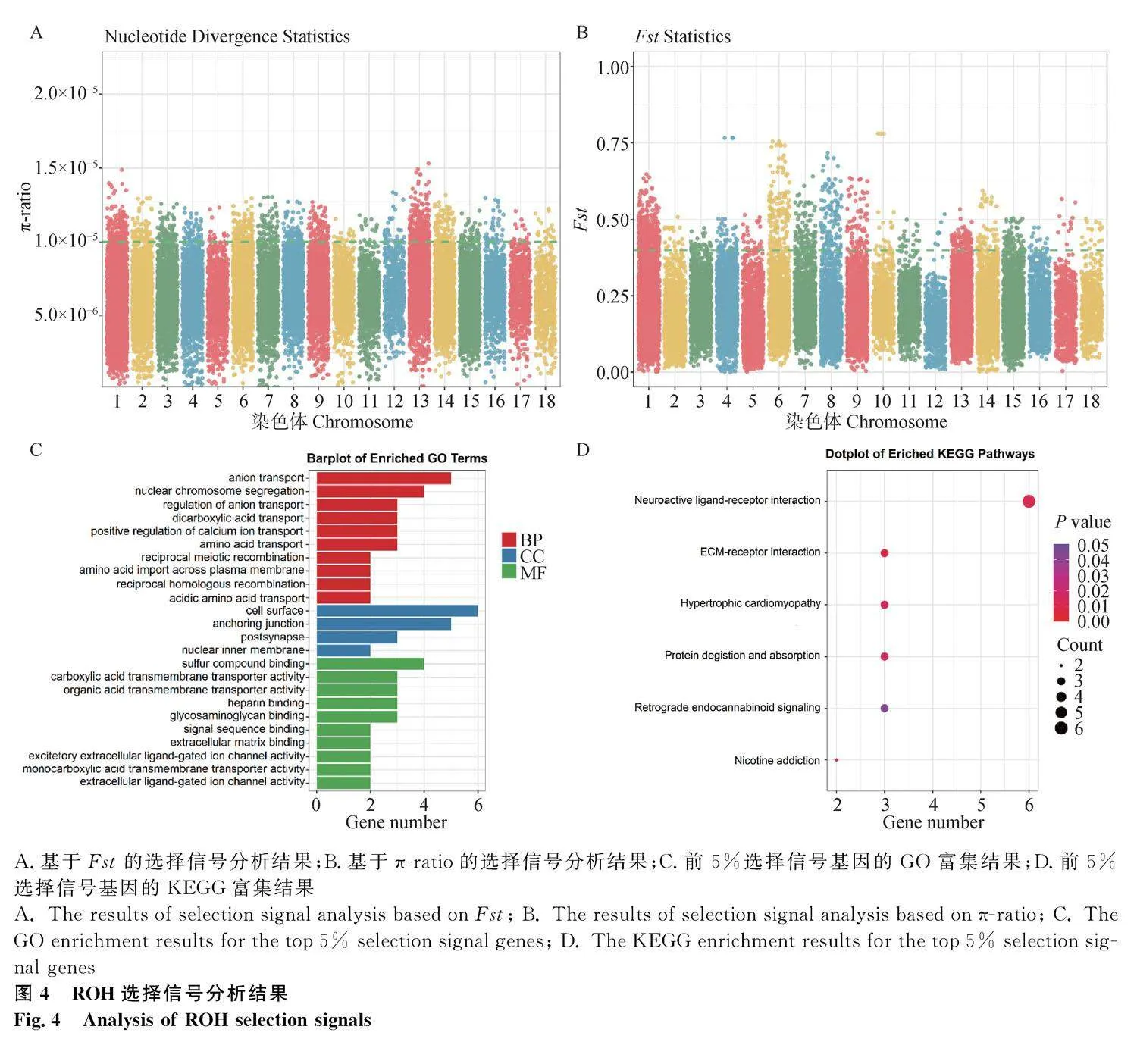
本研究使用Fst與π-ratio(πA/πB)2 種方法進行ROH選擇信號檢測。計算蘇山豬與巴克夏豬Fst和 π-ratio 值以篩選2個豬品種正選擇區域(圖4A和4B),即Fst和π-ratio都在前5%的區域為共享差異選擇信號。取交集統計分析發現,總共篩選到3 832個選擇信號區域,選擇信號區域在13號染色體上分布最多,達到660個,11號染色體上分布最少,為62個。富集分析發現,這些基因主要參與陰離子轉運和核染色體分離等生物過程,細胞表面、錨定連接和突觸后膜等細胞組分,硫化合物結合、羧酸跨膜轉運蛋白活性和有機酸跨膜轉運蛋白活性等分子功能(圖4C)。這些基因主要富集的信號通路包括神經活性配體-受體相互作用信號通路、胞外基質-受體相互作用信號通路、肥厚型心肌病、蛋白質消化和吸收信號通路、逆行內源性大麻素信號傳導通路等(圖4D)。
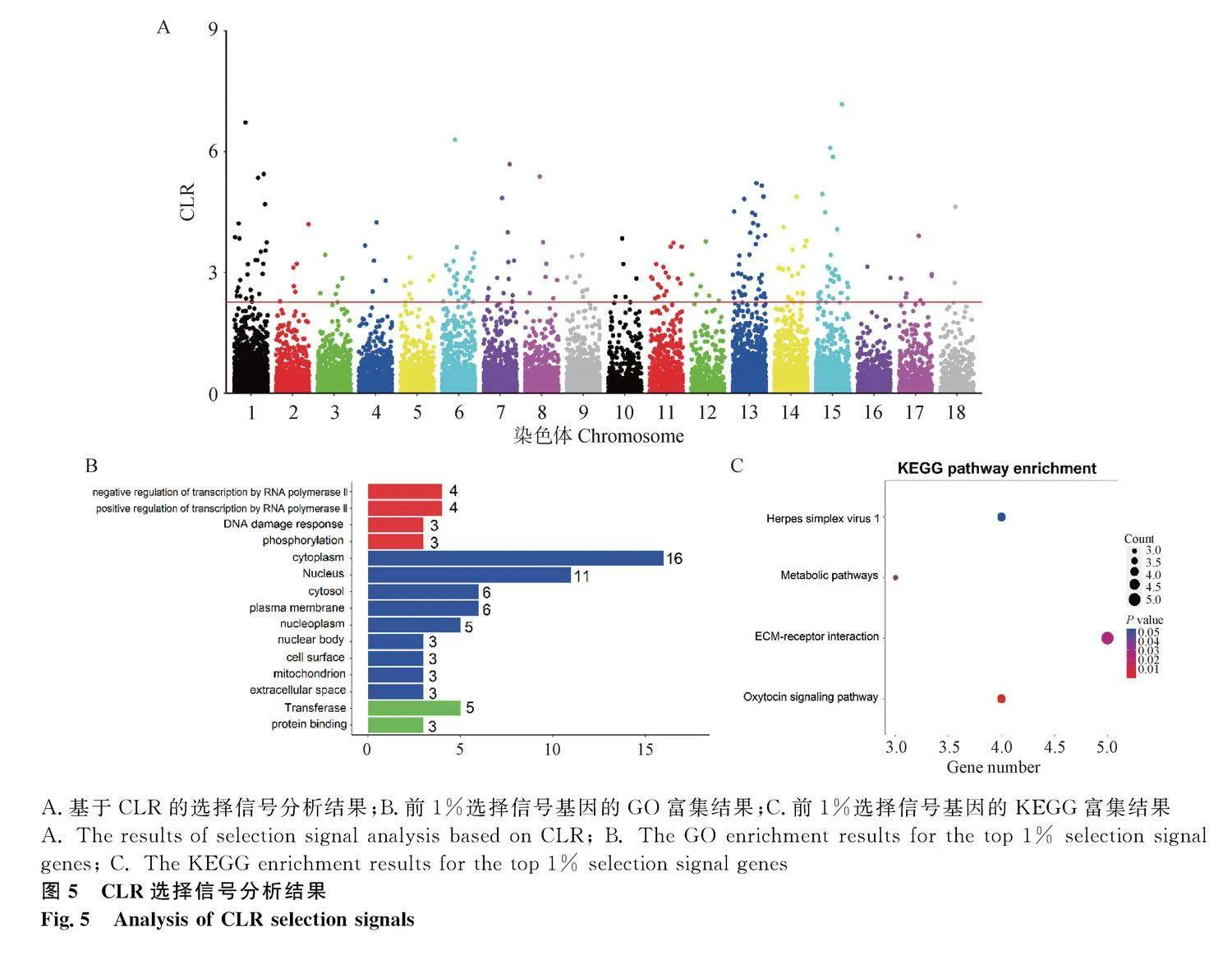
CLR選擇信號分析發現,總共篩選到240個選擇信號區域,選擇信號區域在13號染色體上分布最多,有38個,18號染色體上分布最少,只有2個(圖5A)。富集分析發現,這些基因主要參與RNA聚合酶II的轉錄調控等生物過程,細胞質和細胞核等細胞組分,轉移酶和蛋白結合等分子功能(圖5B)。這些基因主要富集的信號通路包括催產素信號通路、細胞外基質-受體相互作用、代謝途徑和單純皰疹病毒1型感染信號通路(圖5C)。
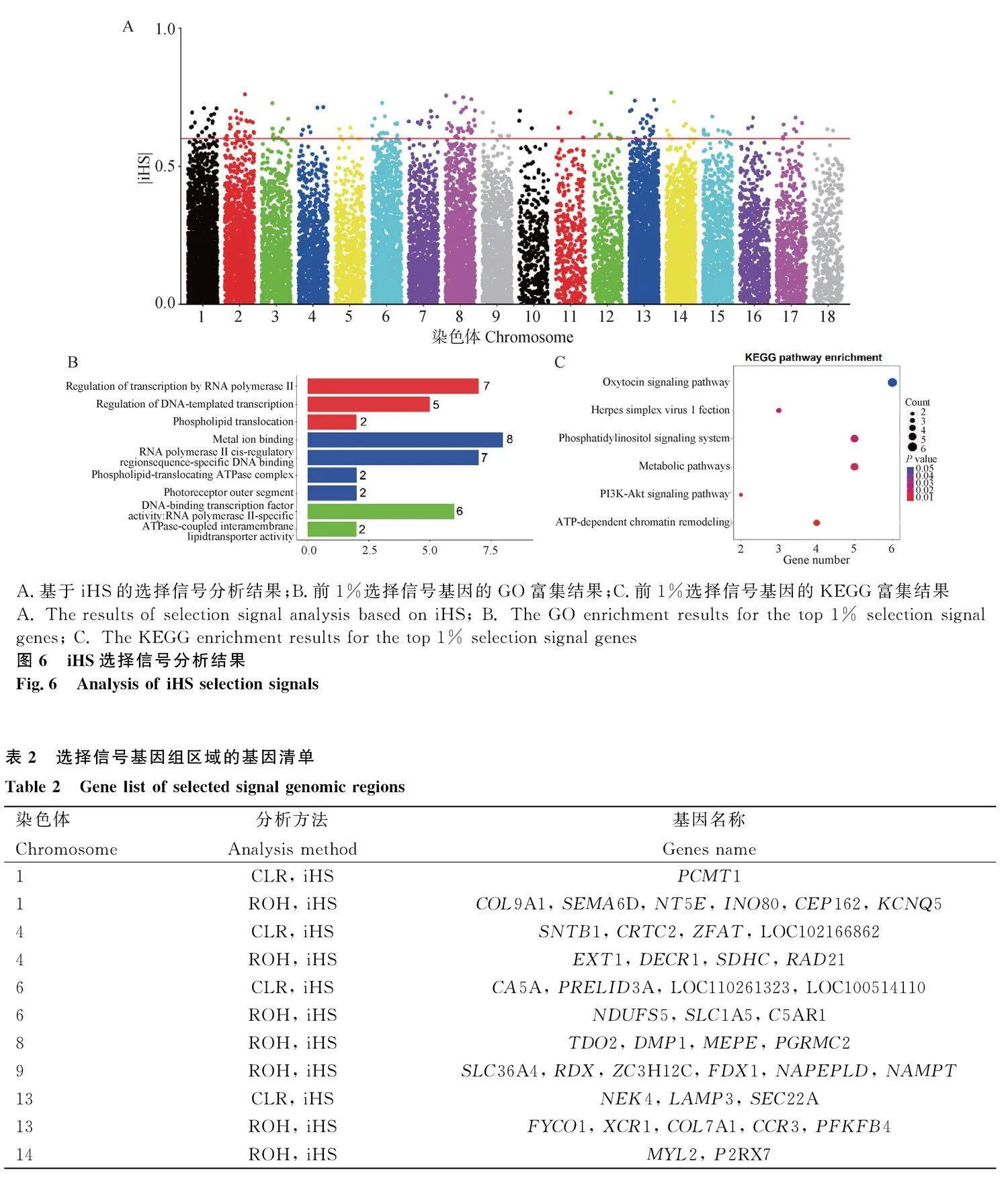
iHS選擇信號分析發現,總共篩選到196個強選擇位點,強選擇位點在8號染色體上分布最多,有31個,18號染色體上分布最少,只有2個(圖6A)。富集分析發現,這些基因主要參與RNA聚合酶II的轉錄調控和DNA轉錄調控等生物過程,金屬離子結合和RNA聚合酶II順式調控區特異性DNA結合等細胞組分,DNA結合轉錄因子活性和ATP酶偶聯的膜內脂質轉運活性等分子功能(圖6B)。這些基因主要富集的信號通路包括催產素信號通路、PI3K-Akt信號通路、ATP依賴的染色質重塑、代謝途徑、磷脂酰肌醇信號系統和單純皰疹病毒1型感染信號通路(圖6C)。
另外,本研究對3種選擇信號結果進行合并分析,取兩種方法的交集發現,總共有42個基因在兩種方法中均為受選擇區域的位點(表2)。
3" 討" 論
本研究利用“中芯一號”SNP芯片開展了43個蘇山豬樣本和21個巴克夏豬樣本的全基因組SNPs分析,篩選到蘇山豬有效 SNPs位點42 282個,巴克夏豬有效SNPs位點27 718個。“中芯一號”以江西農業大學黃路生院士團隊研究成果為基礎,以杜長大、F2資源家系、兩頭烏、蘇太豬、嵌合家系、萊蕪豬、二花臉豬合并巴馬香豬等多個群體作為參考群,目前已有涵蓋杜、長、大主要商業品種及中國6大類地方品種高覆蓋度的基因組全序列單倍型庫[15]。在本研究中,本團隊前期培育的蘇山豬含太湖豬、長白豬和大白豬血統,因此SNPs在染色體上的密度分布比較全,幾乎全覆蓋。相比而言,巴克夏豬SNPs在染色體上的密度分布有些區域沒有覆蓋到,有效SNPs位點少于蘇山豬,提示“中芯一號”確實更適用于中國地方品種豬基因組育種研究和應用。
ROH是一種普遍的遺傳現象,在不同種群基因組上廣泛存在[16-18],可以指示親緣的遠近和近交的歷史,ROH片段越長,家系內存在近世代近交的可能性越高[19]。近交系數FROH用來衡量個體的近交程度,FROH值越大,表示個體的近交程度越高[20]。本研究中,蘇山豬和巴克夏豬兩個豬品種ROH長度在0~6 Mb之間的個體數目最多,百分比均超過70%,加之近交系數比較小,提示家系內親緣關系比較遠,近交的可能性比較低。另外,在蘇山豬和巴克夏豬群體中分別檢測到4個和40個高頻ROH區域,分別對應241個和3 186個SNPs,通過對高頻 ROH區域進行基因注釋,分別注釋到8個和103個基因。對KEGG信號通路中顯著的部分基因進行檢索發現,RAD21、INO80和SMARCB1主要與DNA 復制有關[21,22];XCR1和CCR3主要參與免疫炎癥反應[23];COL21A1和CAPN3主要參與肌肉合成與降解[24,25];DECR1和IP6K3主要參與脂質代謝和糖代謝[26,27];DRG1和 IGF1主要參與細胞生長和發育以及細胞周期調控[28,29]。
選擇信號通常指的是基因組中那些表現出正選擇或負選擇特征的區域,這些信號表明某些基因或基因區域受到了自然選擇的作用,導致它們在進化過程中的變異頻率與中性進化預期的頻率不同,研究這些選擇信號可以直接發現功能基因,是篩選功能基因的重要策略之一[30,31]。本研究中,使用3種方法(ROH、CLR和iHS)對蘇山豬和巴克夏豬進行選擇信號分析,總共篩選到2個正選擇信號區域的基因。對強選擇位點的部分基因進行檢索發現,MYL2和SNTB1與肌肉發育有關[32,33];MEPE、DMP1和 COL9A1與骨骼發育有關[34,35];NDUFS5和PGRMC2與能量代謝有關[36,37];SLC1A5和SLC36A4與信號傳遞和營養吸收有關[38,39];C5AR1和P2RX7與免疫應答和炎癥反應有關[40,41]。CA5A和Nek4參與調控線粒體的生理和形態[42,43]。LAMP3基因參與調控細胞自噬并影響細胞生理過程[44]。PCMT1被報道與細胞遷移、侵襲和凋亡有關[45]。
4" 結" 論
本研究初步揭示了蘇山豬和巴克夏豬的基因組SNP圖譜,并通過高頻ROH分析和選擇信號檢測鑒定到可能影響豬生長發育、肉質、營養和一般抗病力的候選基因。接下來將通過試驗探究這些基因的多態性與性狀的關聯程度,或者擴大群體數量進行進一步的全基因組關聯分析,最終鑒定有效遺傳標記并運用到育種實踐中。
參考文獻(References):
[1]" STONEKING M.Single nucleotide polymorphisms.From the evolutionary past[J].Nature,2001,409(6822):821-822.
[2]" 張瑞鋒,黃" 珍,謝水華,等.豬全基因組選擇技術發展現狀和應用前景[J].中國畜牧雜志,2023,59(10):21-29.
ZHANG R F,HUANG Z,XIE S H,et al.The development status and application prospect of genomic selection for pigs[J].Chinese Journal of Animal Science,2023,59(10):21-29.(in Chinese)
[3]" 邱" 奧,王" 雪,孟慶利,等.3款豬50K SNP芯片基因型填充效果研究[J].中國畜牧雜志,2021,57(S1):33-38.
QIU A,WANG X,MENG Q L,et al.Study on genotype imputation performance of three porcine50K SNP chips[J].Chinese Journal of Animal Science,2021,57(S1):33-38.(in Chinese)
[4]" 龍" 熙,吳平先,潘紅梅,等.基于SNP芯片的內江豬群體遺傳結構分析[J].中國畜牧雜志,2024,doi:10.19556/ j.0258-7033.20230914-04.
LONG X,WU P X,PAN H M,et al.Genetic structure analysis of Neijiang Pig population based on SNP chip[J].Chinese Journal of Animal Science,2024,doi:10.19556/j.0258-7033.20230914-04.(in Chinese)
[5]" 陶" 璇,楊雪梅,梁" 艷,等.基于SNP芯片的丫杈豬保種群體遺傳結構研究[J].畜牧獸醫學報,2023,54(6):2308-2319.
TAO X,YANG X M,LIANG Y,et al.Analysis of genetic structure of conservation population in Yacha Pig based on SNP chip[J].Acta Veterinaria et Zootechnica Sinica,2023,54(6):2308-2319.(in Chinese)
[6]" 宋科林,閆尊強,王鵬飛,等.基于SNP芯片分析徽縣青泥黑豬遺傳多樣性和遺傳結構[J].畜牧獸醫學報,2024,55(3):995-1006.
SONG K L,YAN Z Q,WANG P F,et al.Analysis on genetic diversity and genetic structure based on SNP chips of Huixian Qingni Black pig[J].Acta Veterinaria et Zootechnica Sinica,2024,55(3):995-1006.(in Chinese)
[7]" 何曉錦,郭建華,劉洪江,等.里岔黑豬基因組選擇信號檢測與分析[J].中國畜牧雜志,2024,60(4):131-135.
HE X J,GUO J H,LIU H J,et al.Detection and analysis of genomic selection signals in Licha Black Pigs[J].Chinese Journal of Animal Science,2024,60(4):131-135.(in Chinese)
[8]" 任守文,李碧俠,葛云山,等.蘇山豬選育研究[J].中國畜牧雜志,2020,56(11):47-51.
REN S W,LI B X,GE Y S,et al.Study on breeding of Sushan Pig[J].Chinese Journal of Animal Science,2020,56(11):47-51.(in Chinese)
[9]" ZHAO F P,XIE R,FANG L Z,et al.Analysis of 206 whole-genome resequencing reveals selection signatures associated with breed-specific traits in Hu Sheep[J].Evol Appl,2024,17(6):e13697.
[10]" TAMURA K,STECHER G,KUMAR S.MEGA11:molecular evolutionary genetics analysis version 11[J].Mol Biol Evol,2021,38(7):3022-3027.
[11]" DANECEK P,AUTON A,ABECASIS G,et al.The variant call format and VCFtools[J].Bioinformatics,2011,27(15):2156-2158.
[12]" WANG K,LI M Y,HAKONARSON H.ANNOVAR:functional annotation of genetic variants from high-throughput sequencing data[J].Nucleic Acids Res,2010,38(16):e164.
[13]" DEGIORGIO M,HUBER C D,HUBISZ M J,et al.SweepFinder2:increased sensitivity,robustness and flexibility[J]. Bioinformatics, 2016,32(12):1895-1897.
[14]" GAUTIER M,VITALIS R.rehh:an R package to detect footprints of selection in genome-wide SNP data from haplotype structure[J]. Bioinformatics,2012,28(8):1176-1177.
[15]" 曾浩南,鐘展明,徐志婷,等.3款豬50K SNP芯片基因型填充至序列數據的效果評估[J].華南農業大學學報,2022,43(4):10-15.
ZENG H N,ZHONG Z M,XU Z T,et al.Evaluation on genotype imputation performance of three porcine50K SNP chips from chip data to sequencing data[J].Journal of South China Agricultural University,2022,43(4):10-15.(in Chinese)
[16] "GORSSEN W,MEYERMANS R,JANSSENS S,et al.A publicly available repository of ROH islands reveals signatures of selection in different livestock and pet species[J].Genet Sel Evol,2021,53(1):2.
[17]" SHI L Y,WANG L G,LIU J X,et al.Estimation of inbreeding and identification of regions under heavy selection based on runs of homozygosity in a Large White Pig population[J].J Anim Sci Biotechnol,2020,11:46.
[18]" LIU J X,SHI L Y,LI Y,et al.Estimates of genomic inbreeding and identification of candidate regions that differ between Chinese indigenous sheep breeds[J].J Anim Sci Biotechnol,2021,12(1):95.
[19]" DI GREGORIO P,PERNA A,DI TRANA A,et al.Identification of ROH islands conserved through generations in pigs belonging to the Nero Lucano breed[J].Genes (Basel),2023,14(7):1503.
[20]" 韓云珍,陽文攀,洪" 淵,等.基于芯片數據估計不同方法對槐豬近交系數的影響[J].畜牧獸醫學報,2023,54(3):947-955.
HAN Y Z,YANG W P,HONG Y,et al.Estimating the inbreeding coefficient of Huai Pigs by different methods based on chip data[J].Acta Veterinaria et Zootechnica Sinica,2023,54(3):947-955.(in Chinese)
[21]" PORTAL D,ZHOU H F,ZHAO B,et al.Epstein-Barr virus nuclear antigen leader protein localizes to promoters and enhancers with cell transcription factors and EBNA2[J].Proc Natl Acad Sci U S A,2013,110(46):18537-18542.
[22]" DERMAWAN J K,SINGER S,TAP W D,et al.The genetic landscape of SMARCB1 alterations in SMARCB1-deficient spectrum of mesenchymal neoplasms[J].Mod Pathol,2022,35(12):1900-1909.
[23]" PAWLIK K,MIKA J.Targeting members of the chemokine family as a novel approach to treating neuropathic pain[J].Molecules, 2023,28(15):5766.
[24]" QIN L H,ZHU X J,ZHANG L Y,et al.Identification of hub genes and pathways in the development of gastric cancer by gene co-expression network analysis[J].J Biol Regul Homeost Agents,2021,35(1):35-44.
[25]" MA H S,GONG X L,LI W X,et al.Missense mutation of c.635 Tgt;C in CAPN3 impairs muscle injury repair in a limb-girdel muscular dystropy model[J].Clin Genet,2023,103(6):663-671.
[26]" ZHOU H J,ZHANG J,YAN Z K,et al.DECR1 directly activates HSL to promote lipolysis in cervical cancer cells[J].Biochim Biophys Acta Mol Cell Biol Lipids,2022,1867(3):159090.
[27]" LI H Y,DATUNASHVILI M,REYES R C,et al.Inositol hexakisphosphate kinases differentially regulate trafficking of vesicular glutamate transporters 1 and 2[J].Front Cell Neurosci,2022,16:926794.
[28]" XIE Z C,ZHANG L C,ZHANG Q,et al.A Glu209Lys substitution in DRG1/TaACT7,which disturbs F-actin organization,reduces plant height and grain length in bread wheat[J].New Phytol,2023,240(5):1913-1929.
[29]" GUI R R,LI W Q,LI Z P,et al.Effects and potential mechanisms of IGF1/IGF1R in the liver fibrosis:a review[J].Int J Biol Macromol,2023,251:126263.
[30]" 薛周艤源,宋顯威,吳林慧,等.畜禽選擇信號檢測方法及其統計學問題[J].畜牧獸醫學報,2018,49(6):1099-1107.
XUE Z Y Y,SONG X W,WU L H,et al.The identification methods of selection signatures in livestock and its statistical problems[J].Acta Veterinaria et Zootechnica Sinica,2018,49(6):1099-1107.(in Chinese)
[31]" TONG X K,CHEN D,HU J C,et al.Accurate haplotype construction and detection of selection signatures enabled by high quality pig genome sequences[J].Nat Commun,2023,14(1):5126.
[32]" JI K X,JIAO D,YANG G,et al.Transcriptome analysis revealed potential genes involved in thermogenesis in muscle tissue in cold-exposed lambs[J].Front Genet,2022,13:1017458.
[33]" SHI A D,HE C Q,OTTEN K,et al.Reduced myotube diameter induced by combined inhibition of transforming growth factor-β type I receptors Acvr1b and Tgfbr1 is associated with enhanced β1-syntrophin expression[J].J Cell Physiol,2024,doi: 10.1002/jcp.31418.
[34]" DONMEZ B O,KARAGUR E R,DONMEZ A C,et al.Calcium-dependent activation of PHEX,MEPE and DMP1 in osteocytes[J].Mol Med Rep,2022,26(6):359.
[35]" GOLSHAN-TAFTI M,DASTGHEIB S A,ALIJANPOUR K,et al.A thorough analysis of data on the correlation between COL9A1 polymorphisms and the susceptibility to congenital talipes equinovarus:a meta-analysis[J].J Orthop Surg Res,2024,19(1): 345.
[36]" SALSCHEIDER S L,GERLICH S,CABRERA-OREFICE A,et al.AIFM1 is a component of the mitochondrial disulfide relay that drives complex I assembly through efficient import of NDUFS5[J].EMBO J,2022,41(17) :e110784.
[37]" GALMOZZI A,KOK B P,KIM A S,et al.PGRMC2 is an intracellular Haem chaperone critical for adipocyte function[J].Nature, 2019,576(7785):138-142.
[38]" LIU N,DAI Z L,ZHANG Y C,et al.Maternal L-proline supplementation enhances fetal survival,placental development,and nutrient transport in mice[J].Biol Reprod,2019,100(4):1073-1081.
[39]" SHARMA D,YU Y L,SHEN L Y,et al.SLC1A5 provides glutamine and asparagine necessary for bone development in mice[J].Elife,2021,10:e71595.
[40]" HREICH S J D,JUHEL T,LEROY S,et al.Activation of the P2RX7/IL-18 pathway in immune cells attenuates lung fibrosis[J].Elife,2024,12:RP88138.
[41]" ZHANG C,CAO K K,YANG M R,et al.C5aR1 blockade reshapes immunosuppressive tumor microenvironment and synergizes with immune checkpoint blockade therapy in high-grade serous ovarian cancer[J].Oncoimmunology,2023,12(1):2261242.
[42]" ASPATWAR A,SUPURAN C T,WAHEED A,et al.Mitochondrial carbonic anhydrase VA and VB:properties and roles in health and disease[J].J Physiol,2023,601(2):257-274.
[43]" BASEI F L,DE CASTRO FEREZIN C,DE OLIVEIRA A L R,et al.Nek4 regulates mitochondrial respiration and morphology[J].FEBS J,2022,289(11):3262-3279.
[44]" TANAKA T,WARNER B M,MICHAEL D G,et al.LAMP3 inhibits autophagy and contributes to cell death by lysosomal membrane permeabilization[J].Autophagy,2022,18(7):1629-1647.
[45]" ZHONG J C,YUAN C,LIU L,et al.PCMT1 regulates the migration,invasion,and apoptosis of prostate cancer through modulating the PI3K/AKT/GSK-3β pathway[J].Aging (Albany NY),2023,15(20):11654-11671.
(編輯" 郭云雁)

