中國假百合屬親緣關系及假百合遺傳多樣性的ISSR分析
楊 梅,周頌東,何興金,彭 昶
(四川大學 生命科學學院 生物資源與生態環境教育部重點實驗室,成都 610064)
?
中國假百合屬親緣關系及假百合遺傳多樣性的ISSR分析
楊梅,周頌東*,何興金,彭昶
(四川大學 生命科學學院 生物資源與生態環境教育部重點實驗室,成都 610064)
摘要:利用7條ISSR引物對中國假百合屬植物24個居群255個個體的遺傳多樣性進行了初步探討。結果表明:(1)UPGMA聚類結果顯示,假百合(Notholirion bulbuliferum)、鐘花假百合(N.campanulatum)與大葉假百合(N.macrophyllum)分別聚為三支,在分子水平上出現了明顯的分化,揭示三者是獨立物種。(2)N.bulbuliferum×N.campanulatum與鐘花假百合聚為一支,這可能與其母系遺傳和極強的無性繁殖體系有關,但兩者間基因流(Nm=0.216 0)很低,假百合與N.bulbuliferum×N.campanulatum的基因流(Nm=0.144 9)也極低,說明N.bulbuliferum×N.campanulatum正在分化。(3)假百合種下各居群間按照地理結構可明顯分為4支,經Mantel檢測表明存在顯著的譜系地理結構(r=0.410,P=0.01)。(4)AMOVA分析顯示,假百合居群間遺傳變異為77.12%(P<0.01),而居群內為22.88%(P<0.01),同樣表明居群間遺傳分化大于居群內。研究結果揭示了橫斷山區假百合屬植物的親緣關系,從分子水平上為其鑒定提供了依據;并從遺傳結構上為藥用植物假百合的可持續利用和開發奠定了理論基礎。
關鍵詞:遺傳多樣性;ISSR;假百合;鐘花假百合;大葉假百合
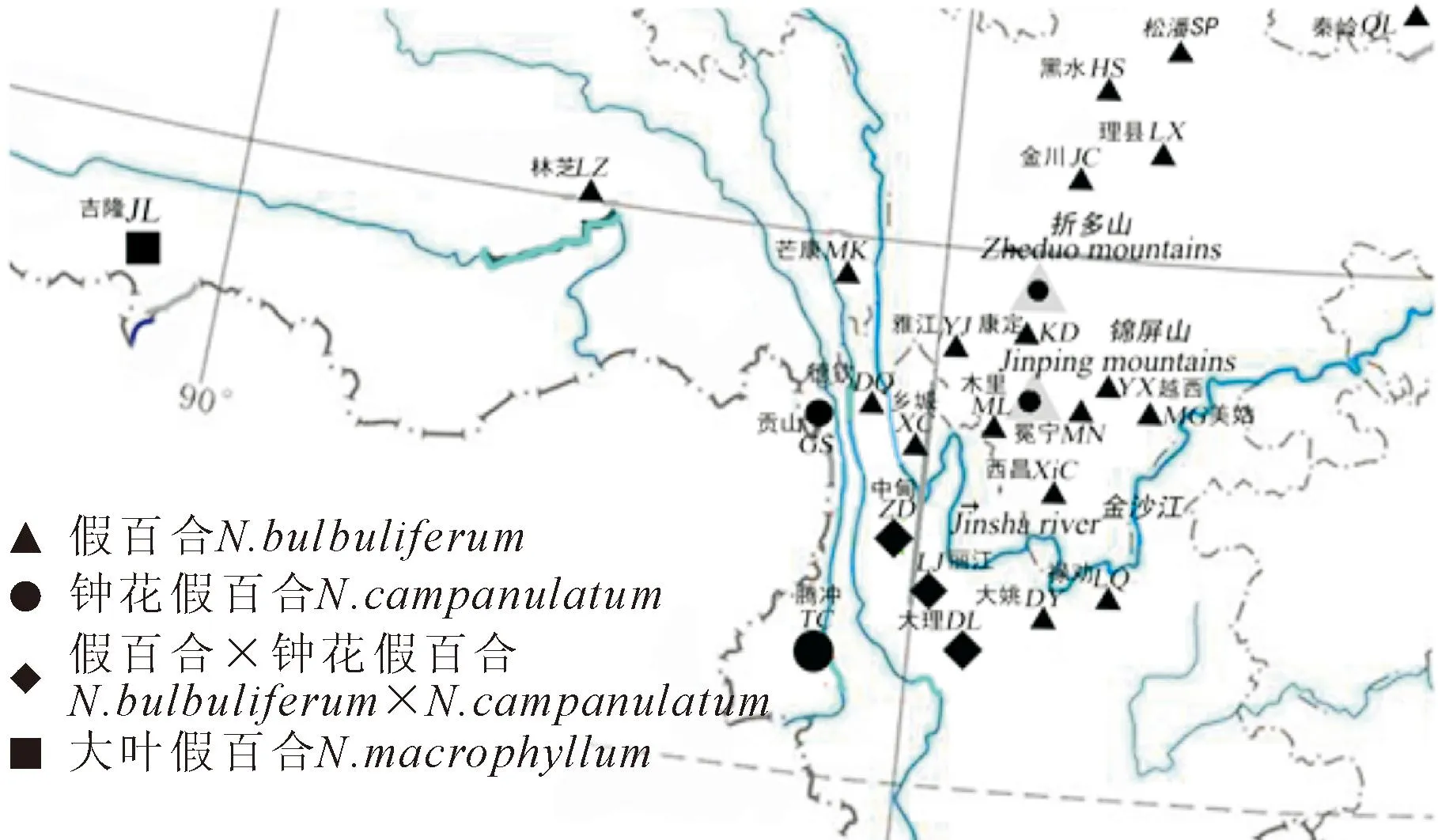
假百合屬是百合科百合族較為原始的類群[1-2],屬下共有5種,其中大葉假百合(Notholirionmacrophyllum)、鐘花假百合(N.campanulatum)和假百合(N.bulbuliferum)等3種分布于中國西部橫斷山區及東喜馬拉雅[3]。因其鱗莖由基生葉增厚套迭而成,外面具黑褐色的膜質鱗莖皮,與百合屬的特征相似而被作為百合屬的一個亞屬;而后又有學者將其歸為貝母屬的一個亞屬[4]。假百合屬植物具卵形的小鱗莖,成熟后外殼稍硬,內有數片白色肉質的鱗片;柱頭明顯3裂,這些特征明顯區別于百合族的其它屬,Boissier將其提升為獨立的屬并得到大多數學者的支持,同時發表了大葉假百合[5-7]。Conton與Stearn又陸續發現了鐘花假百合和假百合[6-7]。而有研究顯示,假百合與鐘花假百合之間存在雜交,即假百合×鐘花假百合(N.bulbuliferum×N.campanulatum)。據文獻記載以及野外觀察發現這四者在未開花時很難辨認(圖1),假百合為常用中藥材,對其鑒定的準確與否直接關系到藥材質量,所以從分子水平上對其屬下種間關系探討迫在眉睫。假百合屬植物生長在2 700~4 000 m高海拔地帶,且大多生長在人跡罕至的深山中,極少受到關注,更未從分子水平上對這四者進行過親緣關系及遺傳多樣性的研究。
ISSR被稱作簡單重復區間多態性擴增,或微衛星PCR,方法是用17~22個重復堿基序列作為引物擴增出重復序列間的片段[8],因其操作步驟簡單易行[9-10],應用范圍十分廣泛。在百合族中運用ISSR技術探討了青島百合[11]的遺傳多樣性,提出了麝香百合的分子鑒定依據[12];趙麗華等[13]采用ISSR技術對中國百合屬親緣關系進行了研究;沈呈娟等[14]對近緣類群寶興百合與匍莖百合進行了親緣關系與遺傳多樣性的研究。本實驗通過ISSR分子標記對中國假百合屬植物的親緣關系進行了研究,為藥用植物假百合的分子鑒定提供了參考,并對假百合進行了居群水平上的遺傳多樣性研究,為假百合可持續利用和保護提供了理論依據。
1材料和方法
1.1材料
實驗包括24個居群,共計255個個體,其中假百合、鐘花假百合、假百合×鐘花假百合、大葉假百合的居群數分別為18、2、3、1個。按居群采樣時,每個個體至少間隔50 m以上,將采集的新鮮葉片置入硅膠干燥備用。并將野外采集的個體引種栽培于實驗室,憑證標本存放于四川大學標本館(SZ)。采樣基本覆蓋中國假百合屬的分布范圍(表1,圖2)。
1.2ISSR標記分析
對實驗材料新鮮嫩葉采用植物基因組DNA試劑盒(天根生化科技有限公司,北京)提取總DNA。DNA樣品用1%瓊脂糖凝膠電泳檢測,利用紫外分光光度計確定其濃度,將樣品稀釋至25 ng/μL,最后將樣品置于-20 ℃冰箱中保存備用。隨機從每個居群中抽取2個樣本作為引物篩選的模板,根據哥倫比亞大學(UBC)公布的引物序列,從中篩選出穩定性好,重復性強且條帶清晰的7條引物作為本次實驗的引物(Invitrogne公司合成),引物編號及序列見表2。
從每個居群選取3個個體進行預實驗,最終確定PCR擴增反應體系總體積為25 μL:包含25 ng模板DNA,1.0 UTaqDNA聚合酶,1×PCR緩沖液,1 μmol/L ISSR引物,0.5 mmol/L dNTPs,1.5 mmol/L MgCL2。PCR擴增程序為94 ℃預變性4 min;94 ℃變性45 s,51.5 ℃~55.5 ℃(視引物Tm
居群編號同表1
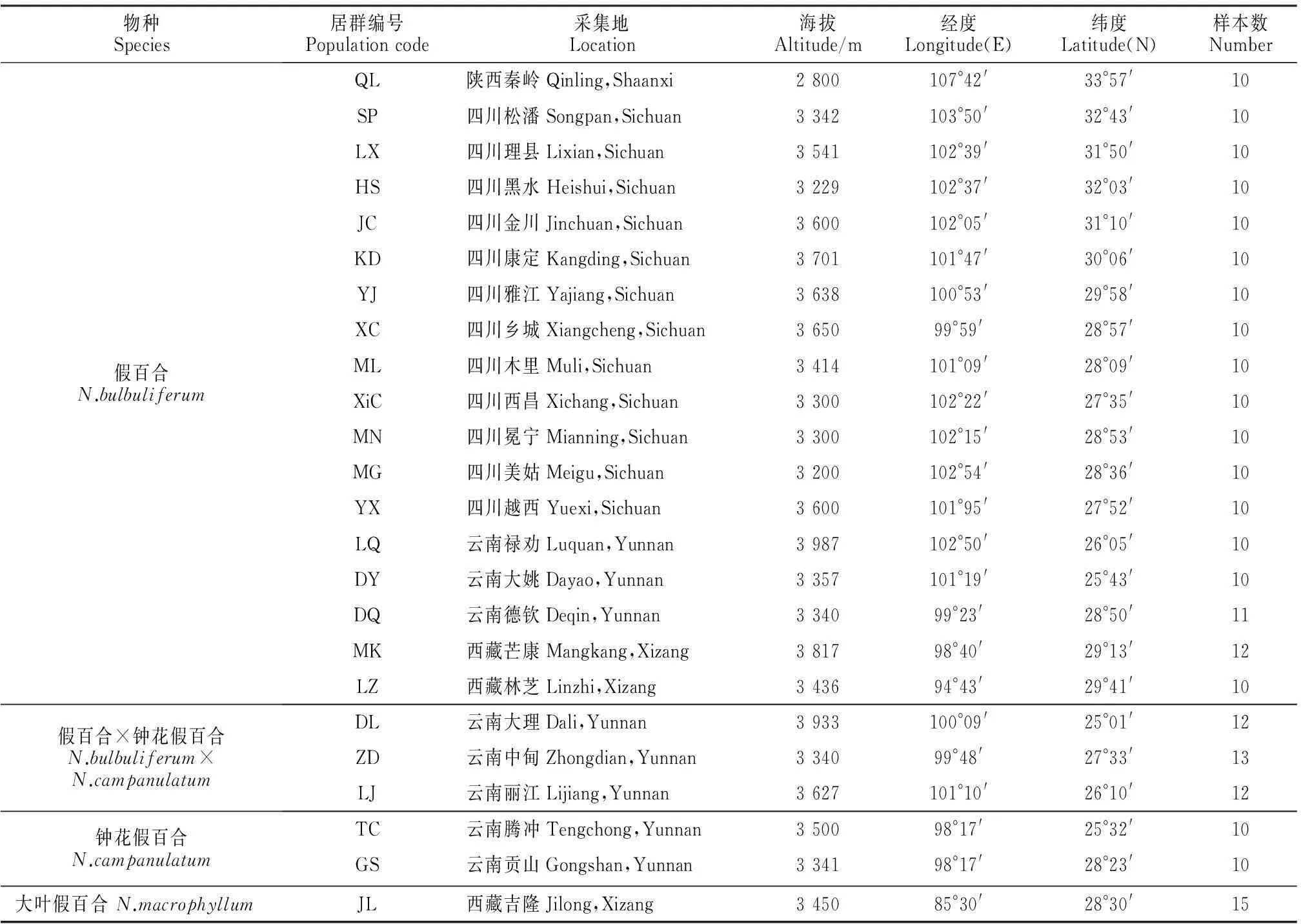
物種Species居群編號Populationcode采集地Location海拔Altitude/m經度Longitude(E)緯度Latitude(N)樣本數Number假百合N.bulbuliferumQL陜西秦嶺Qinling,Shaanxi2800107°42'33°57'10SP四川松潘Songpan,Sichuan3342103°50'32°43'10LX四川理縣Lixian,Sichuan3541102°39'31°50'10HS四川黑水Heishui,Sichuan3229102°37'32°03'10JC四川金川Jinchuan,Sichuan3600102°05'31°10'10KD四川康定Kangding,Sichuan3701101°47'30°06'10YJ四川雅江Yajiang,Sichuan3638100°53'29°58'10XC四川鄉城Xiangcheng,Sichuan365099°59'28°57'10ML四川木里Muli,Sichuan3414101°09'28°09'10XiC四川西昌Xichang,Sichuan3300102°22'27°35'10MN四川冕寧Mianning,Sichuan3300102°15'28°53'10MG四川美姑Meigu,Sichuan3200102°54'28°36'10YX四川越西Yuexi,Sichuan3600101°95'27°52'10LQ云南祿勸Luquan,Yunnan3987102°50'26°05'10DY云南大姚Dayao,Yunnan3357101°19'25°43'10DQ云南德欽Deqin,Yunnan334099°23'28°50'11MK西藏芒康Mangkang,Xizang381798°40'29°13'12LZ西藏林芝Linzhi,Xizang343694°43'29°41'10假百合×鐘花假百合N.bulbuliferum×N.campanulatumDL云南大理Dali,Yunnan3933100°09'25°01'12ZD云南中甸Zhongdian,Yunnan334099°48'27°33'13LJ云南麗江Lijiang,Yunnan3627101°10'26°10'12鐘花假百合N.campanulatumTC云南騰沖Tengchong,Yunnan350098°17'25°32'10GS云南貢山Gongshan,Yunnan334198°17'28°23'10大葉假百合N.macrophyllumJL西藏吉隆Jilong,Xizang345085°30'28°30'15
值而定)退火45 s,72 ℃延伸1 min,共35個循環;72 ℃延伸8 min。以DL2000作為分子量標準檢測擴增產物,用含有Gold view的1.5%瓊脂糖凝膠于120 V恒壓電泳45 min。最后在凝膠成像系統儀上進行拍照并保存(Bio-Rad Gel Doc XR+imaging system),用于后續分析。
1.3數據處理與分析
ISSR作為顯性分子標記視每一個多態位點為一個等位基因。以DL2000進行參照對比,在同一相對遷移位置出現清晰條帶的計為1,沒有或模糊的條帶記為0,將條帶數據信息構建成0和1的原始數據矩陣。使用POPGENE 1.32軟件分析遺傳變異的各項參數:如多態位點百分率(PPB)、Nei’s基因多樣度指數(H)、Nei’s遺傳距離(D)和遺傳一致度(Hi)、平均每個位點上的觀察等位基因數(Na)、平均每個位點的有效等位基因(Ne)、Shan-non多樣性信息指數(I)、居群間遺傳分化系數(Gst)、居群內基因多樣度(Hs)、總的基因多樣度(Ht)、基因流(Nm)等[15-16]。然后利用NTSYS-pc 2.10構建樹狀聚類圖以及計算遺傳相似性系數(Gs)[17],對假百合屬下種間關系進行分析。遺傳變異在居群內與居群間的分布情況通過AMOVA 1.55軟件計算得出[18]。最后使用GenAlEX 6.5對遺傳距離與地理距離之間相關性進行Mantel檢驗[19]。

表2 ISSR引物序列和最佳退火溫度
注:Y=C/T;R=A/G。
Note:Y=C/T;R=A/G.
2結果與分析
2.1ISSR擴增產物的初步檢測
圖3為引物UBC815對假百合屬植物進行擴增后,用1.5%瓊脂糖凝膠電泳檢測的結果。其它引物都達到很好的擴增效果,表明選定的反應體系和PCR擴增程序效果較好,擴增產物可用于下一步的數據分析。
2.2假百合屬ISSR結果分析
從20條ISSR引物中篩選出了能擴增出清晰、穩定性和重復性較好的7條引物,對假百合屬全部供試材料進行PCR分析,共計擴增出91個清晰可重復的多態性有效位點,其中多態性標記位點91個(PPB=100%)。7條引物擴增后的DNA條帶數目從10到16,平均條帶數目為13,變異長度從200 bp到2 000 bp。POPGENE1.32分析顯示(表3):在這7條引物中平均每個位點的有效等位基因(Ne)從 1.044 0到1.248 2,平均值為1.146 3。平均每個位點上的觀察等位基因數(Na)從1.155 8到1.441 6,平均值為1.259 0。Nei’s基因多樣度指數(H)從0.051 8到0.262 0,平均值為0.146 8。以及Shannon多樣性信息指數(I)從0.082 3到0.317 7,平均值為0.164 0。
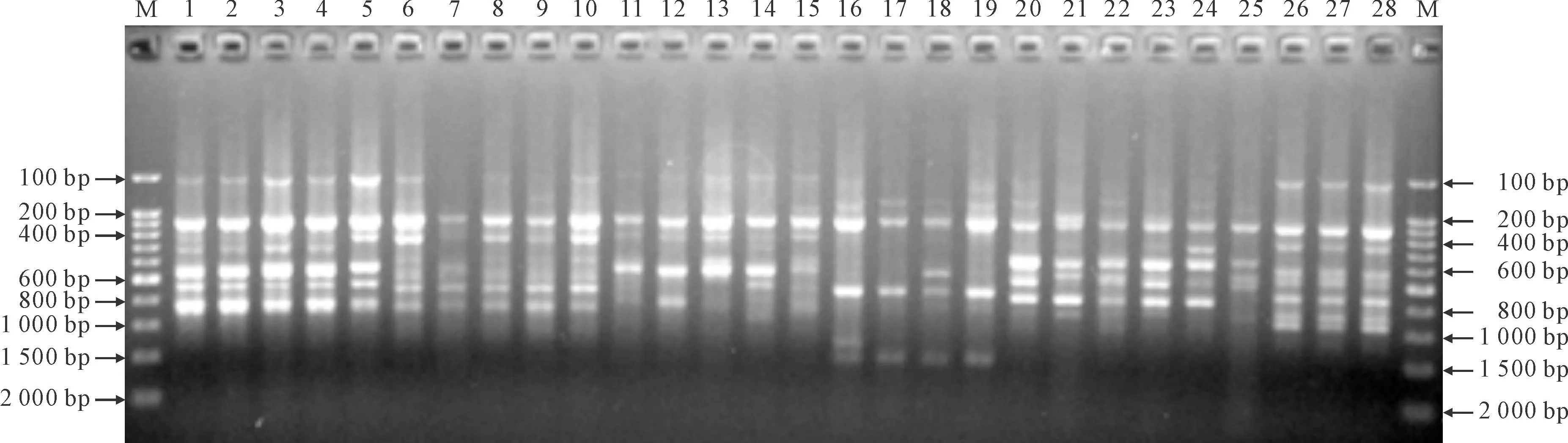
1~3.假百合,康定居群;4~9.大葉假百合;10~13.鐘花假百合;14~23.假百合×鐘花假百合;24~28.假百合,秦嶺居群
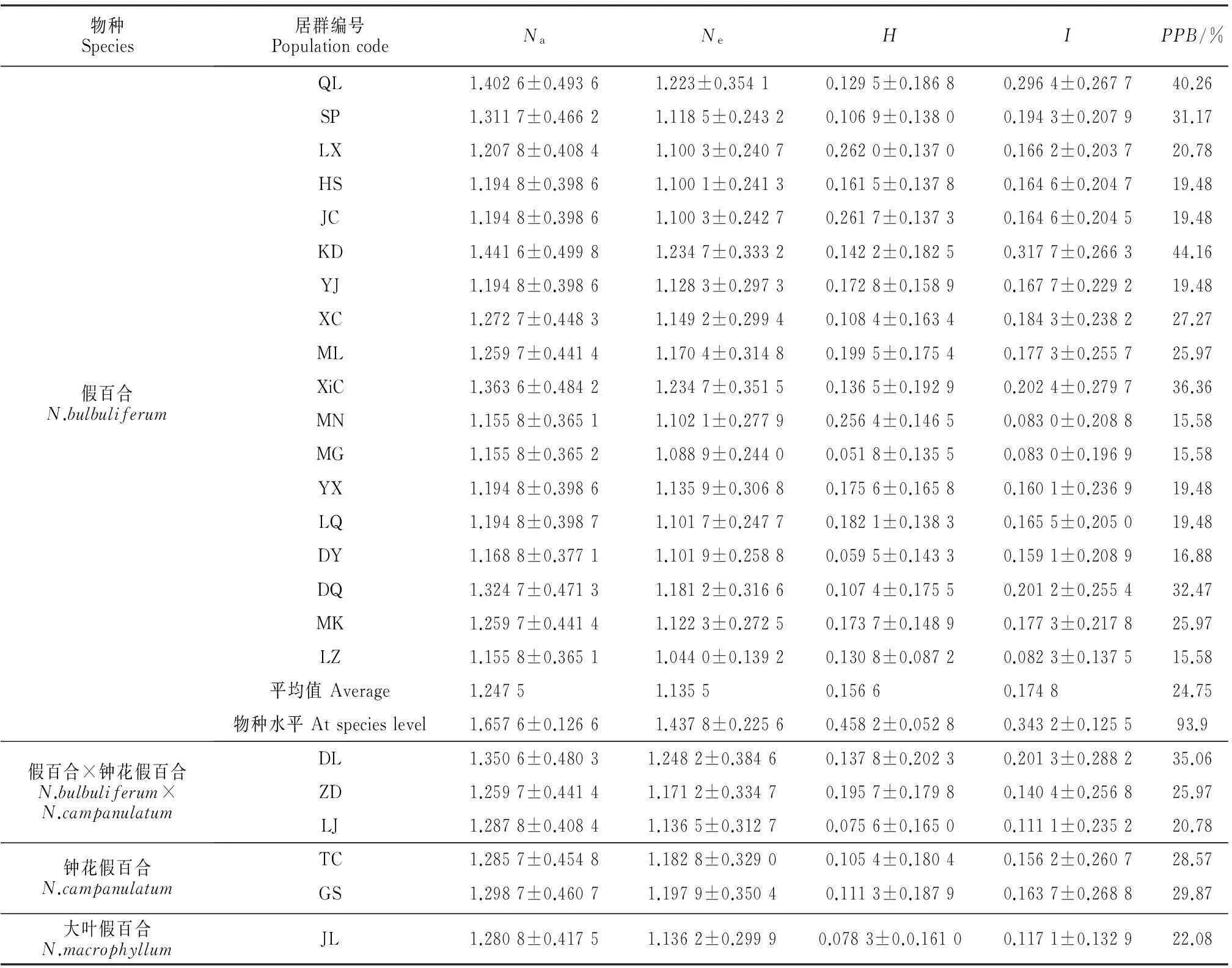
物種Species居群編號PopulationcodeNaNeHIPPB/%假百合N.bulbuliferumQL1.4026±0.49361.223±0.35410.1295±0.18680.2964±0.267740.26SP1.3117±0.46621.1185±0.24320.1069±0.13800.1943±0.207931.17LX1.2078±0.40841.1003±0.24070.2620±0.13700.1662±0.203720.78HS1.1948±0.39861.1001±0.24130.1615±0.13780.1646±0.204719.48JC1.1948±0.39861.1003±0.24270.2617±0.13730.1646±0.204519.48KD1.4416±0.49981.2347±0.33320.1422±0.18250.3177±0.266344.16YJ1.1948±0.39861.1283±0.29730.1728±0.15890.1677±0.229219.48XC1.2727±0.44831.1492±0.29940.1084±0.16340.1843±0.238227.27ML1.2597±0.44141.1704±0.31480.1995±0.17540.1773±0.255725.97XiC1.3636±0.48421.2347±0.35150.1365±0.19290.2024±0.279736.36MN1.1558±0.36511.1021±0.27790.2564±0.14650.0830±0.208815.58MG1.1558±0.36521.0889±0.24400.0518±0.13550.0830±0.196915.58YX1.1948±0.39861.1359±0.30680.1756±0.16580.1601±0.236919.48LQ1.1948±0.39871.1017±0.24770.1821±0.13830.1655±0.205019.48DY1.1688±0.37711.1019±0.25880.0595±0.14330.1591±0.208916.88DQ1.3247±0.47131.1812±0.31660.1074±0.17550.2012±0.255432.47MK1.2597±0.44141.1223±0.27250.1737±0.14890.1773±0.217825.97LZ1.1558±0.36511.0440±0.13920.1308±0.08720.0823±0.137515.58平均值Average1.24751.13550.15660.174824.75物種水平Atspecieslevel1.6576±0.12661.4378±0.22560.4582±0.05280.3432±0.125593.9假百合×鐘花假百合N.bulbuliferum×N.campanulatumDL1.3506±0.48031.2482±0.38460.1378±0.20230.2013±0.288235.06ZD1.2597±0.44141.1712±0.33470.1957±0.17980.1404±0.256825.97LJ1.2878±0.40841.1365±0.31270.0756±0.16500.1111±0.235220.78鐘花假百合N.campanulatumTC1.2857±0.45481.1828±0.32900.1054±0.18040.1562±0.260728.57GS1.2987±0.46071.1979±0.35040.1113±0.18790.1637±0.268829.87大葉假百合N.macrophyllumJL1.2808±0.41751.1362±0.29990.0783±0.0.16100.1171±0.132922.08
2.3假百合屬聚類分析
通過NTSYSpc-2.10軟件計算出假百合屬各類群間遺傳相似性系數(Gs),結果顯示Gs值范圍從0.535 2到0.813 3,平均值為0.702 2。Gs最低值存在于大葉假百合與假百合之間為0.535 2,這表明其親緣關系最遠;最高值為鐘花假百合與N.bulbuliferum×N.campanulatum為0.813 3,說明其親緣關系最近。通過聚類分析也表明,大葉假百合與假百合相距最遠,假百合與鐘花假百合距離最近(圖4)。
2.4假百合遺傳多樣性
利用篩選的7個ISSR引物(表2)對假百合進行PCR擴增,共計擴增出83個清晰可重復的有效位點,其中多態位點有78個。結果顯示(表3):在物種水平上,假百合的多態位百分率(PPB)為93.9%,Ne為(1.437 8±0.225 6),H為(0.458 2±0.052 8),I為(0.343 2±0.125 5)。在居群水平上,各個居群的PPB范圍從15.58%~44.16%,平均值為24.75%。假設種群處于Hardy-Weinberg平衡條件下,18個居群的平均有效等位基因為1.247 5,平均Nei’s基因多樣性指數為0.135 5,平均Shannon多樣性信息指數為0.174 8,各項參數均低于物種水平。
Shannon多樣性指數表明各居群的遺傳變異由低到高為林芝<冕寧、美姑<大姚<越西<祿勸<雅江<黑水、金川<理縣<芒康、米林<鄉城<松潘<德欽<西昌<秦嶺<康定,與PPB值分析的結果一致。各居群間遺傳差異較大,其中康定居群(KD)的遺傳多樣性水平最高(PPB=44.16%,Ne=1.234 7,I=0.317 7),林芝居群間的遺傳多樣性水平最低(PPB=15.58%,Ne=1.044 0,I=0.082 3)。

居群編號同表1
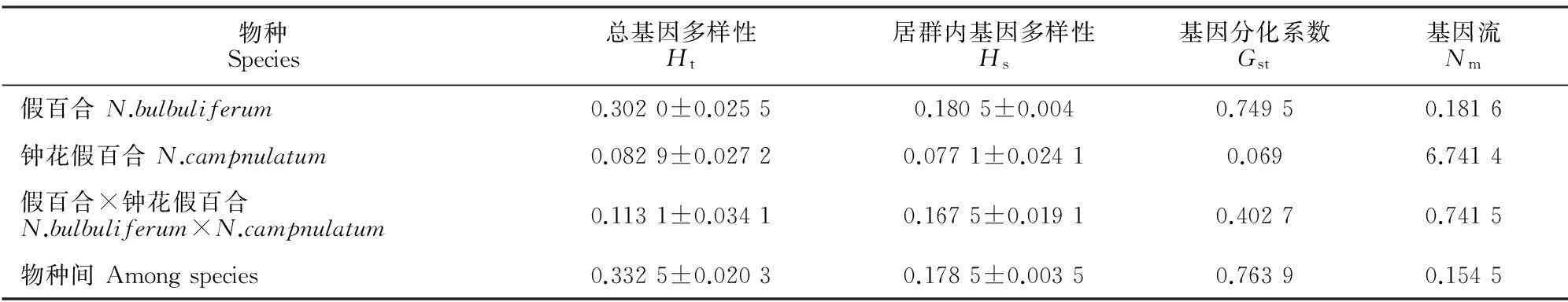
物種Species總基因多樣性Ht居群內基因多樣性Hs基因分化系數Gst基因流Nm假百合N.bulbuliferum0.3020±0.02550.1805±0.0040.74950.1816鐘花假百合N.campnulatum0.0829±0.02720.0771±0.02410.0696.7414假百合×鐘花假百合N.bulbuliferum×N.campnulatum0.1131±0.03410.1675±0.01910.40270.7415物種間Amongspecies0.3325±0.02030.1785±0.00350.76390.1545
2.5假百合遺傳分化與基因流
通過POPGENE 1.32軟件計算得出假百合18個居群Ht為0.302 0,Hs為0.180 5,Gst為0.749 5(表4),即74.95%的變異存在于居群之間,25.05%的變異存在于居群內,結果顯示居群間的遺傳分化大于居群內的分化。居群間的基因流(Nm)為0.181 6,表明居群之間的基因流水平較低。
利用AMOVA 1.55分析表明在總的遺傳變異中,有77.12%(P<0.001)的遺傳變異發生在居群之間,22.88%(P<0.001)的遺傳變異存在于居群內,與POPGENE 1.32分析結果一致,都表明遺傳變異主要存在于居群間。
2.6假百合聚類分析
POPGENE 1.32分析得出假百合18個居群兩兩間的Nei’s遺傳一致度(Hi),范圍為0.602 6~0.983 1,遺傳距離(D)為0.017 1~0.464 2(表5)。鄉城與雅江居群間遺傳一致度最高(Hi=0.983 1),遺傳距離最近(D=0.017 1),在聚類分析中也聚得最近(圖4);根據Nei’s遺傳相似性系數,使用NTSYSpc 2.1軟件中的SHANN對假百合18個居群進行UPGMA聚類分析,18個居群按照遺傳距離遠近以及遺傳一致度高低聚為2大支4個亞支(圖4)。其中雅江和鄉城遺傳一致度最高,遺傳距離最近首先聚在一起,然后與康定和木里聚為Clade Ⅰ;秦嶺、松潘、理縣、黑水和金川遺傳一致度與地理距離也較近優先聚為Clade Ⅱ;西昌、冕寧、越西與美姑形成Clade Ⅲ;祿勸、大姚等與其它居群則聚為Clade Ⅳ。2個大類在0.70閾值處聚在一起。Mantel關于地理距離和分子遺傳距離的檢測揭示了假百合居群間的地理距離和遺傳距離存在顯著的相關性(r=0.410,P=0.01)。
3討論
3.1中國假百合屬遺傳多樣性與種間親緣關系的探討
生物的遺傳多樣性是珍貴的自然資源,也是人類賴以生存的基礎。物種的遺傳多樣性越高說明其遺傳背景越復雜,同時也具有更強的進化潛力和對惡劣環境的耐受力,且更容易擴大生境以及適應新的環境[20]。在本研究中,利用7對ISSR引物對中國假百合屬4個類群進行了擴增。結果顯示多態性百分率(PPB)為100%。通常來說當PPB>50%時,被試物種的遺傳多樣性就被視為較高,這表明中國假百合屬植物具有很高的遺傳多樣性。根據花的形態以及顏色劃分,中國假百合屬下有3個種:假百合、鐘花假百合與大葉假百合。而后在云南西北部發現了N.bulbuliferum×N.campanulatum。因其形態特征在未開花時差距甚微,且假百合與鐘花假百合之間存在雜交,從表型上很難區分。然而假百合為名貴中藥材,所以對其正確鑒定十分必要,在本研究中遺傳相似性系數均值(Gs)為0.702 2,表明假百合屬種間具有較高的遺傳相似性;鐘花假百合作為雜交個體的母本與N.bulbuliferum×N.campanulatum具有較高的遺傳相似性(Gs=0.813 3)且在UPGAMA聚類分析中聚為一支,親緣關系最近,這可能與鐘花假百合作為雜交個體的母本且在種子植物中為母系遺傳有關[21-22];大葉假百合與假百合在聚類分析時也相距最遠,表明其親緣關系最遠。
3.2假百合遺傳多樣性及居群間遺傳分化
對于生物遺傳多樣性的研究是我們探討物種起源以及進化的基礎,并且可以為人類提供合理的保護、開發和利用的理論依據[23-24]。根據ISSR分析結果顯示,假百合物種水平上多態位百分率(PPB)為93.9%,Nei’s遺傳多樣性指數(H)為0.458 2,Shannon’s信息多樣性指數(I)為0.343 2。這一較高的遺傳多樣性可能是由于假百合的分布從秦嶺延伸到東喜馬拉雅以及生長在平均海拔高度為3 000 m的橫斷山區,而這一地區具有復雜的地質地貌,高山峽谷縱橫,生活環境多變。通常,物種具有廣泛的分布就會展現出較高的遺傳多樣性,這種現象在竹黃菌[25-26]的研究中也有發現。一方面,長期的地理隔離導致各居群間適應不同的環境,從而產生較大的遺傳變異;另一方面,也可能是假百合的祖先類群具有多樣性復雜的基因庫,而后由于青藏高原隆起[27]、橫斷山造山運動[28-29]以及第四紀冰期氣候的反復波動導致生境片段化后,而出現如今不同分布地間的遺傳差異。
假百合種下居群間的遺傳分化系數(Gst)為0.749 5,遠遠高于Nybom統計的多種植物ISSR遺傳分化系數均值(Gst=0.34)[30],同樣也高于寶興百合(Gst=0.642 5)、匍莖百合(Gst=0.563 7)的ISSR遺傳分化系數[14],這說明假百合居群間存在較高的遺傳分化。而且從NTSYSpc 2.10聚類結果以及各居群的采樣分布可以看出,Clade Ⅰ與Clade Ⅱ被折多山山脈隔開;Clade Ⅲ與Clade Ⅳ被金沙江流域阻隔;而這兩大支之間存在錦屏山山脈。橫斷山區復雜的地貌環境可能孕育了假百合的異質居群結構。而Mantel關于地理距離與遺傳距離的檢測存在極顯著的相關性也恰好說明這一點。雖然假百合有性生殖依靠蟲媒傳份,這會使得居群間遺傳分化降低,但是假百合生長在橫斷山區,該地區由高黎貢山、大雪山、錦屏山等7條幾乎平行的山脈和金沙江、瀾滄江與怒江等幾大流域組成,高山峽谷縱橫,大多數山脈海拔達到五千多米,形成了天然的地理隔離屏障。這種依靠蟲媒傳粉方式的植物被自然條件阻隔,從而限制了居群間的基因交流,這也是造成假百合居群間遺傳分化值高的又一原因。再者,假百合居群間的基因流(Nm)為0.181 6,當Nm<1時,遺傳漂變就可導致居群間明顯的遺傳分化[31],說明遺傳漂變也可能是假百合種下居群間遺傳分化較高的原因。
分布范圍、種子傳播機制、繁育系統等因素都可影響群體遺傳結構,但在異交類型植物中群體間的分化值一般較小[32]。假百合居群間遺傳分化系數遠高于遠交植物,這可能是因為假百合具有復雜的兼性生殖繁育系統[33]。在自然生存環境中,假百合具有大量的小鱗莖。野外取樣過程中觀察發現小鱗莖繁殖能力極強,在脫離母株后,大多數小鱗莖便形成無性生殖植株,同時也存在種子實生苗。假百合在漫長的進化歷史中和自然選擇的壓力下,已經形成了適應環境要求的有性和無性兩種繁育制度。通過大量觀察發現,假百合聚居現象特別明顯,大多成群分布,遇到有水溝的地方則沿水流方向兩岸分布。據此推測依靠小鱗莖的無性繁殖體系是假百合主要的繁殖方式。較強的無性繁殖能力導致了假百合居群內遺傳多樣性的降低。
3.3假百合可持續利用與保護策略
對于物種來說,遺傳多樣性水平高低與對環境的適應能力以及變異和進化潛力的強弱是緊密相關的[34]。豐富的遺傳多樣性是物種具有更高的適應和存活能力的基礎,從而才能提高物種的進化、繁殖以及優化遺傳結構的能力[35]。基于目前的研究顯示,假百合具有很高的遺傳分化。因此,對集巨大藥用價值與觀賞價值于一體的假百合野生資源以及遺傳多樣性的保護是非常有意義的。假百合野生居群被藥農大量采挖,加之近年來道路建設使得假百合生境破壞以及原生態旅游業的大規模開發,假百合大而艷麗的花朵吸引了游客的采摘。所以,對現存假百合居群應該采取一些有效的保護措施,比如:對假百合的生存環境適度保護,禁止人們過度采挖等;因秦嶺、松潘、康定、西昌、德欽等地具有較高的遺傳多樣性,這些具有豐富的基因多樣性資源的地區是將來進行育種的優良種質庫的來源,在制定保護措施和對其利用時應多加注意。
參考文獻:
[1]GAO Y D,HARRISA J,ZHOU S D,etal.Evolutionary events inLilium(includingNomocharis,Liliaceae) are temporally correlated with orogenies of the Q-T plateau and the Hengduan Mountains [J].MolecularPhylogeneticsandEvolution,2013,68(3):443-460.
[2]GAO Y D,ZHOU S D,HE X J.Chromosome diversity and evolution in tribe Lilieae (Liliaceae) with emphasis on Chinese species [J].JournalofPlantResearch,2012,125:55-69.
[3]梁松筠.百合科(狹義)植物的分布區對中國植物區系研究的意義[J].植物分類學報,1995,33(1):27-51.
LIANG S Y.Chorology of Liliaceae (S.STR) and it’s bearing on the Chinese acta phytotaxonom [J].JournalofSystematicsandEvolution,1995,33(1):27-51.
[4]BAKER J G.Revision of the genera and species ofTulipeae[J].JournaloftheLinneanSociety,1871,14:211-310.
[5]BOISSIER E.Genevaeet Basileae:H.Georg Bibliopolam[J].FloraOrientalis,1884,5:172-203.
[6]COTTON A D,STEARN W T.The genusNotholirion[J].LilyYear-Book,1934,3(19):f.6.
[7]STEARN W T,COTTON A D.A note onParadisea,DiurantheraandNotholirion[J].KewBulletin,1950,5(3):421.
[8]ZIETKIEWICE E,RAFALAKE A,LABUDA D.Genome fingerprinting by simple sequence repeat(SSR) anchored polymerase chain reaction amplification[J].Genomics,1994,20(2):176-183.
[9]DOYLE J J.Gene trees and species trees:molecular systematics as an one-character taxonomy[J].SystematicBotany,1992,71:144-163.
[10]TSUMURA Y,OHBA K,STRAUSS S H.Diversity and inheritance of inter-simple sequence repeat polymorphisms in Douglas-fir(Pseudotsugamenziesii) and sugi (Cryptomeriajapoonica) [J].TheoreticalandAppliedGenetics,1996,9:40-45.
[11]GUO W H,JEONG J,KIM Z,etal.Genetic diversity ofLiliumtsingtauensein China and Korea revealed by ISSR markers and morphological characters[J].BiochemicalSystematicsandEcology,2011,39:352-360.
[12]XI M L,SUN L N,QIU S,etal.Invitromutagenesis and identification of mutants via ISSR in lily (Liliumlongiflorum)[J].PlantCellReports,2012,31:1 043-1 048.
[13]ZHAO L H,LIU H M,CAI G Z ,etal.Assessment of the genetic diversity and genetic relationships ofLiliumin China using ISSR markers[J].BiochemicalSystematicsandEcology,2014,55:184-189.
[14]沈呈娟,周頌東,何興金.寶興百合與匍莖百合遺傳多樣性的ISSR分析[J].西北植物學報,2014,34(7):1 331-1 338.
SHEN C J,ZHOU S D,HE X J.Genetic diversity ofLiliumduhartreiandLiliumlankongenserevealed by ISSR markers [J].ActaBotanicaBoreali-OccidentaliaSinica,2014,34(7):1 331-1 338.
[15]NEI M.Estimation of average heterozygosity and genetic distance from a small number of individuals [J].Genetics,1978,89:583-590.
[16]YEH F C,YANG R C,BOTLE T B J,etal.POPGENE:The user friendly shareware for population genetic analysis.(Ver.1.32)[M].Canada:Molecular Biology and Biotechnology Centre,University of Alberta,1997.(program available from:http://www.ualberta.ca/~fyeh/).
[17]ROHLF F J.NTSYS-pc:Numerical Taxonomy and Multivariate Analysis System (Ver.2.1) Exeter Software [CP/DK].New York:Setauket,1998.
[18]EXCOFFIER L.AMOVA:Analysis of Molecular Variance (Ver.1.55) [CP/DK].Switzerland:Genetics and Biometry Laboratory,University of Geneva,1995.
[19]PEAKALL R,SMOUSE P E.GenAlEx 6.5:genetic analysis in Excel.Population genetic software for teaching and research——an update[J].Bioinformatics,2012,28:2 537-2 539.
[20]MARTINS M,TENREIRO R,OLIVEIRA M.Genetic relatedness of Portuguese almond cultivars assessed by RAPD and ISSR markers [J].PlantCellReports,2003,22:71-78.
[21]BAUMEL A,AINOUCHE M L,BAYER R J,etal.Molecular phylogeny of hybridizing species from the genusSpartina(Poaceae)[J].MolecularPhylogeneticsandEvolution,2002,22:303-314.
[22]ZHA H G,MILNE R I,SUN H.Asymmetric hybridization inRhododendronagastum:a hybrid taxon comprising mainly F1s in Yunnan,China [J].AnnalsofBotany,2010,105:89-100.
[23]HELENUR K.High levels of genetic polymorphism in the insular endemic herbJepsoniamalvifolia[J].JournalofHeredity,2001,92:427-432.
[24]LI E X,YI S,QIU Y X,etal.Phylogeography of two east asian species inCroomia(Stemonaceae) inferred from chloroplast DNA and ISSR fingerprinting variation[J].MolecularPhylogeneticsandEvolution,2008,49:702-714.
[25]FAN Y,ZHONG C G,CHENG J,etal.Genetic differentianton ofShiraiabambusicolapopulatins from east China revealed by RAPD analysis[J].GenomicsandAppliedBiology,2009,28(5):889-895.
[26]QI S S,FAN Y,GONG Z N,etal.Genetic diversity ofShiraiabambusicolafrom East China assessed using ISSR markers [J].BiochemicalSystematicsandEcology,2015,59:239-245.
[27]HARRISON T M,COPELAND P,KIDD W S F,etal.Raising Tibet [J].Science,1992,255:1 663-1 670.
[28]陳富斌.再論橫斷運動[J].火山地質與礦產,1996,17:14-21.
CHEN F B.Second discussion on the Hengduan movement [J].VolcanologyandMineralResources,1996,17:14-21.
[29]施雅風.晚新生代以來青藏高原的隆起與環境演化[M].廣州:廣州科學技術出版社,1998:6-20.
[30]NYBOM H,BARTISH I V.Effects of life history traits and sampling strategies on genetic diversity estimates obtained with RAPD markers in plants[J].PerspectivesinPlantEcologyEvolutionandSystematics,2000,3(2):93-114.
[31]SLATKIN M.Gene flow in natural population [J].AnnualReviewofEcology,Evolution,andSystematics,1985,16:393-430.
[32]HAMRICK J L,GODT M J W.Plant Population Genetics,Breeding,and Genetic Resources[M].Sinauer:Sunderland,Mass,1990:43-63.
[33]BUSSEL J D.The distribution of random amplified polymorphic(RAPD)diversity amongst population ofIsotomapetraea(Lobeliaceae)[J].MolecularEcology,1999,8:775-789.
[34]HOLSINGER K E.Genetics and Conservation of Rare Plant [M].New York:Oxford University Press,1991:20-55.
[35]FRANKHAM R,BALLOU J D,BRISCOE D A.Introduction to Conversation Genetics[M].Cambridge:Cambridge University Press,2002:10-36.
(編輯:宋亞珍)
Genetic Relationships ofNotholirionand Genetic Diversity ofN.bulbuliferumin China Revealed by ISSR Markers
YANG Mei,ZHOU Songdong*,HE Xingjin,PENG Chang
(Key Laboratory of Bio-Resources and Eco-Environment of Ministry of Education,College of Life Sciences,Sichuan University,Chengdu 610064,China)
Abstract:To understand the sibship of Notholirion and the genetic differentiation of N.bulbuliferum,the genetic diversity of 255 individuals from 24 populations was analyzed by using seven inter-simple sequence repeat (ISSR) markers.(1)The results of the UPGMA analysis exhibited significant genetic differentiation between N.bulbuliferum,N.campanulatum,and N.macrophyllum,which indicated that they are separate species.(2)N.bulbuliferum×N.campanulatum clustered together with N.campanulatum,which may be a result from the matrilineal inheritance and strong asexual reproduction capacity;its low gene flow (Nm=0.216 0) implied that N.bulbuliferum×N.campanulatum may be undergoing differentiation.(3)The Mantel test showed a substantial significant correlation between genetic and geographic distances in N.bulbuliferum (r=0.410,P=0.01),and clustered four groups.(4)The analysis of molecular variance (AMOVA) revealed that the variation of N.bulbuliferum among the populations was 77.12% (P<0.01),and the variation within the population was 22.88% (P<0.01).These findings clearly evidenced the genetic relationship of Notholirion in the Hengduan Mountains.Importantly,the high diversity of N.bulbuliferum found in this study indicated that reasonable measures should be taken for the conservation and restoration for medicinal and ornamental plant species.
Key words:genetic diversity;inter-simple sequence repeats (ISSR);Notholirion bulbuliferum;N.campanulatum;N.macrophyllum
中圖分類號:Q346.+5;Q789
文獻標志碼:A
作者簡介:楊梅(1989-),女,在讀碩士研究生,主要從事植物系統進化研究。E-mail:meiyang100418@163.com*通信作者:周頌東,副教授,碩士生導師,主要從事植物分類與系統進化相關方面的研究。E-mail:songdongzhou@ aliyun.com
基金項目:國家自然科學基金(31270241,31470009,31570198);國家基礎條件平臺;國家標本平臺教學標本子平臺(http://mnh.scu.edu.cn);科技部基礎性研究專項(2013FY112100)
收稿日期:2015-12-02;修改稿收到日期:2016-02-01
文章編號:1000-4025(2016)03-0449-09
doi:10.7606/j.issn.1000-4025.2016.03.0449

