基于微衛星標記的雪豹種群結構及遺傳多樣性

摘 要 掌握雪豹(Panthera uncia)的遺傳多樣性信息對其保護和管理有重要意義。對104只雪豹個體的組織樣品提取DNA,結合文獻中提供的70個雪豹基因分型數據,利用9個微衛星多態性位點進行遺傳多樣性研究。結果顯示:當樣本量從70個增加到174個時,雪豹種群有分化為2個種群的趨勢,即西北部群和中部群;共檢測到45個等位基因(Na),中部、西北部2個種群平均每個位點Na分別為4. 556和4. 667,平均期望雜合度(He)分別為0. 574和0. 591,平均觀測雜合度(Ho)分別為0. 517和0. 498。雪豹群體的平均近交系數(FIS)為0. 137,平均遺傳分化系數(FST)為0. 067,平均多態信息含量(PIC)為0. 602,種群間遺傳變異為15. 24%,種群內遺傳變異為84. 76%。9個微衛星位點具有中高程度多態性,與其他雪豹研究相比,2個雪豹種群遺傳多樣性處于中等水平,種群間遺傳分化水平處于中等程度,遺傳變異大部分來源于群體內部。研究結果對全球雪豹的種群結構和遺傳多樣性研究具有重要意義,也為雪豹未來的科學保護提供可靠的遺傳背景。
關鍵詞:雪豹;種群結構;遺傳多樣性;微衛星標記
中圖分類號:Q953
文獻標志碼:A
文章編號:2310 - 1490(2024)- 04 - 0699 - 10
DOI:10.12375/ysdwxb.20240402
雪豹(Panthera uncia)是全球廣泛關注的瀕危物種之一,隸屬于食肉目(Carnivora)貓科(Felidae)豹屬(Panthera)[1],通常出現在海拔3 000 ~ 4 500 m的區域,但在海拔900 ~ 1 500 m的戈壁沙漠的北部地區及海拔高至5 800 m的喜馬拉雅或青藏高原區域也有活動[2]。長期以來,因棲息地喪失、獵物減少、氣候變化以及非法盜獵等因素的影響,雪豹種群持續下降[3?4],已被列為國家一級重點保護野生動物和《中國生物多樣性紅色名錄:脊椎動物卷》瀕危(EN)等級[5?6]。目前,雪豹分布于我國青藏高原及其周邊的12個國家,是山地生物多樣性的旗艦物種[7]。在中國,雪豹分布在8個省區,其棲息地面積占全球雪豹棲息地面積的60%以上,中國在雪豹的物種保護方面有重要地位[1]。
了解并掌握雪豹的遺傳背景、致危因素及遺傳多樣性水平,對雪豹的科學保護具有重要意義。由于雪豹活動的特殊性,樣品采集面臨著諸多挑戰。隨著技術的發展,非損傷性遺傳取樣法提供了解決方案,通過收集野生動物脫落的毛發及排泄物等樣品,使用分子標記如擴增片段長度多態性[8]、隨機擴增多態性DNA[9]、線粒體基因[10]及微衛星[11]等,在這些分子標記中,微衛星因其高度多態性、選擇中性和共顯性等優點,在個體識別、遺傳多樣性評估和種群遺傳結構分析等方面具有廣泛的應用前景[12]。
目前,通過采集雪豹糞便獲得遺傳信息,并使用微衛星分子標記對雪豹群體遺傳多樣性進行了較廣泛的研究,已經覆蓋中國、蒙古國和印度等9 個國家[13?20]。有研究推測全球雪豹應分為3個亞種,西部亞種(P. uncia uncia)分布于天山山脈、帕米爾高原、喀喇昆侖山脈和喜馬拉雅山脈西段等;中部亞種(P. u. uncioides)分布于青藏高原和喜馬拉雅山中東段;北部亞種(P. u. irbis)分布于阿爾泰山脈和蒙古國南部戈壁[16]。綜合以上研究,與豹屬其他物種相比,雪豹的遺傳多樣性處于較低水平[1],但雪豹的遺傳多樣性及亞種劃分可能因樣本采集位置及數量受限而導致結果差異。因此,本研究進一步擴大雪豹的采樣范圍及數量,以獲得更準確的遺傳學數據,為未來的雪豹種群劃分及遺傳學保護提供科學依據。
1 材料與方法
1. 1 試驗樣本
以東北林業大學野生動植物檢測中心實驗室在執法鑒定和行業監管中采樣得到的104個雪豹個體組織樣本(101個來源于四川西部、西藏和青海等地,3個來自蒙古國進境執法檢查)為研究對象,將其置于密封袋中,-20 ℃保存。由文獻[16]獲得70個已知來源地的3個雪豹種群微衛星基因分型數據。
1. 2 DNA 提取
使用AxyPrep Genomic DNA Miniprep Kit(Axy?gen,美國)試劑盒按說明書對104個雪豹組織樣本進行DNA 提取。使用1. 0% 瓊脂糖凝膠電泳檢測DNA純度,用紫外分光光度計儀器(Implen,德國)測定DNA濃度,并置于-20 ℃保存備用。
1. 3 PCR 擴增
根據雪豹已有研究成果[16],選用9對微衛星引物(PUN1157、PUN82、PUN100、PUN8972、PUN1283、PUN80、PUN1270、PUN272、PUN44)用于肌肉樣本DNA的擴增(表1)。PCR反應體系和反應條件與文獻[16]一致。取3 μL PCR產物進行1. 0%瓊脂糖凝膠檢測,其中成功擴增的PCR產物用ABI 3730XL測序儀(Applied Biosystems Inc,美國)進行毛細管電泳檢測,得到等位基因大小。以上實驗,除DNA提取外,均由北京六合華大基因科技有限公司完成。
1. 4 數據處理
利用9個微衛星位點分別對70個文獻中的樣本和合并104個樣本后的全部樣本(174個)進行種群結構分析。主成分分析(principal component analy?sis,PCA)使用R 3. 2. 4的adegenet 1. 2. 4包[21]。種群結構分析使用Structure 2. 3. 4軟件[22]中的貝葉斯聚類方法,K 值1 ~ 8,每個K 值計算15次并確定最佳K值[23]。使用GenAlEx 6. 5[24]統計3個群體的等位基因數(Na)、有效等位基因(Ne)、觀測雜合度(Ho)、期望雜合度(He)、香農信息指數(I)、近交系數(FIS)和群體遺傳分化系數(FST)。使用PowerMarker 3. 25[25]統計遺傳多態性信息含量(PIC)以及個體間的Nei’s遺傳距離。基于174個雪豹樣本間Nei’s遺傳距離,使用MEGA11 軟件[26]的個體鄰接法(neighborjoining,NJ)構建聚類樹。使用Arlequin 3. 5. 2. 2 軟件[27]進行分子方差分析(analysis of molecular vari?ance,AMOVA)。
2 結果與分析
2. 1 PCR 擴增結果
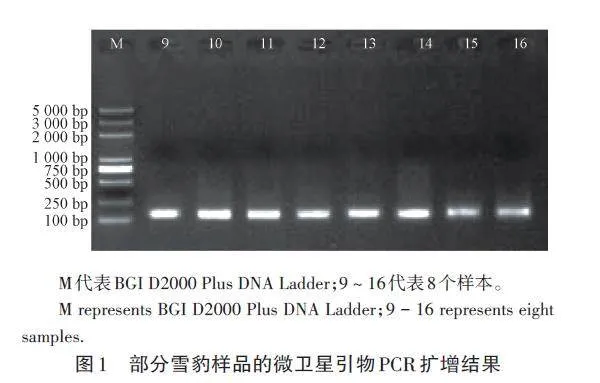
用9對微衛星引物對104個雪豹樣本DNA進行擴增,獲得長度在100 ~ 150 bp的擴增條帶,擴增條帶清晰,大小一致(圖1),可以用于后續多態性分析。
2. 2 種群結構
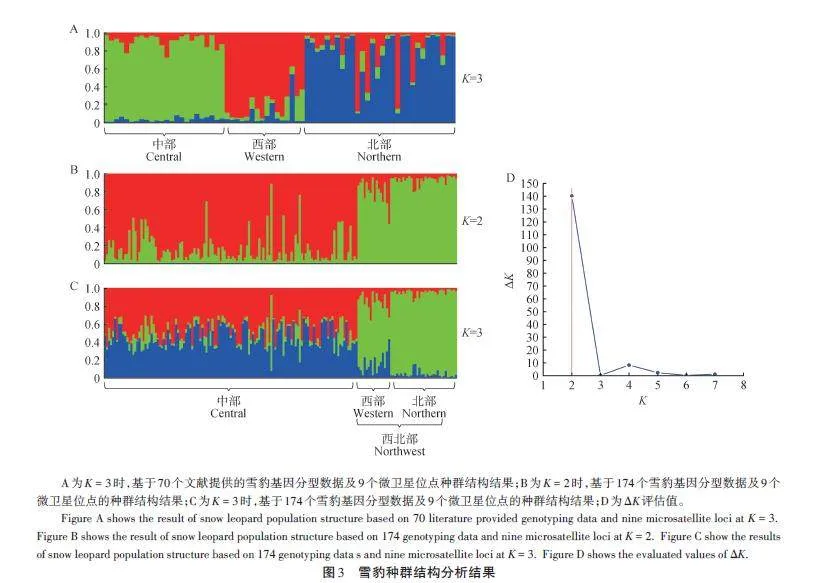
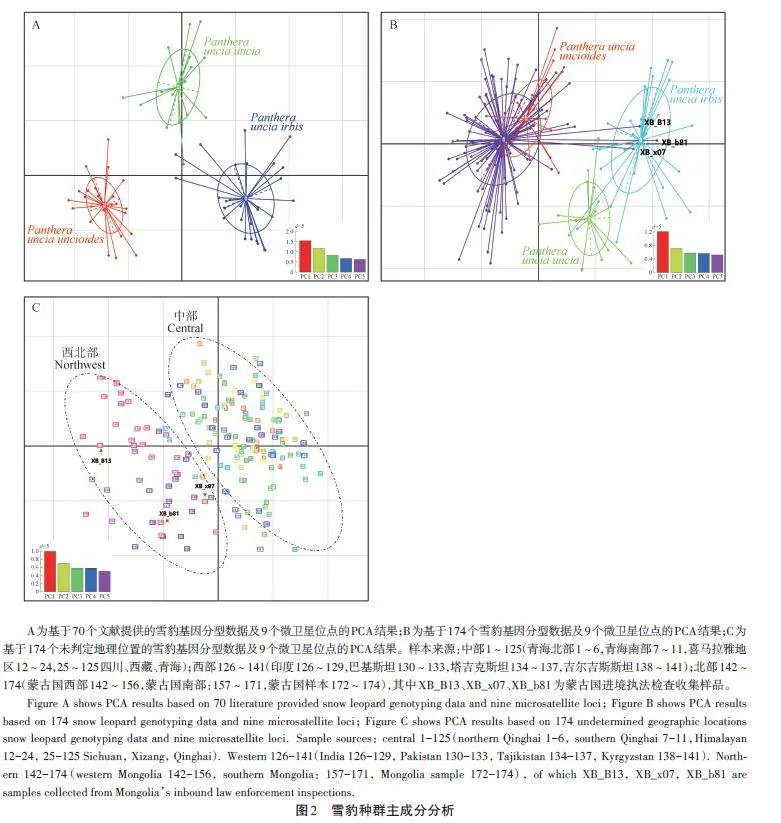
從圖2A可知,9個微衛星位點可將70個已知樣本數據按照3個雪豹種群清晰分開,表明這些微衛星位點具有較高的靈敏度。
全部樣本的PCA結果顯示:101個樣本與文獻[16]中的中部樣本聚集在一起,3個樣本與文獻[16]中的北部樣本聚集在一起,與樣本來源地相符(圖2B);同時相對于中部樣本,西部樣本與北部樣本呈現出聚集的趨勢。為排除地理標簽對PCA分析的影響,去除地理標簽限制后繪制的PCA結果顯示:整體數據主要分為2個聚類群(圖2C),即西部與北部種群數據并為一個群體,中部種群數據并為一個群體。
基于PCA 結果,對雪豹的種群結構進行分析。由圖3A可知,對于70個已知樣本,當K = 3時,中部、西部和北部種群祖先成分呈不同結構,與文獻[16]中的結果基本一致。174個樣本的分析結果顯示:當K = 2和K = 3時,兩種結果均體現出西部種群和北部種群祖先成分具有一致性(圖3B,C),且當K = 2時,ΔK 呈現最大值(圖3D)。結果表明,雪豹分為2個種群具有一定的合理性。
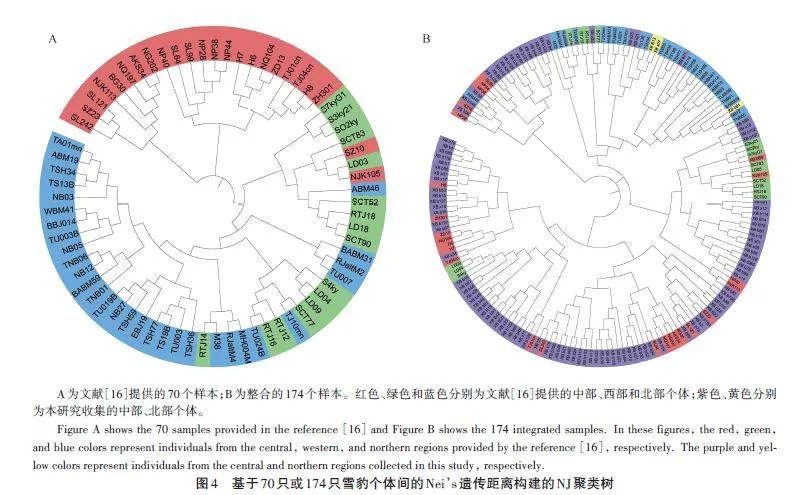
此外,基于70個樣本和174個樣本的Nei’s遺傳距離分別構建了NJ聚類樹(圖4)。70個樣本的聚類樹顯示(圖4A),西部與北部個體混合在一支,中部個體主要分為兩支;174 個樣本的聚類樹顯示(圖4B),西部與北部大部分個體仍主要聚集在一支,不過一部分中部個體與西部個體混在一支。雖然兩個NJ聚類樹均存在少量個體的混合穿插,但均表明西部與北部個體的遺傳距離較近,也支持雪豹西部與北部種群并為一個群體。
2. 3 遺傳多樣性分析
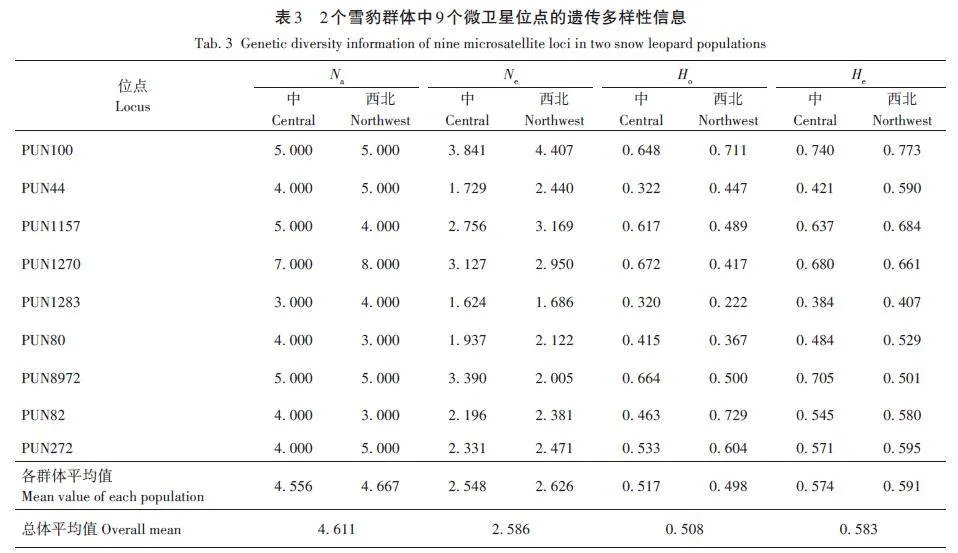
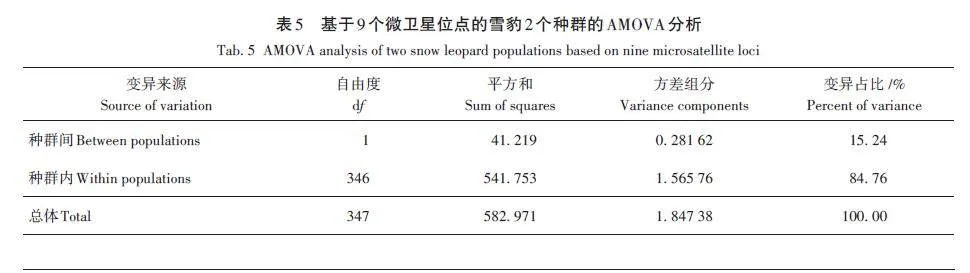
首先分析全部樣本的總體遺傳多樣性,共識別出45個Na。由表2可知,所有微衛星位點的Na平均值為4. 611(3. 500 ~ 7. 500);Ne 平均值為2. 587(1. 655 ~4. 124);I 平均值為1. 079(0. 707 ~ 1. 468);Ho 平均值為0. 508(0. 271 ~ 0. 679);He 平均值為0. 583(0. 396 ~ 0. 756);FIS平均值為0. 137,其中PUN82為負值,其余8個位點為正值;FST平均值為0. 067(0. 010 ~0. 179);PIC平均值為0. 602(0. 411 ~ 0. 787)。結果表明,9個位點均呈現中高程度的遺傳多樣性,其中3個位點表現為中度多態性(0. 25 lt; PIC lt; 0. 50),分別為PUN44、PUN1283和PUN82,其余位點均為高度多態性位點(PIC gt; 0. 50),遺傳多樣性較豐富。
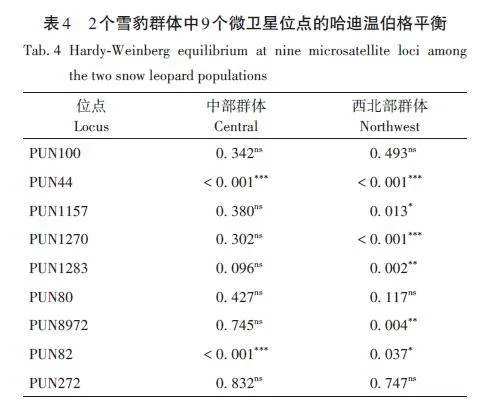
中部群和西北部群的遺傳多樣性結果顯示(表3):9 個位點在2 個種群中檢測到3 ~ 8 個Na,其中PUN1270位點檢測的Na數量最多,PUN1283、PUN80和PUN82位點檢測到的Na數量最少;中部和西北部2個種群的平均Na分別為4. 556和4. 667;平均Ne分別為2. 548和2. 626;平均Ho分別為0. 517和0. 498;平均He分別為0. 574和0. 591。哈迪溫伯格平衡檢驗結果顯示:在中部種群中,PUN44和PUN82兩個位點不符合哈迪溫伯格平衡;西北部種群中PUN44、PUN1157、PUN1270、PUN1283、PUN8972 和PUN82六個位點偏離哈迪溫伯格平衡(表4)。
2. 4 微衛星標記的遺傳分化
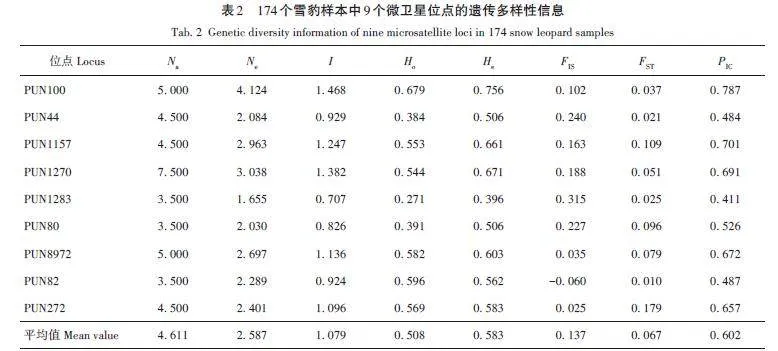
AMOVA結果顯示,在雪豹2個種群中,種群間的遺傳變異占15. 24%,種群內的遺傳變異占84. 76%(表5),表明變異大部分發生在種群內部,種群之間的遺傳變異所占比例較小,同時也表明2個雪豹種群間的基因交流較少,大部分的變異來源于群體內部。
3 討論
3. 1 雪豹種群遺傳結構
關于雪豹群體或亞種的劃分一直存在爭議。最早在2015年,Riordan et al.[28]根據模型分析雪豹種群的連通性,建議將雪豹分為南、北2個地理種群。在2017 年,Kitchener et al.[29]在對貓科動物重新分類時沒有采納該意見,依然判斷全球雪豹為1個種群。同年,Janecka et al.[16]基于33個微衛星位點,對70個雪豹糞便樣本進行基因分型,結合遺傳結構和地理隔離,支持將全球雪豹分為3個亞種。本研究利用9個微衛星位點,先后對文獻[16]中70只雪豹個體數據和174只個體數據進行分析,得到了不同的種群結構。70只雪豹數據的種群結構與文獻[16]結果相近(圖2A,圖3A),支持雪豹3個群體的劃分。但是,在174個樣本的結果中,西部群體和北部群體接近,形成一個群體,與中部種群相對應(圖2B、C);種群結構上也支持了2個群體的劃分(圖3B、C,圖4)。出現這樣的變化,可能歸因于Janecka et al.[16]研究的樣本量較小、地理覆蓋不全,進而放大了小群體之間的差異。當樣本量增大時,西部群體和北部群體逐步聚集。實際上,Janecka et al.[16]的研究結果也支持這一觀點,例如,在其小樣本分析中,雖然都存在少量混合,但北方群體的蒙古國西部群(15個樣本)和南部群(17個樣本)形成了2個不同的集群(文獻[16]圖2i);中部群體也分成了2個群體(文獻[16]圖2g),青海地區群(北部和南部,共11個樣本)與西藏地區群(含不丹和尼泊爾,共13 個樣本)。Senn et al.[30]也認為Janecka et al. 的研究缺乏足夠的樣本量,不足以支持3個亞種的劃分。兩個NJ聚類樹也支持北部與西部群體并為一個群體,聚類樹上少量個體的混合穿插,可能與群體間的基因流動有關,也可能與微衛星位點數量偏少、精度不夠有關。因此,本研究認為目前的研究結果不支持Jan?ecka et al. 雪豹3個亞種的劃分,支持將雪豹按照2個群體劃分,即中部群和西北部群。在地理上,雪豹中部群體與北部、西部群體也存在一定的阻隔。雪豹中部群體,在北方有戈壁沙漠與北部群體相隔[1],南部有喜馬拉雅山脈與其南麓相隔,西部有塔克拉瑪干沙漠、塔里木盆地和南部的喀喇昆侖山脈等[31],也可能阻隔了其與西部群體的交流。不過,相對于中部樣本(125個),西部(16個)和北部(33個)的樣本數量仍較少,樣本數量不平衡可能影響了研究結果。
3. 2 雪豹種群遺傳多樣性
遺傳多樣性水平可以反映物種的進化潛力[32],能為物種現狀評估和保護提供重要信息[33]。目前,使用微衛星標記的方法對雪豹種群進行遺傳多樣性研究,樣本范圍覆蓋了9個國家,樣本數共達到211只,但單次研究中每個地區有效的樣本采集數量不超過30只[1],而且關于雪豹群體遺傳多樣性的不同研究結果出現了一定的波動。
多態信息含量是表示微衛星位點變異程度高低、衡量基因片段多態性的一個指標[34],包括低度多態性位點(PIC lt; 0. 25)、中度多態性位點(0. 25 0. 50)[35]。本研究使用的9個微衛星位點中,不存在低度多態性位點,適用于雪豹遺傳學分析。全部雪豹群體在9個微衛星位點上檢測到的Na 為3 ~ 8,Ne 為1. 655 ~4. 124,在其他雪豹研究中,Na為2. 571 ~ 6. 286[13?20],Ne為2. 031 ~ 2. 800[16,20],本研究結果與已有研究結果基本一致。本研究結果中Na 和Ne 的數值范圍更大,可能與樣本量大有關。此外,Na值均大于Ne,表明等位基因分布不均勻,存在差異,可能受到群體間潛在的近親繁殖或遺傳漂變等因素的影響,未來種群也存在等位基因丟失以及遺傳多樣性下降的風險。
雜合度是衡量群體遺傳多樣性程度最重要的指標之一,數值越大代表種群間遺傳多樣性越豐富。此前關于雪豹的遺傳多樣性研究中,不同調查群體的Ho在0. 371 ~ 0. 887,He在0. 330 ~ 0. 781[13?20]。本結果中,中部和西北部2 個雪豹群體的Ho 分別為0. 517和0. 498,He分別為0. 574和0. 591,與此前的研究結果相比,處于中等水平,可能是樣本量增大之后得到了更接近于雪豹整體實際情況的結果。在這些研究中,周蕓蕓等[19]在青海2個縣以及甘肅阿克塞縣調查的雪豹遺傳多樣性偏高(平均Ho為0. 843,平均He為0. 759),可能歸因于樣本量小而產生的差異。通過雜合度數值,與豹屬其他物種[1]相比,雪豹的遺傳多樣性較低。
結果中所有位點的FIS 平均值為0. 137,遠低于巴基斯坦地區雪豹的FIS 平均值(0. 38)[18]。可能歸因于在巴基斯坦進行雪豹樣本采集的5個地區相距較近,而且該國雪豹分布范圍較小、數量較少[7],因此,可能加劇了群體內部近親繁殖的概率。當種群數量擴大時,近交系數下降,表明在更大的雪豹分布區中,雪豹的近交程度可能沒有達到更高的水平。相比于近交程度較低的大熊貓(Ailuropoda melano?leuca)(種群平均FIS為0. 081)[12,36]和近交程度很高的華南虎(Panthera tigris amoyensis)(0 lt; FIS lt; 0. 42)[12,37],雪豹種群近交程度偏低。
以上分析中,不同研究得到的雪豹遺傳多樣性指標存在著一定的波動,這可能受到樣本數量及采樣范圍大小的影響,當樣本量大、地理來源更廣時,得到的結果可能更接近于實際情況。不過局部小樣本量的研究,對當地雪豹小種群的保護管理也具有一定的指導意義。
本研究利用174只雪豹個體9個位點的微衛星數據,對雪豹種群結構和遺傳多樣性進行分析,現有的結果支持將雪豹劃分為2個群體,即中部群體和西北部群體。與其他雪豹有關研究相比,這2個種群的遺傳多樣性處于中等水平,近交水平也較低(低于Aruge et al.[18]的研究),略高于大熊貓。本研究通過大樣本微衛星數據對全球雪豹的遺傳結構進行了分析,對雪豹的種群劃分和遺傳多樣性提供了更全面的數據支持,對雪豹的遺傳多樣性研究和指導保護實踐具有重要意義。
參考文獻:
[1] 郝宇波, 金紅, 楊林,等. 雪豹保護遺傳學和基因組學研究進展[J]. 獸類學報, 2022, 42(5): 508-518.
HAO Y B, JIN H, YANG L, et al. Research advances in conser?vation genetics and genomics of snow leopard (Panthera uncia)[J]. Acta Theriologica Sinica, 2022, 42(5): 508-518.
[2] JACKSON R, MALLON D, MISHRA C, et al. Snow leopard sur?vival strategy: revised version 2014. 1 [R]. Seattle:Snow Leop?ard Network, 2014: 17.
[3] MAHESHWARI A, NIRAJ S K. Monitoring illegal trade in snowleopards: 2003-2014[J]. Global Ecology and Conservation,2018, 14: e00387.
[4] 洪洋,張晉東. 臥龍自然保護區雪豹的生境選擇偏好與食源結構特征[J]. 野生動物學報,2021,42(2):295-305.
HONG Y, ZHANG J D. Habitat selection and food source of snowleopard (Panthera uncia) in Wolong National Nature Reserve, Si?chuan Province, China[J]. Chinese Journal of Wildlife,2021,42(2):295-305.
[5] 國家林業和草原局,農業農村部. 國家重點保護野生動物名錄(2021 年2 月1 日修訂)[J]. 野生動物學報,2021,42(2):605-640.
National Forestry and Grassland Administration, Ministry of Agri?culture and Rural Affairs. List of national key protected wild ani?mals (revised on February 1, 2021) [J]. Chinese Journal ofWildlife, 2021, 42(2): 605-640.
[6] 生態環境部, 中國科學院. 中國生物多樣性紅色名錄: 脊椎動物卷(2020)[EB/OL].(2023-05-18)[2024-04-10]. https://www. mee. gov. cn/xxgk2018/xxgk/xxgk01/202305/t20230522_1030745. html.
Ministry of Ecology and Environment, Chinese Academy ofSciences. China’s red list of biodiversity: vertebrate volume(2020)[EB/OL]. (2023-05-18)[2024-04-10]. https://www.mee. gov. cn/xxgk2018/xxgk/xxgk01/202305/t20230522_1030745.html.
[7] 楊子文,韓姝伊,李壹,等. 氣候變化對雪豹全球潛在適生區分布的影響與評估[J]. 生態學報,2023,43(4):1412-1425.YANG Z W, HAN S Y, LI Y, et al. Impacts and assessment ofclimate change on the global distribution of potentially suitablehabitats for Panthera uncia[J]. Acta Ecologica Sinica, 2023,43(4):1412-1425.
[8] PFAU R S, KOZORA A N, GATICA-COLIMA A B, et al. Popu?lation genetic structure of a Chihuahuan Desert endemic mammal,the desert pocket gopher, Geomys arenarius[J]. Ecology and Evo?lution, 2023, 13(10): e10576.
[9] HUSSEIN M A A, EID M, RAHIMI M, et al. Comparative as?sessment of SSR and RAPD markers for genetic diversity in somemango cultivars[J]. PeerJ, 2023, 11: e15722.
[10] RAJ N, SUKUMARAN S, JOSE A, et al. Population geneticstructure of Randall’s threadfin bream Nemipterus randalli in In?dian waters based on mitochondrial and nuclear gene sequences[J]. Scientific Reports, 2024, 14(1): 7556.
[11] SHANG K, ZHANG L W, SONG J R, et al. Characterization ofthe microsatellite landscape provides insights into the evolution?ary dynamics of the mammals based on the chromosome-level ge?nomes[J]. Gene, 2023, 851: 146965.
[12] 魏輔文, 馬天笑, 胡義波. 中國瀕危獸類保護遺傳學研究進展與展望[J]. 獸類學報, 2021, 41(5): 571-580.
WEI F W, MA T X, HU Y B. Research advances and perspec?tives of conservation genetics of threatened mammals in China[J]. Acta Theriologica Sinica, 2021, 41(5): 571-581.
[13] JACKSON R, AHLBORN G. Snow leopards (Panthera uncia)in Nepal: home range and movements[J]. National GeographicResearch, 1989, 5(2): 161-175.
[14] JANECKA J E, JACKSON R, MUNKHTSOG B, et al. Charac?terization of 9 microsatellites and primers in snow leopards and aspecies-specific PCR assay for identifying noninvasive samples[J]. Conservation Genetics Resources, 2014, 6(2): 369-373.
[15] JANE?KA J E, JACKSON R, YUQUANG Z, et al. Populationmonitoring of snow leopards using noninvasive collection of scatsamples: a pilot study[J]. Animal Conservation, 2008, 11(5):401-411.
[16] JANECKA J E, ZHANG Y G, LI D Q, et al. Range-wide snowleopard phylogeography supports three subspecies[J]. Journal ofHeredity, 2017, 108(6): 597-607.
[17] ROZHNOV V V, ZVYCHAINAYA E Y, KUKSIN A N, et al.Noninvasive molecular genetic analysis in studying the ecology ofthe snow leopard: problems and prospects[J]. Russian Journalof Ecology, 2011, 42: 439-444.
[18] ARUGE S, BATOOL H, KHAN F M, et al. A pilot study:ge?netic diversity and population structure of snow leopards of Gilgit-Baltistan, Pakistan, using molecular techniques[J]. PeerJ,2019, 7: e7672.
[19] 周蕓蕓, 朵海瑞, 薛亞東, 等. 雪豹的微衛星DNA遺傳多樣性[J]. 動物學雜志, 2015, 50(2): 161-168.ZHOU Y Y, DUO H R, XUE Y D, et al. Genetic diversityanalysis of microsatellite DNA in snow leopard (Panthera uncia)[J]. Chinese Journal of Zoology, 2015, 50(2): 161-168.
[20] 張于光, HACKER C, 張宇,等. 三江源和祁連山國家公園雪豹種群的遺傳結構分析[J]. 獸類學報, 2019, 39(4):442-449.
ZHANG Y G,HACKER C, ZHANG Y, et al. An analysis of ge?netic structure of snow leopard populations in Sanjiangyuan andQilianshan National Parks [J]. Acta Theriologica Sinica, 2019,39( 4): 442-449.
[21] JOMBART T. adegenet: a R package for the multivariate analy?sis of genetic markers[J]. Bioinformatics, 2008, 24(11):1403-1405.
[22] PRITCHARD J K, STEPHENS M, DONNELLY P. Inference ofpopulation structure using multilocus genotype data[J]. Genet?ics, 2000, 155(2): 945-959.
[23] LI Y L, LIU J X. StructureSelector: a web?based software to se?lect and visualize the optimal number of clusters using multiple methods[J]. Molecular Ecology Resources, 2018, 18(1):176-177.
[24] PEAKALL R, SMOUSE P E. GenAlEx 6. 5: genetic analysis inExcel. Population genetic software for teaching and research: anupdate[J]. Bioinformatics, 2012, 28(19): 2537-2539.
[25] LIU K J, MUSE S V. PowerMarker: an integrated analysis envi?ronment for genetic marker analysis[J]. Bioinformatics, 2005,21(9): 2128-2129.
[26] TAMURA K, STECHER G, KUMAR S. MEGA11: molecularevolutionary genetics analysis version 11[J]. Molecular Biologyand Evolution, 2021, 38(7): 3022-3027.
[27] EXCOFFIER L, LISCHER H E L. Arlequin suite ver 3. 5: anew series of programs to perform population genetics analysesunder Linux and Windows[J]. Molecular Ecology Resources,2010, 10(3): 564-567.
[28] RIORDAN P, CUSHMAN S A, MALLON D, et al. Predictingglobal population connectivity and targeting conservation actionfor snow leopard across its range[J]. Ecography, 2016, 39(5):419-426.
[29] KITCHENER A C, BREITENMOSER-WüRSTEN C, EIZIRIKE, et al. A revised taxonomy of the Felidae: the final report ofthe cat classification task force of the IUCN/SSC cat specialistgroup[J]. Cat News, 2017(Special Issue 11):1-80.
[30] SENN H, MURRAY-DICKSON G, KITCHENER A C, et al.Response to Janecka et al. 2017[J]. Heredity, 2018, 120(6):581-585.
[31] LI J, MCCARTHY T M, WANG H, et al. Climate refugia ofsnow leopards in High Asia[J]. Biological Conservation, 2016,203: 188-196.
[32] FRANKEL O H, SOULé M E. Conservation and evolution[M].Cambridge: Cambridge University Press, 1981:358.
[33] HOGBIN P M, PEAKALL R. Evaluation of the contribution ofgenetic research to the management of the endangered plant Zie?ria prostrata[J]. Conservation Biology, 1999, 13(3): 514-522.
[34] 耿廣耀,由玉巖,劉群秀. 豚鹿SSR標記開發與遺傳多樣性分析[J]. 野生動物學報,2022,43(3):816-820.
GENG G Y, YOU Y Y, LIU Q X. SSR molecular marker devel?opment and genetic diversity analysis of Axis porcinus[J]. Chi?nese Journal of Wildlife,2022,43(3):816-820.
[35] 方黎明,付春正,李慧,等. 浙江長興揚子鱷種群遺傳多樣性研究[J]. 野生動物學報,2022,43(3):741-751.
FANG L M, FU C Z, LI H, et al. Research on population ge?netic diversity of Alligator sinensis in the Changxing City, Zheji?ang Province[J]. Chinese Journal of Wildlife,2022,43(3):741-751.
[36] SHAN L, HU Y B, ZHU L F, et al. Large-scale genetic surveyprovides insights into the captive management and reintroductionof giant pandas[J]. Molecular Biology and Evolution, 2014, 31(10): 2663-2671.
[37] XU Y C, FANG S G, LI Z K. Sustainability of the south Chinatiger: implications of inbreeding depression and introgression[J]. Conservation Genetics, 2007, 8(5): 1199-1207.
基金項目:國家林業和草原局機關業務委托項目(HFW220200050)

