農作物病原卵菌基因組數據庫資源概述
高亞梅, 王相晶, 向文勝*
(1.東北農業大學生命科學學院,哈爾濱 150030;2.黑龍江八一農墾大學生命科學技術學院,大慶 163319)
卵菌(Oomycetes)屬于色藻界(Chromista),包括腐生菌及植物、動物和許多微生物的病原菌。病原卵菌導致許多作物、花卉等發生災難性病害,例如引起大豆疫霉根腐病的大豆疫霉(Phytophthora sojae Kaufmann et Gerdemann);引起的馬鈴薯晚疫病的 致 病 疫 霉 [P.infestans (Montagne)de Bary][1-2]。在進化地位上,卵菌與褐藻和硅藻有較近的親緣關系,形成一個獨特的二倍體微生物類群[3],其分子遺傳學的研究相對落后。隨著分子生物學技術的發展,卵菌基因組學及功能基因組學的研究逐漸受到研究者的重視,迅速積累了大量基因組數據資源,這些資源又成為卵菌功能基因組學研究的基礎之一,同時也是基因組數據挖掘的重要來源,加快了卵菌分子生物學的各項研究。本文對農作物病原卵菌基因組數據庫資源及其檢索方法做一概述。
1 卵菌結構基因組學數據庫資源及檢索方法
隨著測序技術的不斷發展,高通量測序使得測序成本不斷降低,越來越多的基因組計劃啟動,甚至可以用宏基因組學(metagenomics)技術測定一個生物群體的序列。因此,在各類數據庫中積累了海量的生物序列信息,供研究者檢索、下載和分析。基因組序列及結構、基因功能和調控元件的相關注釋可為深入研究病原菌毒力、致病性、寄主特異性調控、病原菌生化與生理機制、生態位適應性等提供大量有用信息。目前,共有7個卵菌物種[大豆疫霉P.sojae、分枝疫霉P.ramorumWerres,De Cock et Man、致病疫霉 P.infestans、辣椒疫霉P.capsici Leonian、終極腐霉 Pythium ultimum Trow、Hyaloperonospora parasitica (G?um.)G?ker,Riethm.,Voglmayr,Weiss & Oberw.和古巴假霜霉 Pseudoperonospora cubensis (Berkeley et Curtis)Rostovzev]的全基因組序列正式對外公布(詳見表1)[4-9];另外2個卵菌物種(Peronospora parasitica Tul.及Saprolegnia parasitica Coker)的基因組測序工作正在進行中。通過對這些基因組序列和結構的分析揭示了卵菌基因組在大小、致病相關基因、專性活體寄生等方面存在多樣性[10],并為病原菌遺傳與致病機理、宿主-病原菌相互作用的特征(宿主的特異性,毒性策略等)以及宿主-病原菌相互作用的進化等各方面研究提供了大量的信息。基因組分析揭示的卵菌基因組進化特征包括重復序列在基因組內的擴增、缺失、基因融合和基因垂直轉移等[11-13]。這些無疑都加深了我們對于卵菌基因組結構及進化的認識。

表1 已公布的測序卵菌基因組信息資源Table 1 Oomycete sequenced genome database resources
聯合基因組研究所JGI網站(DOE Joint Genome Institute)提供細菌、古細菌、真核生物和宏基因組等眾多物種的基因組序列信息和分析服務,在其主頁的搜索工具欄選擇相應的物種即可進入相應物種的數據庫,其中卵菌物種包括P.sojae、P.ramorum和P.cinnamomi[14]。基因組序列信息可通過該數據庫SEARCH功能進行關鍵詞檢索,利用BLAST進行序列相似性搜索,利用DOWNLOAD下載,利用BROWSE以圖形化方式瀏覽(見圖1)。另外 GO、KEGG、KOG、CLUSTER、SYNTENY提供基因功能、代謝圖譜、共線性、簇等注釋信息的查詢檢索。

圖1 JGI網站P.cinnamomi var.cinnamomi基因組瀏覽界面Fig.1 The genome browse interface of P.cinnamomi var.cinnamomi in JGI
VMD數據庫(VBI Microbial Database)[15]是另一重要的卵菌基因組數據庫,包括Pythium ultimum(V1.0),Phytophthora infestans(V4.0),P.capsici(V11.0),P.sojae(V1.0,V4.0,V5.0),P.ramorum(V1.0),H.arabidopsidis(V3.0,V6.0,V8.3)基因組及注釋信息。每個數據庫均提供圖形化的瀏覽方式,顯示每個基因的位置、模式和相關基因組的BLAST信息等。VMD數據庫還提供檢索、下載、注釋和工具箱等服務。檢索可以通過不同方式進行,包括 Gene ID、GO ID、Scaffold Number、protein domains/motifs/functions、primary annotation、affymetrixID 等。檢索結果頁面提供基因的序列、基因組位置、功能注釋及軟件預測結果等信息。BLAST工具提供多個可選數據庫,包括已測序卵菌基因組、表達數據庫、大豆和擬南芥數據庫等,進行有針對性的序列相似性比對分析。P.infestans T30-4基因組序列可以在Phytophthora infestans Database數據庫下載,該數據庫同樣提供各類分析工具和可視化的瀏覽頁面。
Pythium Genome Database是專門存儲Pythium ultimum序列信息的數據庫,包括其代表性菌株Pythium ultimum DAOM BR144的基因組序列和不同營養條件下的菌絲體的EST序列。在Pythium Genome Database可以下載 Genome Assembly、Transcripts、Proteins和Gene Model GFF3的信息。通過Genome Browser可視化瀏覽基因組,可以使用序列名、基因名、遺傳位點或區域標記進行檢索。BLAST工具可以選擇卵菌基因組、表達數據等12個數據庫進行序列比對。該數據庫還將儲存Pythium ultimum另一菌株高通量測序結果,開展對兩菌株及它們與其他已測序卵菌的基因組比較研究。
卵菌基因組測序多采用第二代測序技術,隨著測序成本的下降,將會有更多的卵菌基因組數據產生,包括致病菌和非致病菌,為功能基因組學和比較基因組學研究提供更多的數據。
2 卵菌功能基因組學數據庫資源及檢索方法
目前,在各種數據庫中均存儲了大量的各種類型、代表不同信息的數據,如何對這些數據進行分析,獲得蘊含其中的生物學意義是當前生物信息學的重要研究領域。利用生物信息學方法對卵菌基因組內大量未知功能基因的分析比較是基因功能研究和數據注釋的重要手段。以下介紹的一些常用的卵菌EST數據庫、綜合性功能基因組資源平臺和專門數據庫是開展卵菌功能基因組學研究的重要資源。
2.1 卵菌EST數據庫資源
卵菌表達序列標簽EST序列(Expressed Sequence Tags,ESTs)的大量公布為進行全面的基因結構和功能研究提供了重要的數據,必將促進對卵菌致病分子機制的認識,從而為防治卵菌病害設計合理有效的策略。目前數據庫中的EST序列集中在已正式公布的基因組序列的卵菌物種中,例如已有大豆疫霉(P.sojae)的 EST約33350條,而致病疫霉(P.infestans)有99320條(http:∥phytophthora.vbi.vt.edu/EST),還包括一些正在或已完成測序的卵菌物種P.capsici、Phytophthora brassicae De Cock et al、Albugo candida (Pers.)Roussel等[16]。這些 EST序列大部分為病原卵菌侵染寄主植物過程中的轉錄組,代表疫霉侵染與致病過程中表達的基因,還包括卵菌不同發育階段及不同環境條件下的EST。卵菌EST存放于多個數據庫中,如基因組的數據庫、NCBI、轉錄組數據庫OTD等,提供多種途徑可以獲取和檢索。
OTD卵菌轉錄組學數據庫(Oomycetes Transcriptomics Database,V4.0,http:∥vmd.vbi.vt.edu/transcripts/)是一個整合的轉錄組和EST數據資源的數據庫[17],儲存卵菌侵染寄主和不同生長條件下的轉錄組數據,包括EST序列、NGS(next generation sequencing)轉錄組序列、數字基因表達譜序列 (Digital Gene Expression Profile,DGE)等。OTD瀏覽器以可視化方式顯示轉錄本的組裝,轉錄本在基因組上的定位、表達譜及轉錄本在基因組特定位置覆蓋度等信息。該數據庫提供多種檢索方式,可利用EST序列和重疊群ID號、關鍵詞、表達量等進行檢索。來自H.arabidopsidis的37492 ESTs通過聚類形成Unigenes,并利用BLAST、InterProScan、TMHMM、TargetP和SignalP進行了注釋。EST序列可從該數據庫下載。OTD提供與VMD、PTD數據庫的鏈接界面。疫霉轉錄組學數據庫(Phytophthora transcriptomics database,PTD http:∥phy.njau.edu.cn/ptd)提供大豆疫霉的數字基因表達譜信息[18],可通過基因ID、關鍵詞進行檢索,利用序列比對BLAST搜索同源基因,可查看不同發育階段的差異表達基因。基于轉錄信息的基因研究是功能基因組學研究的重要策略,例如EST數據不僅為基因的功能研究提供有價值的表達信息,而且基于EST的電子基因克隆技術也可用來發現新基因。近年來,二代測序技術產生的轉錄組序列為基因功能研究提供了更為有利的工具,例如RNA-Seq產生的轉錄本信息可以更為有效地發現未知轉錄本和稀有轉錄本,提供轉錄本的結構和表達水平信息,用于精確地識別可變剪切位點以及cSNP(編碼序列單核苷酸多態性)[19]。
2.2 卵菌綜合性功能基因組資源
綜合性疫霉病原菌基因組學資源(Comprehensive Phytopathogen Genomics Resource,CPGR)包括4個數據庫:基因組倉庫、注釋數據庫、轉錄物組裝和rDNA數據庫[20]。基因組倉庫儲存包括植物病原菌基因組及EST測序計劃信息,每年至少更新2次。注釋數據庫包含基因組注釋信息,包括物種名、所屬類群、引起的疾病、NCBI序列登錄號、基因組大小、測序計劃狀態及機構、特征、相關注釋以及文獻信息等。數據庫頁面包含依據分類單元和測序狀態的過濾器功能。轉錄物組裝數據來自NCBI數據庫的EST和mRNA,去除低重復和污染序列后,經拼接注釋而成。CPGR的轉錄物組裝和來自GenBank的序列可在其FTP下載。rDNA數據庫包括植物病原菌的名稱和分類單元標識符,另外該數據庫在病原菌和植物病害之間做了超鏈接。CPGR的搜索工具允許用戶使用序列和功能注釋搜索該數據庫。卵菌注釋可以通過位點標識符、功能、Pfam功能域、Interpro功能域搜索。對于已測序的卵菌,用戶可在CPGR網站利用其提供的一系列界面實現對基因組信息(序列和注釋信息)的瀏覽、下載和檢索。目前只有P.infestans T30-4和Pythium ultimum DAOM BR144可利 用 CPGR 的 genome browser進行可視化瀏覽,包括等位基因、基因模式(gene models)、rRNA 和tRNA 基因、推測的簡單重復序列SSRs(putative simple sequence repeats)、GC 含 量 (GC content)和 六 框 翻 譯 (sixframe translation)。位點信息和基因模式與其他內容形成超鏈接。基因組瀏覽器還包括基因列表(gene list)、RNA 基因列表(RNA gene list)、Pfam功能域列表、Interpro功能域列表、推測SSRs,縮放工具允許用戶在各個分辨率水平瀏覽基因組。主頁的resource項下包含的簡單重復序列標記搜索工具(SSR Candidate Marker Search Tool)可以用于對提交的序列進行SSR搜索,并利用PRIMER3搜索合適的擴增引物。用戶可自行設定SSR類型和重復數目。SSRs廣泛存在于各類生物基因組中,是應用較為廣泛的遺傳標記[21-22]。在基因組序列水平上對SSR的系統分析是SSR分子標記的基礎性工作[23-24]。我 們 利 用 CPGR 數 據 庫 的 SSR 數 據 對P.infestans與Pythium ultimum 基因組內的SSR進行了比較分析。P.infestans包含1958個SSR,平均每122.5kb有一個SSR,Pythium ultimum 包含1911個SSR,平均每22.39kb有一個SSR,兩基因組內均以二、三、六堿基重復為最豐富,在基序的重復次數上也具有一定的相似性。在二、三、六堿基重復中,每種都存在優勢基序,詳見表2。在P.infestans基因組中,二、三、六堿基重復分別占總SSR的26.3%,21.81%和35.44%,在 Pythium ultimum中它們所占的百分比分別為27.68%,26.84%和27.42%,其他堿基重復所占的比例很少。在兩基因組二、三堿基重復的優勢基序中,大部分是相同的優勢基序類型,但是六堿基重復的優勢基序相同的比較少,而且,六堿基重復的基序類型分布也比較分散。但是兩基因組的重復序列的長度都在20bp左右,長序列較少。而且有些基序類型沒有出現。由以上分析可以看出,兩個卵菌基因組內的SSR數目相差不多,但由于基因組大小差異導致SSR在基因組內的密度存在差異。優勢堿基重復單元集中在二、三、六,說明其遺傳變異速度中等。SSR長度比較集中。基因組水平上的SSR分析為在以后的研究中應用SSR標記提供了有用的信息。由于SSR標記在已測序卵菌基因組內的位置及側翼序列是已知的,所以可以快速、準確地找到連鎖的基因位點,從而完成候選基因的篩查、鑒定、基因注釋及功能研究,SSR標記將在卵菌功能基因組研究中發揮重要作用。
CFGP(Comparative Fungal Genomics Platform)是一個綜合性的真菌比較基因組學平臺,包含283個真菌基因組的數據信息(6個卵菌)、專門數據庫的超鏈接和各類比較基因組分析工具,包括BLAST、ClustalW、InterProScan、SignalP等[25]。平臺采用數據驅動的用戶界面(Data-driven User Interface DUI),用戶可實現數據瀏覽,選擇和分析的連續進行,節省收集數據、轉化數據格式、提交數據、不同數據庫間瀏覽查詢的時間,極大地方便了大量數據的分析。該平臺的數據查詢主要是通過頁面的SEQUENCE菜單實現,有10種查詢方式:Taxonomy、Contig、Genome reference、MyGene、SWISSprot、MSIPI、NR、PDB、PDBchain、SequenceSet browser。數據通過 SNUGB(Seoul National University Genome Browser)以可視化方式顯示,并可以選擇顯示不同的數據庫信息。查詢到的序列通過勾選進入到Favorites功能框架。Favorites作為生物信息分析的工作界面,包括Edit、Function、Anal-ysis和Download 4項功能,每個功能分若干項(見圖2)。其中的Function包括BLAST、BLASTmatrix等27種分析工具,是主要的分析界面,可用于序列比對分析、功能結構域分析查詢、系統進化分析、分泌蛋白分析、亞細胞定位、跨膜螺旋預測、RNA二級結構預測、翻譯后修飾和保守結構域搜索。選擇一種工具后,CFGP即通過PERL模塊實現與相應程序的鏈接,設定參數即可運行獲得結果。分析結果保存在History中。除了查看自己的分析結果,在History中也可查看其他人在CFGP分析的結果。在分析工具中,值得一提的是BLASTMatrix工具,它用于在多個不同真菌物種中搜索潛在的同源基因。BLASTMatrix結果提供提交序列在每個物種最佳命中序列的列表,該列表以每個物種的分類地位組織在一起,同時會提供在不同分類群組內同源基因的分布模式圖。輸出結果還包括InterPro或GO術語,可以幫助用戶預測可能的基因功能,進一步分析確定其直系同源關系。
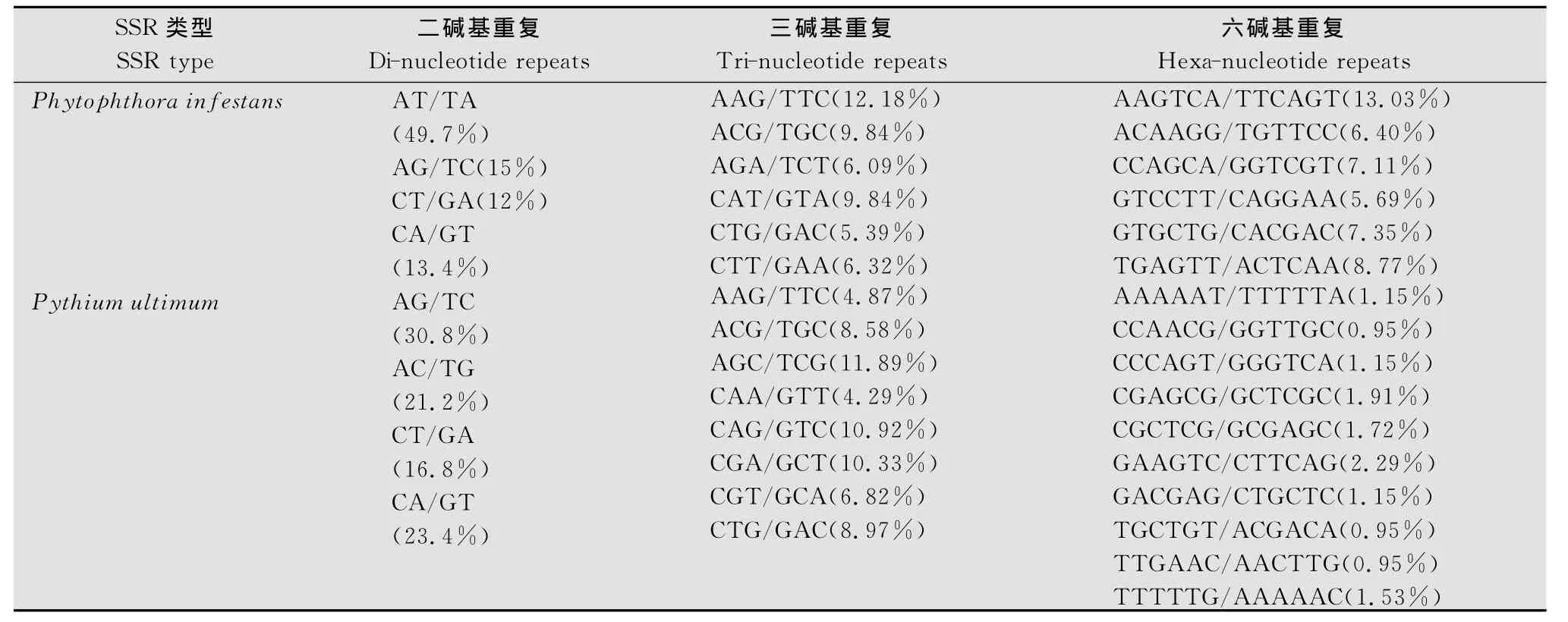
表2 P.infestans與Pythium ultimum基因組內SSR二、三、六堿基重復優勢基序Tabel 2 Major motifs of di-,tri-and hexa-nucleotide repeats in genome of P.infestans and Pythium ultimum

圖2 CFGP網站的Favorites工作界面Fig.2 The favorites interface in CFGP
FungiDB真菌功能基因組學資源,包括33種真菌和6種卵菌的基因組信息(V 2.1),整合了基因組序列和注釋信息,可開展比較基因組學研究、基因表達分析、生物信息學分析和數據挖掘等[26]。FungiDB提供利用多種策略在選定的單個或多個物種中進行基因、ESTs、ORF、基因組序列等的快速檢索,可實現多步檢索策略的交叉、合并和刪除,創建用戶自己的檢索策略進行數據分析。同時提供包括BLAST、序列檢索(Sequence Retrieval)、文獻檢索(PubMed and Entrez)等分析工具。
2.3 卵菌專門數據庫資源
除了綜合性資源外,一些專門數據庫也是卵菌功能基因組學研究的重要資源。專門數據庫是針對特定目標由一級數據庫衍生而來,對生物學知識和信息進一步整理形成的二級數據庫,例如真菌分泌體數據庫FSD,專門存儲那些含有信號肽、在高爾基體或內質網進行加工能夠分泌到細胞外的蛋白,這些蛋白通過在全基因組水平進行生物信息學分析確定,該數據庫中可以查詢到6種已測序卵菌的所有預測獲得的分泌體蛋白[27]。另外,真菌的轉錄因子數據庫FTFD[28]、真菌細胞色素 P450數據庫 FCPD[29]等均存儲有卵菌的相應蛋白的信息。這些專門數據庫可用于對于特定基因或領域的研究。
3 總結
基因組學極大地提高了我們對于植物病原菌的理解,例如卵菌病原菌的大量測序揭示了調控宿主與寄生物相互作用的效應物分子類型[4,30-31]。通過在全基因組水平上對數據信息的挖掘,尤其是比較基因組學研究,將對揭示卵菌的特異性、病原菌群體結構、卵菌與病害關系、發現病原菌診斷標記起到重要作用[32]。隨著測序方法的發展,數據產生規模的提高,對數據的處理和挖掘已經成為研究者的新挑戰。
[1] Erwin D C,Riberro O K.Phytophthora diseases worldwide[M].St Paul:APS Press,1996:200-562.
[2] 鄭小波.疫霉菌及其研究技術[M].北京:中國農業出版社,1997:1-29.
[3] Baldauf S L,Roger A J,Wenk-Siefert I,et al.A kingdom-level phylogeny of eukaryotes based on combined protein data[J].Science,2000,290(5493):972-977.
[4] Tyler B M,Tripathy S,Zhang X,et al.Phytophthora genome sequences uncover evolutionary origins and mechanisms of pathogenesis[J].Science,2006,313(5791):1261-1266.
[5] Haas B J,Kamoun S,Zody M C,et al.Genome sequence and analysis of the Irish potato famine pathogen Phytophthora infestans[J].Nature,2009,461(7262):393-398.
[6] Lamour K H,Mudge J,Gobena D,et al.Genome sequencing and mapping reveal loss of heterozygosity as a mechanism for rapid adaptation in the vegetable pathogen Phytophthora capsici[J] Molecular Plant-Microbe Interactions,2012,25(10):1350-1360.
[7] Lévesque C A,Brouwer H,Cano L,et al.Genome sequence of the necrotrophic plant pathogen Pythium ultimumreveals original pathogenicity mechanisms and effector repertoire[J].Genome Biology,2010,11(7):R73-R94.
[8] Baxter L,Tripathy S,Ishaque N,et al.Signatures of adaptation to obligate biotrophy in the Hyaloperonospora arabidopsidis genome[J].Science,2010,330(6010):1549-1551.
[9] Tian M,Win J,Savory E,et al.454genome sequencing of Pseudoperonospora cubensis reveals effector proteins with a putative QXLR translocation motif[J].Molecular Plant-Microbe Interactions,2011,24(5):543-553.
[10]Lamour K H,Kamoun S.Oomycete genetics and genomics:Diversity,interactions and research tools[M].Hoboken,USA:Wiley-Blackwell Press,2009:540-582.
[11]Richards T A,Dacks J B,Jenkinson J M,et al.Evolution of filamentous plant pathogens:Gene exchange across eukaryotic kingdoms[J].Current Biology,2006,16(18):1857-1864.
[12]Kemen E,Gardiner A,Schultz-Larsen T,et al.Gene gain and loss during evolution of obligate parasitism in the white rust pathogen of Arabidopsis thaliana[J].PLoS Biology,2011,9(7):e1001094.
[13]Judelson H S.Dynamics and innovations within Oomycete genomes:Insights into biology,pathology,and evolution[J].Eukaryot Cell,2012,11(11):1304-1312.
[14]Grigoriev I V,Nordberg H,Shabalov I,et al.The genome portal of the department of Energy Joint Genome Institute[J].Nucleic Acids Research,2012,40(Database issue):D26-D32.
[15]Tripathy S,Pandey V N,Fang B,et al.VMD:A community annotation database for oomycetes and microbial genomes[J].Nucleic Acids Research,2006,34(Database issue):D379-D381.
[16]Links M G,Holub E,Jiang R H,et al.De novo sequence assembly of Albugo candida reveals a small genome relative to other biotrophic oomycetes[J].BMC Genomics,2011,12:503-514.
[17]Tripathy S,Deo T,Tyler B M.Oomycete transcriptomics database:A resource for oomycete transcriptomes[J].BMC Genomics,2012,13(1):303-316.
[18]Ye W,Wang X,Tao K,et al.Digital gene expression profiling of the Phytophthora sojae transcriptome[J].Molecular Plant-Microbe Interactions,2011,24(12):1530-1539.
[19]祁云霞,劉永斌,榮威恒.轉錄組研究新技術:RNA-Seq及其應用[J].遺傳,2011,33(11):1191-1202.
[20]Hamilton J P,Neeno-Eckwall E C,Adhikari B N,et al.The comprehensive phytopathogen genomics resource:A webbased resource for data-mining plant pathogen genomes[J].Database:The Journal of Biological Databases and Curation,2011:bar53-65.
[21]Brurberg M B,Elameen A,Le V H,et al.Genetic analysis of Phytophthora infestans populations in the Nordic European countries reveals high genetic variability[J].Fungal Biology,2011,115(4-5):335-342.
[22]Vercauteren A,Larsen M,Goss E,et al.Identification of new polymorphic microsatellite markers in the NA1and NA2lineages of Phytophthora ramorum[J].Mycologia,2011,103(6):1245-1249.
[23]Schena L,Cardle L,Cooke D E.Use of genome sequence data in the design and testing of SSR markers for Phytophthoraspecies[J].BMC Genomics,2008,9:620-642.
[24]Garnica D P,Pinzón A M,Quesada-Ocampo L M,et al.Survey and analysis of microsatellites from transcript sequences in Phytophthoraspecies:Frequency,distribution,and potential as markers for the genus[J].BMC Genomics,2006,7:245-255.
[25]Park J,Park B,Jung K,et al.CFGP:A web-based,comparative fungal genomics platform[J].Nucleic Acids Research,2008,36(Database issue):D562-D571.
[26]Stajich J E,Harris T,Brunk B P,et al.FungiDB:An integrated functional genomics database for fungi[J].Nucleic Acids Research,2012,40(Database issue):D675-D681.
[27]Choi J,Park J,Kim D,et al.Fungal Secretome Database:Integrated platform for annotation of fungal secretomes[J].BMC Genomics,2010,11:105-119.
[28]Park J,Park J,Jang S,et al.FTFD:An informatics pipeline supporting phylogenomic analysis of fungal transcription factors[J].Bioinformatics,2008,24(7):1024-1025.
[29]Park J,Lee S,Choi J,et al.Fungal cytochrome P450database[J].BMC Genomics,2008,9:402-412.
[30]Win J,Kamoun S.Adaptive evolution has targeted the C-terminal domain of the RXLR effectors of plant pathogenic oomycetes[J].Plant Signal Behavior,2008,3(4):251-253.
[31]Savory E A,Zou C,Adhikari B N,et al.Alternative splicing of a multi-drug transporter from Pseudoperonospora cubensis generates an RXLR effector protein that elicits a rapid cell death[J].PLoS One,2012,7(4):e34701-e34713.
[32]Seidl M F,Van den Ackerveken G,Govers F,et al.A domain-centric analysis of oomycete plant pathogen genomes reveals unique protein organization[J].Plant Physiology,2011,155(2):628-644.

