銀杏4-香豆酸輔酶 A 連接酶基因的克隆與序列分析
雷靜,許鋒,王曉輝,張威威,廖詠玲
(長(zhǎng)江大學(xué)園藝園林學(xué)院,湖北 荊州434025)
銀杏4-香豆酸輔酶 A 連接酶基因的克隆與序列分析
雷靜,許鋒,王曉輝,張威威,廖詠玲
(長(zhǎng)江大學(xué)園藝園林學(xué)院,湖北 荊州434025)
[摘要]根據(jù)銀杏(Ginkgo biloba L.)轉(zhuǎn)錄組中的基因序列設(shè)計(jì)引物,從銀杏中克隆到了4-香豆酸輔酶A連接酶(4-coumarate:CoA ligase,4CL)的cDNA片段,命名為Gb4CL,GenBank 登錄號(hào)為KU820947。Gb4CL全長(zhǎng)1736bp,含有1個(gè)1671bp的ORF,編碼557個(gè)氨基酸。核苷酸和蛋白質(zhì)序列多重比較結(jié)果顯示,Gb4CL與其他植物的4CL基因的核苷酸與蛋白質(zhì)序列均高度同源。Gb4CL編碼的蛋白質(zhì)與日本柳杉(Cryptomeria japonica)、白豆杉(Pseudotaxus chienii)、北美云杉(Picea sitchensis)的4CL氨基酸同源性分別為82%、83%、80%。4CL系統(tǒng)進(jìn)化樹(shù)顯示,Gb4CL與裸子植物親緣關(guān)系最近。該研究通過(guò)克隆Gb4CL基因,并進(jìn)行相關(guān)的生物信息學(xué)分析,可為掌握銀杏木質(zhì)素生物合成中關(guān)鍵基因的調(diào)控機(jī)理提供參考。
[關(guān)鍵詞]銀杏(Ginkgo biloba L.);4CL;基因克隆;序列分析
銀杏(GinkgobilobaL.)是我國(guó)特產(chǎn)的古老珍貴樹(shù)種,具有極高的經(jīng)濟(jì)、生態(tài)、觀賞和科研價(jià)值,其藥用價(jià)值也已受到世界范圍內(nèi)研究者廣泛關(guān)注。銀杏葉片主要含有2種活性成分——黃酮類(lèi)化合物(Flavonoids)和萜內(nèi)酯(銀杏內(nèi)酯 Ginkgolides)。其中木質(zhì)素合成涉及到的重要次生代謝途徑,即苯丙氨酸代謝途徑(phenylpropanoid pathway)中生成的如香豆素、黃酮醇、木質(zhì)素、軟木酷及其他的苯類(lèi)化合物,對(duì)植物維持細(xì)胞壁結(jié)構(gòu)、抗病害、抗紫外線損傷、作為花粉發(fā)育和植物與微生物相互作用的信號(hào)分子等生長(zhǎng)與發(fā)育過(guò)程作用顯著[1,2]。同時(shí)在人類(lèi)生活中這類(lèi)次生代謝產(chǎn)物還可作為藥物、食品添加劑、芳香劑、染料等,具有極大的經(jīng)濟(jì)和社會(huì)價(jià)值。因此利用基因工程手段研究改造相關(guān)基因次生代謝產(chǎn)物的合成具有重大的實(shí)際意義。
4-香豆酸輔酶 A 連接酶(4-coumarate:CoA ligase,4CL)是苯丙氨酸途徑中的關(guān)鍵性限速酶,作用于苯丙酸途徑中最后一步反應(yīng),分別催化p-香豆酸、咖啡酸、阿魏酸和芥子酸生成相應(yīng)的輔酶A(CoA)酯,這些硫酯處于苯丙酸代謝途徑和各種末端產(chǎn)物特異合成途徑的分支點(diǎn),其中生成的香豆酰CoA、阿魏酰CoA 及芥子酰CoA 轉(zhuǎn)化為肉桂醇衍生物后,通過(guò)還原反應(yīng)生成木質(zhì)素單體[3]。人們對(duì)4CL有較為明確的認(rèn)識(shí)始自4CL基因的克隆。迄今已從多種植物中分離到編碼4CL的基因,如歐芹(Petroselinumcrispum)[4]、馬鈴薯(Solanumtuberosum)[5]、火炬松(Pinustaeda)[6]、煙草(Nicotianatabacum)[7]、大豆(Glycinemax)[8]、擬南芥(Arabidopsisthaliana)[9]、花楸(Sorbusaucuparia)[10]、小立碗蘚(Physcomitrellapatens)[11]、鈍鯪紫背苔(Plagiochasmaappendiculatum)[12]等。而有關(guān)銀杏4CL基因克隆的研究尚未見(jiàn)報(bào)道。為此,本研究以銀杏為材料,對(duì)其4CL基因進(jìn)行克隆,并做相關(guān)核苷酸、蛋白質(zhì)、進(jìn)化樹(shù)分析研究,以期為進(jìn)一步研究銀杏4CL基因的功能提供參考。
1材料與方法
1.1材料
銀杏取自長(zhǎng)江大學(xué)銀杏科技園,品種為家佛手,取十五年生銀杏的葉,采集后液氮速凍存放于-80℃冰箱中。
實(shí)驗(yàn)所用大腸桿菌DH5α為長(zhǎng)江大學(xué)園藝園林學(xué)院園藝生物技術(shù)實(shí)驗(yàn)室保存,pMD18-T vector kit購(gòu)自香港Invitrogen公司,AMV反轉(zhuǎn)錄酶、dNTPs、RNasin和TaqDNA聚合酶購(gòu)自美國(guó)Promega(Madison,WI,USA)公司。引物合成及序列測(cè)定由上海生工生物工程技術(shù)服務(wù)有限公司(Shanghai Sangon Biotechnology Company China)完成。
1.2方法
1.2.1總 RNA 的提取
按照蔡榮等[13]的方法提取銀杏葉的總RNA,利用瓊脂糖凝膠電泳和分光光度計(jì)分析總RNA 的純度和濃度,保存于-80℃冰箱中備用。
1.2.2銀杏4CL基因cDNA的克隆
取銀杏葉總RNA1μg用于cDNA第一鏈的合成,具體操作按照AMV Reverse Transcriptase kit說(shuō)明書(shū)。根據(jù)銀杏轉(zhuǎn)錄組中4CL基因序列設(shè)計(jì)引物,上游引物Gb4CLup:5’-ATGGCTCTTATTGCGCCTTCT-3’;下游引物Gb4CLdown:5’-GCATTTGTGACGCACGAGAA-3’,以合成的cDNA第一鏈為模板,擴(kuò)增得到銀杏4CL基因開(kāi)放閱讀框(ORF)序列。反應(yīng)程序?yàn)椋?4℃預(yù)變性4min;94℃變性30s,55℃退火30s,72℃延伸90s,共32個(gè)循環(huán);最后于72℃下延伸10min。1%瓊脂糖凝膠電泳檢測(cè) PCR 產(chǎn)物,并用高純度 PCR 產(chǎn)物純化試劑盒回收 PCR 產(chǎn)物。按照pMD18-T 載體試劑盒說(shuō)明書(shū),將回收片段與pMD18-T 載體連接,轉(zhuǎn)化大腸桿菌DH5α菌株,選取陽(yáng)性克隆提取質(zhì)粒DNA,經(jīng)酶切鑒定后測(cè)序。
1.2.3生物信息學(xué)分析

M.DL2000 DNA Marker;1.Gb4CL基因PCR擴(kuò)增產(chǎn)物圖1 Gb4CL基因片段PCR擴(kuò)增圖
Gb4CL基因cDNA序列的ORF查找及翻譯借助DNAMAN 6.0和Vector NTI 10.0完成,核酸和蛋白質(zhì)同源性分析在NCBI(http://www.ncbi.nlm.nih.gov/BLAST/)上用BLAST 完成。然后利用Vector NTI 10.0完成4CL氨基酸序列比對(duì),通過(guò)Clustal X1.83和MEGA 4.0 構(gòu)建4CL基因的分子進(jìn)化樹(shù),并進(jìn)行Bootstrap檢測(cè)。
2結(jié)果與分析
2.1Gb4CL 基因cDNA克隆及其核苷酸序列分析
以合成的銀杏cDNA第一條鏈為模板,利用Gb4CLup和Gb4CLdown引物組合,通過(guò)RT-PCR方法克隆得到的銀杏4CL基因cDNA片段,命名為Gb4CL,GenBank 登錄號(hào)為KU820947,PCR擴(kuò)增電泳結(jié)果見(jiàn)圖1。該片段克隆測(cè)序全長(zhǎng)為1736bp,ORF有1671bp,編碼557個(gè)氨基酸。核苷酸序列比對(duì)顯示,該片段與其他植物4CL基因序列相似性大于70%(表1),如與芝麻(Sesamumindicum)4CL的同源性為73%,與馬鈴薯(Solanumtubero-

表1 銀杏4CL基因與其他植物4CL基因核苷酸序列同源性比較
sum)、番茄(Solanumpennellii)、潘那利番茄(Solanumlycopersicum) 4CL的同源性均為70%。因此,可以初步推測(cè)該片段為銀杏4CL基因家族成員之一。
2.2Gb4CL 蛋白質(zhì)分析
根據(jù)Gb4CL核苷酸序列的ORF推測(cè)的4CL氨基酸序列結(jié)果見(jiàn)圖2。利用 Computer pI/Mw軟件分析推Gb4CL蛋白質(zhì)等電點(diǎn)和分子量分別為 5.62和60ku,與所報(bào)道的其他植物的4CL蛋白質(zhì)性質(zhì)相似。利用Vector NTI 10.0對(duì)Gb4CL蛋白質(zhì)序列與其他植物4CL蛋白質(zhì)序列進(jìn)行比較。Gb4CL多肽與其他植物4CL氨基酸序列之間的相似性大于70%(圖3),與同為裸子植物的日本柳杉(Cryptomeriajaponica,AFJ73433.1)、白豆杉(Pseudotaxuschienii,AFJ73459.1)、北美云杉(Piceasitchensis,ABR17998.1)的同源性分別為82%、83%、80%,與錘枝樺(Betulapendula,AIR95613.1)和可可(Theobromacacao,XP_007014191.1)的同源性為71%,與土肉桂(Cinnamomumosmophloeum,AFG26323.1)、水曲柳(Fraxinusmandshurica,AHL44986.1)和甜椒(Capsicumannuum,ACF17632.1)的同源性為70%,說(shuō)明 Gb4CL與其他植物中4CL蛋白質(zhì)的序列和功能極為相似。
Gb4CL序列中也具有完整保守的功能結(jié)構(gòu)域(motif),如圖3中肽基序BOXI在4CL蛋白序列中幾乎絕對(duì)保守,被認(rèn)為是4CL催化反應(yīng)中保守的AMP結(jié)合功能域,負(fù)責(zé)催化木質(zhì)素合成途徑中4-香豆酸和輔酶A的連接,而且與熒光素酶、長(zhǎng)鏈脂肪酰基2CoA合成酶、肽合成酶中發(fā)現(xiàn)的保守基序相似,也是腺苷酸形成酶超家族(the superfamily of adenylate-forming enzymes)的分類(lèi)依據(jù)之一[14]。肽基序BOXII在所有 4CL 中絕對(duì)保守,其中甘氨酸Gly(G)、谷氨酸Glu(E)、半胱氨酸Cys(C)是最為保守的氨基酸位點(diǎn),且中心的 C 殘基被認(rèn)為直接參與催化進(jìn)程[15]。這與黃勝雄等[16]的研究相一致。

方框中為起始子和終止子,下劃線為特異引物Gb4Clup和Gb4Cldown圖2 Gb4CL基因核酸序列及其所推導(dǎo)的氨基酸序列
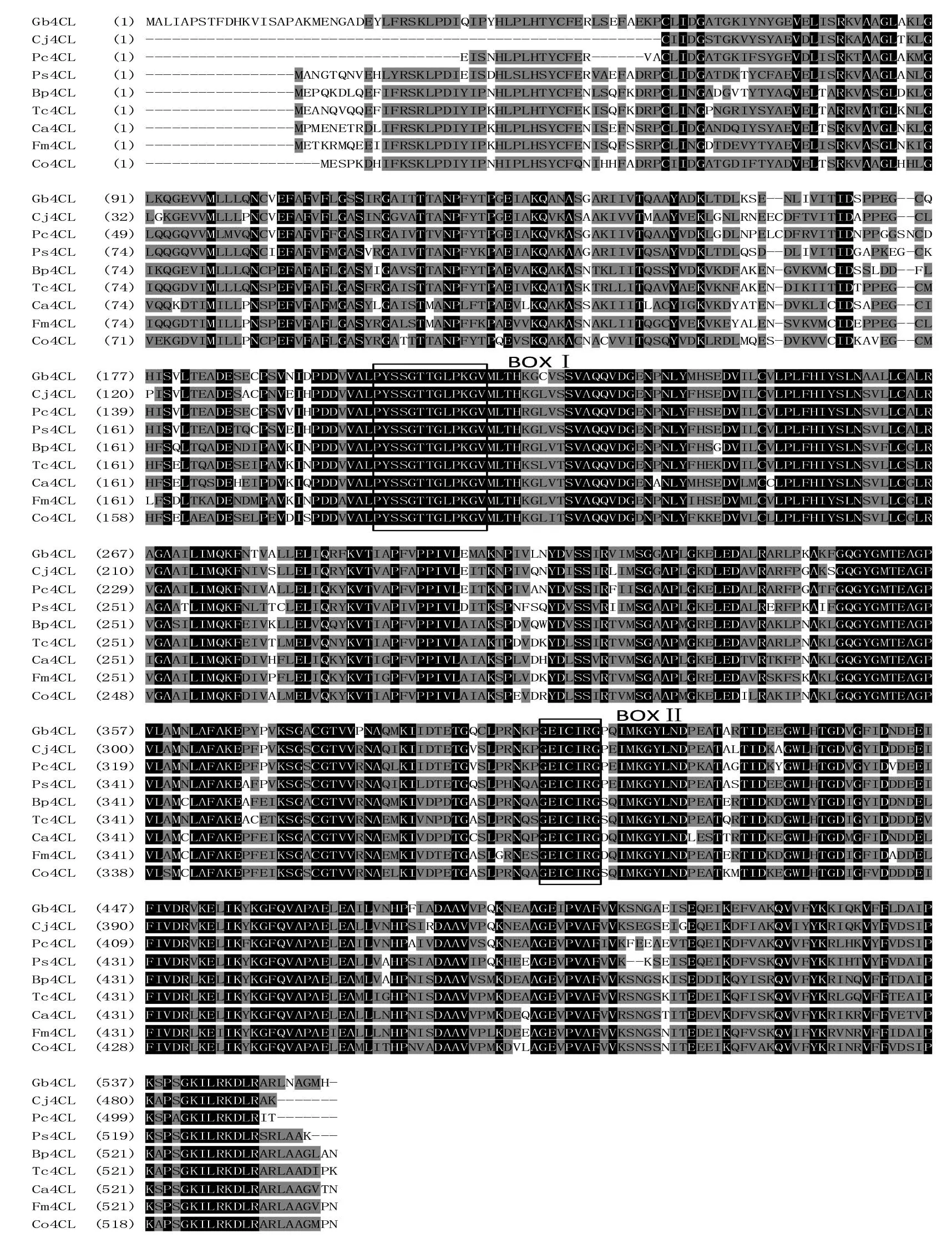
氨基酸完全一致的序列用黑底白字表示,完全不相似氨基酸序列用白底黑字表示,部分相似的氨基酸序列用灰底黑字表示。BOX I表示保守的AMP結(jié)合功能域;BOX II表示GEICIRG保守區(qū)。蛋白質(zhì)簡(jiǎn)稱(chēng)、植物學(xué)名及GenBank登錄號(hào)如下:Cj4CL日本柳杉(Cryptomeria japonica),AFJ73433.1;Pc4CL白豆杉(Pseudotaxus chienii),AFJ73459.1;Ps4CL北美云杉(Picea sitchensis),ABR17998.1;Bp4CL錘枝樺(Betula pendula),AIR95613.1;Tc4CL可可(Theobroma cacao),XP_007014191.1;Ca4CL甜椒(Capsicum annuum),ACF17632.1;Fm4CL水曲柳(Fraxinus mandshurica),AHL44986.1;Co4CL土肉桂(Cinnamomum osmophloeum),AFG26323.1圖3 Gb4CL蛋白質(zhì)與其他植物4CL蛋白質(zhì)氨基酸序列的多重比較
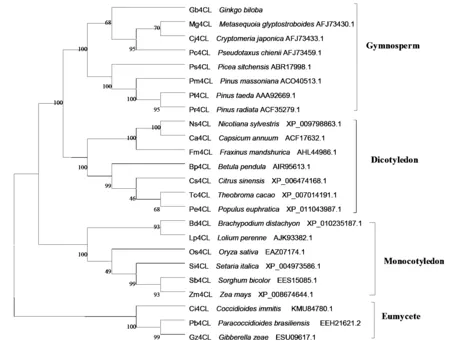
圖4 Gb4CL蛋白與其他植物4CL蛋白氨基酸序列的系統(tǒng)進(jìn)化樹(shù)
2.3Gb4CL 分子進(jìn)化分析
利用軟件 Clustal x 1.83 和 MEGA 4.0通過(guò) Neighbor-joining(NJ)方法構(gòu)建了Gb4CL 的系統(tǒng)進(jìn)化樹(shù)(圖4)。分析表明:在裸子植物(Gymnosperm)、單子葉植物(Monocotyledon)、雙子葉植物(Dicotyledon)和真菌(Eumycete)中4CL都有相同的進(jìn)化起源,4CL基因家族在進(jìn)化上存在一定的保守性,銀杏Gb4CL蛋白與同一分類(lèi)中的水杉(Metasequoiaglyptostroboides,AFJ73430.1)、白豆杉(Pseudotaxuschienii,AFJ73459.1)、日本柳杉(Cryptomeriajaponica,AFJ73433.1)的親緣性最近,與同一分類(lèi)中的其他松科植物北美云杉(Piceasitchensis,ABR17998.1)、馬尾松(Pinusmassoniana,ACO40513.1)、火炬松(Pinustaeda,AAA92669.1)、輻射松(Pinusradiata,ACF35279.1)同源性也達(dá)到80%,在進(jìn)化距離上較單子葉植物而言,裸子植物4CL與雙子葉植物親緣關(guān)系更近,處于同一分支上,與真菌類(lèi)親緣關(guān)系最遠(yuǎn),這表明在裸子植物和被子植物分化之前這些4CL基因就已經(jīng)存在于植物中,在植物中的進(jìn)化時(shí)間超前于裸子植物和被子植物分化的時(shí)間。
3小結(jié)與討論
本研究首次從銀杏中克隆得到其4CL基因,并將其命名為Gb4CL,利用生物信息學(xué)軟件進(jìn)行多序列比對(duì)分析,結(jié)果顯示Gb4CL與其他植物已分離的4CL基因有較高的同源性,并含有共同的功能結(jié)構(gòu)域BOXI(PYSSGTTGLPKLGV)和BOX II(GEICIRG)。4CL基因在植物中多是以基因家族的形式存在的,目前發(fā)現(xiàn)的4CL基因可分為2類(lèi):Ⅰ類(lèi)的4CLs主要與木質(zhì)素的生物合成有關(guān),Ⅱ類(lèi)的4CLs主要調(diào)控類(lèi)黃酮的生物合成[17]。目前已有多項(xiàng)研究顯示通過(guò)抑制4CL基因活性可以降低植物中木質(zhì)素含量,4CL基因的過(guò)量表達(dá)可以增加木質(zhì)素的含量,進(jìn)而增強(qiáng)植物抗病性和抗倒伏能力[18~20],而對(duì)4CL基因的正向或負(fù)向調(diào)控可能僅僅只是影響了木質(zhì)素的合成,對(duì)苯丙氨酸途徑中其他次生代謝產(chǎn)物的合成影響不大,不干擾植物的正常生長(zhǎng)發(fā)育[19,21]。開(kāi)展植物木質(zhì)素生物合成途徑的研究,不僅是在模式植物,而且在一些木本植物如銀杏中同樣有利于更好地揭示植物次生代謝途徑在木質(zhì)素積累中的調(diào)控作用。由于銀杏具有極大的生物效能,因此進(jìn)行銀杏次生代謝過(guò)程中相關(guān)基因的克隆和鑒定對(duì)其生物工程改良具有很大的推動(dòng)作用。
[參考文獻(xiàn)]
[1]Fukasawa-Akada T,Kung S,Watson J C.Phenylalanineammonia-lyasegene structure,expression,andevolution inNicotiana[J].Plant Mol Biol,1996,30:711~722.
[2]Zhong R,Morrison W H,Himmelsbach D S,etal.Essential role of caffeoyl Co-enzyme A O-methyltransferase in lignin biosynthesis in woody poplar plants[J].Plant Physiol,2000,124:563~578.
[3]Whetten R,Sederoff R.Lignin biosynthesis[J].Plant Cell,1995,7:1001~1013.
[4]Neutaedter D A,Lee S P,Douglas C J.A novel parsley 4CL1 cis-element is required for developmentally regulated expression and protein-DNA complex formation[J].Plant J,1999,18:77~88.
[5]Becker-André M,Schulze-Lefert P,Hahlbrock K.Structural comparison,modes of expression,and putative cis-acting elements of the two 4-coumarate:CoA ligase genes inpotato[J].J Biol Chem,1991,266:8551~8559.
[6]Zhang X,Chiang V.Molecular cloning of 4-coumarate:coenzyme A ligase inloblollypineand the roles of thisenzyme in the biosynthesis of lignin in compression wood[J].Plant Physiol,1997,113:65~74.
[7]Lee D,Douglas C J.Two divergent members of a tobacco4-coumarate:coenzyme A ligase (4CL) gene family[J].Plant Physiol,1996,112:193~205.
[8]Lindermayr C,M?llers B,Fliegmannm J,etal.Divergent members of asoybean (GlycinemaxL.) 4-coumarate:coenzyme A ligasegene family:Primary structures,catalytic properties,and differential expression[J].Eur J Biochem,2002,269:1304~1315.
[9]Yi Li,Kim J I,Pysh L,etal.Four isoforms ofArabidopsisthaliana4-coumarate:CoA ligase (4CL) haveoverlapping yet distinct roles in phenylpropanoid metabolism[J].Plant Physiol,2015,10:1~37.
[10]Gaid M M,Scharnhop H,Ramadan Hn,etal.4-Coumarate:CoA ligase family members from elicitor-treatedSorbusaucupariacell cultures[J].J Plant Physiol,2011,168:944~951.
[11]Silber M V,Meimberg H,Ebela J.Identification of a 4-coumarate:CoA ligase gene family in the moss,Physcomitrellapatens[J].Phytochemistry,2008,69:2449~2456.
[12]Shuai G,Hai N,Rui X,etal.Cloning and functional characterization of a 4-coumarate CoA ligasefrom liverwortPlagiochasmaappendiculatum[J].Phytochemistry,2015,111:48~58.
[13]蔡榮,許鋒,陳柳吉,等.銀杏不同組織的總RNA提取方法的改進(jìn)[J].生物技術(shù),2007,17(4):38~41.
[14]Fulda M,Heinz E,Wolter F P.The fadD gene ofEscherichiacoliK12 is located close tornd at 39.6 min of the chromosomal mapand is a new member of the AMP-binding protein family[J].Mol Gen Genet,1994,242:241~249.
[15]Stuible H,Kombrink E.Identification of the substrate specificity-conferring amino acid residues of 4-coumarate:Coenzyme A ligase allowsthe rational design of mutant enzymes with new catalytic properties[J].J Biol Chem,2001,276:26893~26897.
[16]黃勝雄,胡尚連,孫霞,等.木質(zhì)素生物合成酶4CL基因的遺傳進(jìn)化分析[J].西北農(nóng)林科技大學(xué)學(xué)報(bào)(自然科學(xué)版),2008,36(10):199~206.
[17]Wei X,Wang X.Evolution of 4-coumarate:coenzyme A ligase(4CL) gene and divergence ofLarix(Pinaceae)[J].Mol Phylogenet Evol,2004,31:542~553.
[18]賈彩紅,趙華燕,王宏芝,等.抑制4CL基因表達(dá)獲得低木轉(zhuǎn)基因毛白楊[J].科學(xué)通報(bào),2004,49(7):662~666.
[19]楊向東,王漢中,胡贊民,等.毛白楊4CLcDNA的克隆、表達(dá)及活性分析[J].華中農(nóng)業(yè)大學(xué)學(xué)報(bào),2006,25(2):101~105.
[20]黃杰恒,李威,曲存民,等.甘藍(lán)型油菜不同抗倒性材料中木質(zhì)素代謝途徑關(guān)鍵基因表達(dá)特點(diǎn)[J].作物學(xué)報(bào),2013,39(8):1339~1344.
[21]Hu J,Li G,Struss D,etal.SCAR and RAPD markers associated with 18 carbon fatty acids in rapeseed,Brassicanapus[J].Plant Breed,1999,118:145~150.
[收稿日期]2016-03-03
[基金項(xiàng)目]國(guó)家自然科學(xué)基金項(xiàng)目(31000904)。
[作者簡(jiǎn)介]雷靜 (1989-),女,碩士生,研究方向?yàn)榱帜具z傳育種。通信作者:許鋒,xufeng198@126.com。
[中圖分類(lèi)號(hào)]Q785
[文獻(xiàn)標(biāo)識(shí)碼]A
[文章編號(hào)]1673-1409(2016)15-0042-07
[引著格式]雷靜,許鋒,王曉輝,等.銀杏4-香豆酸輔酶 A 連接酶基因的克隆與序列分析[J].長(zhǎng)江大學(xué)學(xué)報(bào)(自科版) ,2016,13(15):42~48.

