番茄抗病品種吉美08 SlDFR基因的克隆與表達
梁思桃 高雁茹 劉廣清 黃瑞基 劉強 任振新 喬清華




摘要:【目的】克隆番茄(Solanum lycopersicum)抗病品種吉美08二氫黃酮醇4-還原酶(dihydroflavonol 4-reductase,DFR)基因,并分析枯萎病菌尖孢鐮刀菌番茄專化型(Fol4287)誘導下其在番茄不同組織中的表達模式,為深入研究SlDFR基因在番茄抗病過程中的調控機制提供理論依據。【方法】采用同源克隆技術從番茄中克隆SlDFR基因cDNA全長序列,并進行生物信息學分析,采用實時熒光定量PCR(qRT-PCR)檢測番茄根、莖、葉中SlDFR基因在枯萎病菌誘導下的表達模式。【結果】從番茄抗病栽培品種吉美08中克隆得到SlDFR基因,cDNA序列全長1659 bp,包含1個1149 bp的開放閱讀框(ORF),編碼379個氨基酸。SlDFR蛋白的相對分子質量為42.43 kD,等電點(pI)為6.08,是一個親水的、穩定的酸性蛋白,亞細胞定位在高爾基體上,無信號肽和跨膜結構域,有38個磷酸化位點,其中,絲氨酸18個,蘇氨酸15個,酪氨酸5個。SlDFR蛋白的二級結構中α-螺旋占37.73%,延伸鏈占13.98%,無規則卷曲占40.69%。系統發育進化樹分析結果表明,SlDFR蛋白序列與同屬茄科馬鈴薯(Solanum pennellii)親緣關系較近,其次為黑果枸杞(Lycium ruthenicum)。qRT-PCR分析結果顯示,SlDFR基因在番茄葉中表達量最高,在根中表達量最低。SlDFR基因在番茄根、莖、葉中表達量受番茄枯萎病菌誘導,均呈現不同程度上調,其中,在根中表達量變化最大,在葉中表達量變化較小,推測SlDFR基因的表達量與番茄枯萎病菌脅迫響應有關,且番茄根部類黃酮的合成為重要脅迫響應途徑。【結論】SlDFR基因表達量受Fol4287的誘導,可能參與番茄枯萎病脅迫響應過程,且對番茄枯萎病菌的響應在番茄根部更強烈,并通過調控番茄根部黃酮類物質的合成提高根系分泌物的抑菌活性從而增強番茄對枯萎病的抗性。
關鍵詞: 番茄;二氫黃酮醇4-還原酶(DFR);基因克隆;表達分析
中圖分類號: S641.2? ? ? ? ? ? ? ? ? ? ? ? ? ? 文獻標志碼: A 文章編號:2095-1191(2022)03-0813-08
Cloning and expression analysis of SlDFR gene in disease-resistant tomato varieties Jimei 08
LIANG Si-tao, GAO Yan-ru, LIU Guang-qing, HUANG Rui-ji, LIU Qiang,
REN Zhen-xin, QIAO Qing-hua
(College of Biology and Pharmacy, Yulin Normal University, Yulin, Guangxi? 537000, China)
Abstract:【Objective】To clone the tomato dihydroflavonol 4-reductase(DFR) gene of the resistant varieties Jimei 08 and to analyze its expression in different tissues of tomato induced by Fusarium wilt, so as to provide theoretical reference for exploration of the regulation mechanism of SlDFR gene in the process of tomato disease resistance. 【Method】The full-length cDNA sequence of SlDFR gene from tomato was cloned through homologous cloning technology, and bioinformatics analysis was conducted, and real-time fluorescent quantitative PCR was used to detect the expression pattern of SlDFR gene in tomato roots, stems and leaves induced by Fusarium wilt. 【Result】The full-length cDNA of SlDFR was 1659 bp and cDNA contained an open reading frame (ORF) of 1149 bp that encoded 379 amino acids. SIDFR protein had a molecular weight of 42.43 kD and its theoretical isoelectric point(pI) was 6.08, indicating that it was a stable hydrophilic one. And its subcellular localization was on Golgi apparatus without signal peptide and transmembrane domain, with 38 phosphorylation sites, including 18 serine (Ser) phosphate sites, 15 threonine (Thr) phosphate sites and 5 tyrosine (Tyr) phosphate sites. In the secondary structure of SlDFR protein, α-helix accounted for 37.73%, extended chain accounted for 13.98%, and random coil accounted for 40.69%. Phylogenetic analysis showed that tomato DFR was closely related to Solanum pennelli followed by Lycium ruthenicum. The results of real-time fluorescence quantitative PCR showed that the expression of SlDFR gene was the highest in leaves, and lowest in roots. After SlDFR gene expression being induced by Fusarium wilt, the expression of SlDFR gene was up-regulated in varying degrees. The change of expression was the largest in roots and the smallest in leaves, indicating that SlDFR gene was related to the stress response of tomato Fusarium wilt, and the synthesis of flavonoids in roots was an important stress response pathway. 【Conclusion】After SlDFR gene expression being induced by Fol4287, SlDFR gene could participate in the stress response of tomato Fusarium wilt, and the response to Fusarium wilt is stronger in the root, and probably the gene regulates flavonoid synthesis in the root to enhance antibacterial activity of root exudates, thus increasing the resistance of tomato to Fusarium wilt.
Key words: tomato; dihydroflavonol 4-reductase (DFR); gene cloning; expression analysis
Foundation items: Guangxi Natural Science Foundation(2020GXNSFBA297036); Start Up Foundation for Scien-tific Research of High-level Talents of Yulin Normal University(G2020ZK06)
0 引言
【研究意義】番茄(Solanum lycopersicum)營養豐富,在全國各地均廣泛種植。隨著設施番茄種植面積逐年擴大及復種指數連年提高,番茄土傳病害的發生與危害程度已呈逐年加重趨勢(李煥玲,2014;杜建峰等,2020;祝海燕等,2020),其中,設施番茄枯萎病的危害尤為嚴重,一旦發生常給番茄生產造成嚴重損失。類黃酮是一種重要的植物保衛素,在植物抵御生物脅迫中發揮著重要作用,如一些黃酮類化合物可較好地抑制炭疽病菌、菜豆殼球孢菌、馬鈴薯壞疽病菌、立枯絲核菌、尖孢鐮刀菌、疫霉病菌和大豆菌核菌等多種病原菌侵染(楊才瓊等,2018)。二氫黃酮醇-4-還原酶(DFR)是類黃酮合成途徑的一種關鍵酶,克隆番茄的SlDFR基因并分析其表達特性,探究其對致病菌的響應機制,對深入研究SlDFR基因在番茄抗病過程中的調控機制具有重要意義。【前人研究進展】DFR是煙酰胺腺嘌呤二核苷酸磷酸(NADPH)依賴的氧化還原酶,屬于短鏈脫氫酶/還原酶(SDR)超家族,可選擇性地催化3種二氫黃酮醇(二氫槲皮素、二氫山奈酚和二氫楊梅素)和2種黃烷酮(柚皮素和圣草酚)生成3種不同的無色花青素苷或黃烷-4-醇進而合成兒茶素、花青素苷和原花色素等(Li et al.,2012;左濤等,2016)。DFR的底物選擇及催化效率是決定植物體內合成類黃酮成分和含量的關鍵因素。O’Reilly等(1985)采用轉座子標簽技術首次從玉米和金魚草中分離DFR基因,其他學者從擬南芥、油菜、小麥、大豆、番茄和牽牛花等多種植物中也克隆到該基因(Kubasek et al.,1992;Inagaki et al.,1999;Gutierrez-Gonzalez et al.,2010;Cunmin et al.,2016;Zuo et al.,2019)。不同植物的DFR蛋白均存在保守的NADPH結合域和底物特異性結合域,但不同物種的DFR對底物結合的偏好性存在差異(于婷婷等,2018)。已有研究認為,DFR對底物結合的特異性通常是由第134位氨基酸殘基決定(Johnson et al.,2001)。還有學者認為,雖然第134位氨基酸在底物選擇中具有重要作用,但不能單獨決定DFR的底物選擇性,其催化效率還受其他氨基酸位阻效應影響(Yan et al.,2014;Chu et al.,2015)。DFR在植物花色形成、紫外線防護、抵抗病原體、花粉發育及激素運輸等過程中發揮著重要作用(Adriana et al.,2019;Zhao et al.,2021)。DFR基因表達水平、底物結合特異性及催化效率是通過調控類黃酮合成影響植物抗逆性的重要途徑。【本研究切入點】已有相關研究證實DFR基因參與植物脅迫響應,提高植物抗病性(李玉霞等,2020)。目前雖已克隆得到SlDFR基因,但對其結構和功能的研究,特別是對抗病性方面的相關研究仍有待補充。【擬解決的關鍵問題】采用同源克隆技術從番茄枯萎病抗性品種吉美08中克隆得到SlDFR基因,對其進行生物信息學分析,并研究其在番茄不同組織受番茄枯萎病菌尖孢鐮刀菌番茄專化型(Fol4287)誘導后的表達模式,旨在為進一步研究SlDFR基因在番茄枯萎病抗性中的功能打下基礎。
1 材料與方法
1. 1 試驗材料
吉美08番茄種子購自山東壽光市洪亮種子有限公司。供試菌株為Fol4287,由福建農林大學閩臺作物有害生物生態防控國家重點實驗室云英子博士提供。RNA提取試劑盒購自北京華越洋生物科技有限公司。反轉錄試劑盒(Prime ScriptTM Reverse Transcriptase)和pMD19-T Vector載體購自寶生物工程(大連)有限公司。DNA凝膠回收試劑盒為Axygen和AP-GX-250。PCR引物和qPCR引物由北京擎科生物科技有限公司合成。
1. 2 試驗方法
1. 2. 1 引物設計與合成 根據數據庫中已有的SlDFR基因片段保守區,使用Primer Premier 5.0設計該基因全長擴增引物(SlDFR-F:5'-GCTGACTCTT TTTTACCTTT-3',SlDFR-R:5'-ATTATGTATGGTTG GGTTTC-3')。根據SlDFR基因序列測序結果,使用Primer Premier 5.0設計該基因的熒光定量引物(qSlDFR-F:5'-ACTCTCCTCCGAAGACGACA-3',qSlDFR-R:5'-TCACCTTCTTCTGGTTCTCA-3')。以Actin為內參基因(Actin-F:5'-CTCAACCCCAAGG CTAACAG-3';Actin-R:5'-ACCTCAGGGCATCGG AAC-3')。
1. 2. 2 SlDFR基因克隆與測序 以番茄根、莖、葉提取總RNA逆轉錄的單鏈cDNA為模板,利用1.2.1中基因全長擴增引物進行PCR擴增。PCR擴增產物經克隆后送至北京擎科生物科技有限公司測序。
1. 2. 3 生物信息學分析 通過NCBI的開放閱讀框(ORF)Finder工具和DNAman進行序列分析。使用在線軟件Protparam(https://web.expasy.org/protparam/)進行DFR蛋白理化性質分析。以Signalp 5.0和TMHMM進行信號肽和跨膜結構域分析。使用NCBI的CDD(https://www.ncbi.nlm.nih.gov/cdd/)和SMART(http://smart.embl-heidelberg.de/)在線分析軟件進行蛋白結構域分析。以Netphos 3.1 server分析潛在磷酸化位點。利用Cell-PLoc 2.0(http://www.csbio.sjtu.edu.cn/bioinf/Cell-PLoc-2/)預測SlDFR蛋白的亞細胞定位。分別利用SOPMA和SWISS-MODEL對SlDFR蛋白的二級結構和三級結構進行預測。以MEGA 10.0進行序列比對和構建系統發育進化樹。
1. 2. 4 SlDFR基因表達量測定及分析 以水培14 d的2葉1心期番茄幼苗為試驗材料,以Fol4287進行不同時間處理后分別取根、莖和葉,提取總RNA,以反轉錄單鏈cDNA為熒光定量PCR(qRT-PCR)模板。以1.2.1中的熒光定量引物為PCR引物,以Actin為內參基因,使用Real Time PCR熒光定量儀(Eppendorf)進行檢測。
1. 3 統計分析
試驗數據采用Excel 2010進行統計分析,以2法計算基因相對表達量。
2 結果與分析
2. 1 SlDFR基因克隆結果
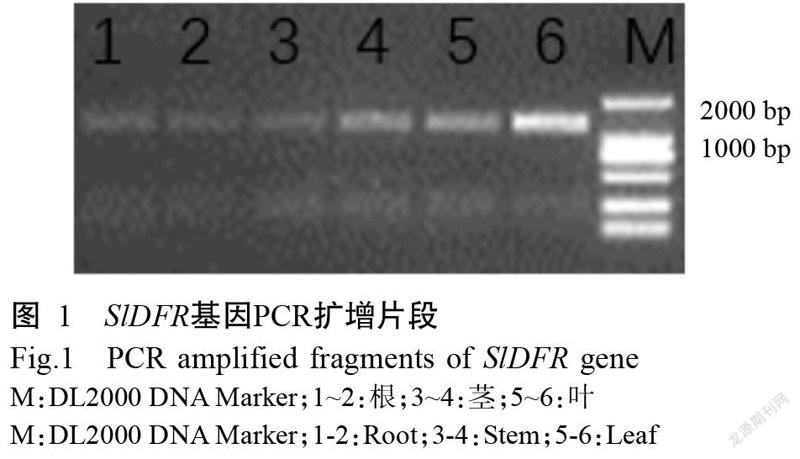
分別使用番茄根、莖、葉組織提取總RNA,使用反轉錄試劑盒反轉錄得到cDNA。cDNA作為模板直接或稀釋后擴增基因全長,得到SlDFR基因cDNA序列(圖1)。從圖1可看出,擴增條帶約1500 bp,對該cDNA序列測序結果顯示SlDFR基因為1659 bp,說明電泳結果與目的片段大小一致。
2. 2 SlDFR蛋白序列及其理化性質分析
通過NCBI的ORF Finder對SlDFR基因全長(1659 bp)的ORF即編碼區進行查找,結果發現SlDFR基因包含1個1149 bp的ORF(啟動子為ATG,終止子為TAG),編碼379個氨基酸。此外,在編碼區的上游和下游分別含有一段93 bp的5'非翻譯區和417 bp的3'非翻譯區。
使用在線軟件Protparam分析SlDFR蛋白的理化性質,發現SlDFR蛋白的分子式為C1914H2976N494O563S16,相對分子質量為42.43 kD,等電點(pI)為6.08,不穩定參數為32.84,蛋白性質穩定(通常認為蛋白的不穩定參數在40.00以下為穩定蛋白);SlDFR蛋白中含量相對較多的氨基酸為Lys(8.4%,32個)、Ala(8.2%,31個)和Leu(7.4%,28個);親水性平均系數為-0.218,脂肪系數為82.88。說明該蛋白是親水的、穩定的酸性蛋白。Signalp 5.0和TMHMM的分析結果表明,SlDFR蛋白無信號肽和跨膜結構域。
2. 3 SlDFR蛋白的保守結構域、磷酸化位點及亞細胞定位預測
使用NCBI的CDD和SMART蛋白結構域在線預測工具分析SlDFR蛋白的結構域,結果(圖2)表明,SlDFR蛋白存在NADPH結合位點,煙酰胺腺嘌呤二核苷酸依賴的脫水酶結構域位于氨基酸序列的20~271位。以Netphos 3.1 server對SlDFR蛋白的潛在磷酸化位點進行分析,結果(圖3)表明,該蛋白共有38個磷酸化位點,其中,絲氨酸18個,蘇氨酸15個,酪氨酸5個。利用Cell-PLoc 2.0預測SlDFR蛋白的亞細胞定位,結果表明SlDFR蛋白可能定位在高爾基體上。
2. 4 SlDFR蛋白的二級和三級結構分析
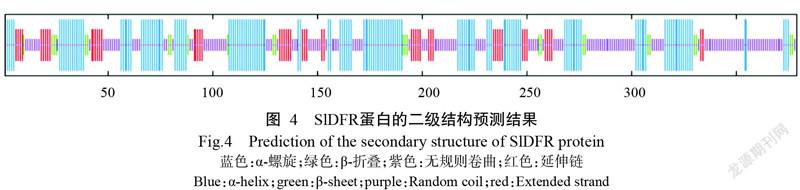
利用SOPMA預測SlDFR蛋白的二級結構,結果(圖4)表明,該蛋白主要由α-螺旋、β-折疊、無規則卷曲和延伸鏈組成,其中,α-螺旋占37.73%,延伸鏈占13.98%,β-折疊占6.60%,無規則卷曲占40.69%。
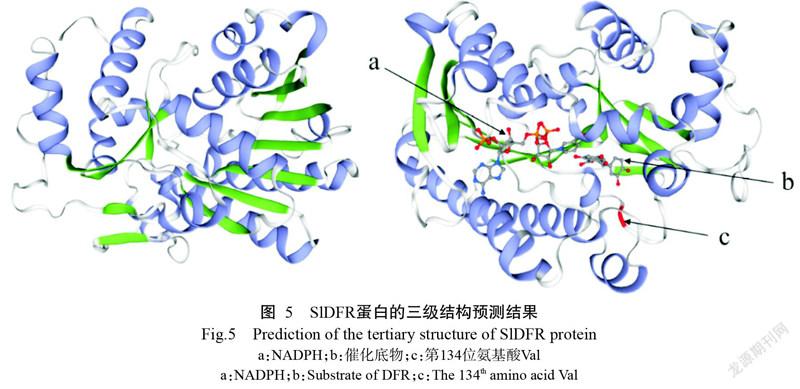
利用SWISS-MODEL在線軟件同源建模得到SlDFR蛋白的三維模型(圖5),其全球模型質量估計(GMQE)值為0.80,介于正常值0~1.00,表明該模型在空間結構上合理性較高;SlDFR蛋白主要是由無規則卷曲和α螺旋組成;SlDFR蛋白存在2個配體結合區(NADPH結合區和底物結合區),其第134位氨基酸為Val,屬于非Asn/Asp型DFR蛋白。
2. 5 DFR蛋白序列系統發育進化樹分析結果
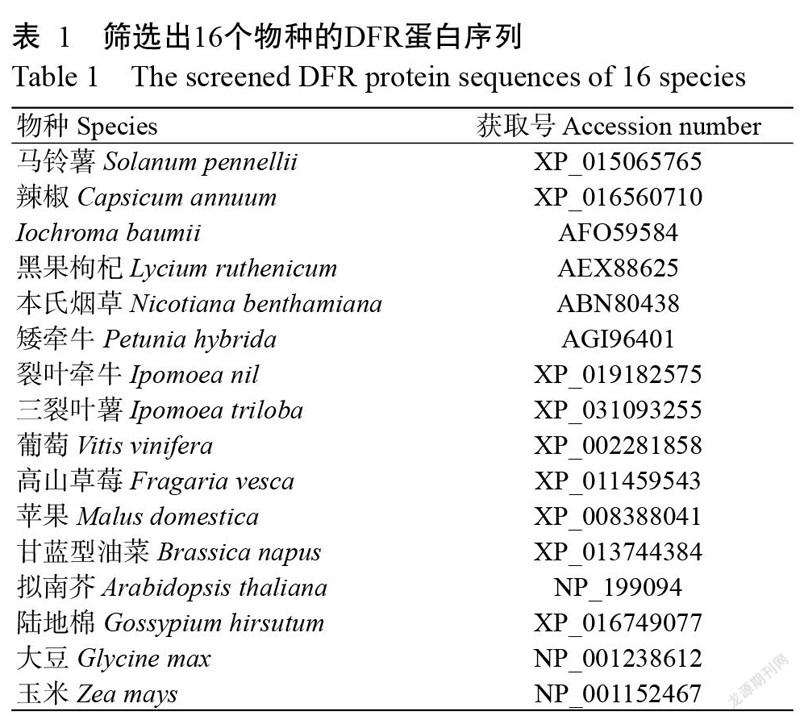
在NCBI中檢索DFR蛋白氨基酸相似序列,篩選出16個物種(表1)的DFR蛋白序列,利用MEGA 10.0對番茄及16個物種的DFR蛋白序列進行比對,結果(圖6)顯示,SlDFR蛋白序列與茄科其他屬物種的親緣關系較近。其中,馬鈴薯(Solanum pennellii)與番茄的同源性最高,其次為黑果枸杞(Lycium ruthenicum)、Iochroma baumii和辣椒(Capsicum annuum),茄科植物中矮牽牛(Petunia hybrida)與番茄的親緣關系較遠;在非茄科植物中,旋花科的裂葉牽牛(Ipomoea nil)和三裂葉薯(Ipomoea triloba)與茄科植物的進化距離較近。
2. 6 SlDFR啟動子順式作用元件分析結果
為進一步了解SlDFR基因的調控功能,從NCBI數據庫中找到番茄SlDFR基因CDS前2000 bp序列,利用啟動子在線分析工具PlantCARE(http://bioinformatics.psb.ugent.be/webtools/plantcare/html/)進行啟動子順式作用元件分析,推測其可能參與的生理過程。結果(表2)表明,SlDFR啟動子區域除含有大量光響應元件外還含有大量激素響應元件,例如茉莉酸響應元件、脫落酸響應元件和赤霉素響應元件等,此外還有1個脅迫響應元件和1個MYB結合位點。
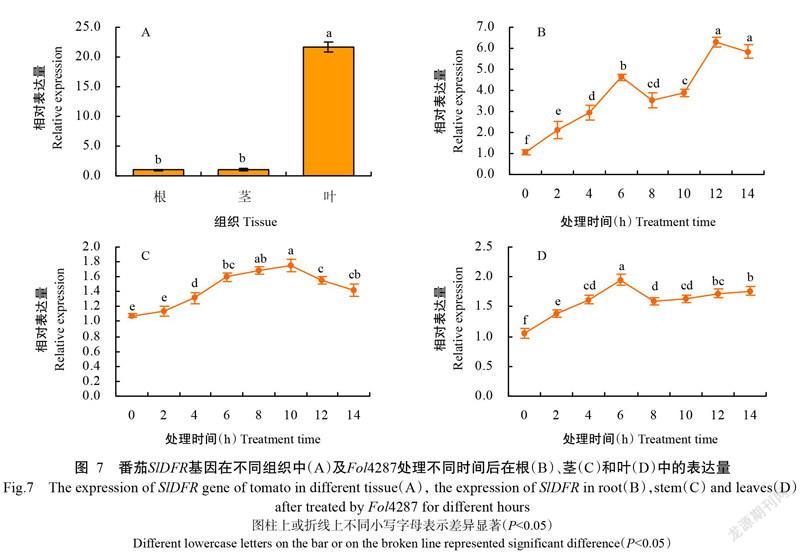
2. 7 SlDFR基因響應Fol4287的表達情況分析
采用Fol4287處理水培番茄0~14 h,通過qRT-PCR分析不同處理時間下根、莖、葉SlDFR基因的表達情況。結果(圖7)顯示,未進行Fol4287處理的對照組中,SlDFR基因在葉中的表達量顯著高于根(P<0.05,下同),為根中表達量的21.67倍(圖7-A),而在莖中的表達量與根相比無顯著差異(P>0.05)。Fol4287處理后SlDFR基因在番茄根、莖、葉中的表達量均表現不同程度上調,其中,在莖中的表達量呈先上升后下降變化趨勢,處理10 h時表達量最高,為處理0 h的1.75倍,且顯著高于除處理8 h外其他處理時間的表達量(圖7-C);Fol4287處理后SlDFR基因在葉中的表達量快速升高,其中在處理6 h時出現最大值,為處理0 h的1.94倍,且顯著高于其他處理時間的表達量(圖7-D);而Fol4287處理后SlDFR基因在根的表達量出現2個峰值,其中,處理6 h時出現第一個峰值,隨后表達量下降,處理12 h時出現最高值,表達量為對照組的6.31倍,且顯著高于除處理14 h外其他處理時間的表達量(圖7-B),與莖和葉的表達量相比變化最大,在葉中表達量變化較小。
3 討論
DFR是類黃酮合成途徑中的關鍵酶。1994年Bongue-Bartelsman等首次從番茄下胚軸中克隆得到SlDFR基因,并對其表達特性進行初步分析。本研究從番茄品種吉美08中克隆得到1個SlDFR基因,氨基酸序列分析結果表明,該基因編碼379個氨基酸,與滇牡丹、威氏綠絨蒿和日本蛇根草等植物DFR基因編碼的氨基酸數量相近(李云琴等,2020;馮猜等,2021;嚴朋飛等,2021);SlDFR蛋白是親水的、穩定的酸性蛋白,且無信號肽和跨膜結構域,為非分泌性蛋白,定位在高爾基體上,而植物DFR蛋白多定位于細胞質中(肖向文等,2014;賴呈純等,2016;王疆然等,2021),因此,SlDFR蛋白亞細胞定位預測結果是否準確有待進一步探究;啟動子順式作用元件分析結果表明,SlDFR啟動子區域含有激素響應元件、脅迫響應元件和MYB結合位點,暗示SlDFR基因參與了番茄多種激素和逆境脅迫響應途徑。
DFR底物結合的特異性控制類黃酮合成途徑中生成的花色素苷、黃烷醇和原花青素支路通量,對植物體內具有抑菌活性的黃酮類物質合成和積累發揮著重要作用。左濤等(2016)研究表明,DFR基因通過調控兒茶素生物合成提高楊樹的抗病性。Zhang等(2019)、Zhuang等(2019)研究指出,DFR基因對植物花青素的合成具有調節作用。花青素除了作為決定植物花色的主要色素外,在植物抵抗干旱、低溫和鹽脅迫等多種非生物脅迫及對火疫病菌、軟腐病菌和黃萎病菌等多種致病菌的響應過程中也具有重要作用(Gould et al.,2018;王鴻雪等,2020)。DFR基因還可作為黃烷酮4-還原酶(FNR)催化柚皮素和圣草酚生成黃烷-4-醇(flavan-4-ols),進而在其他酶的作用下形成3-脫氧花青素(3-deoxyantho-cyanidin),3-脫氧花青素及其中間代謝產物五羥基黃酮(luteo-forol)可作為防御物質抵御真菌和細菌侵害(Li et al.,2012)。Johnson等(2001)通過對非洲菊的研究首次提出DFR底物結合區,并發現其中的第134位氨基酸種類是決定所催化底物的關鍵,其中,第一類的第134位氨基酸是天冬酰胺殘基(Asn),與非洲菊相同,屬于Asn型DFR;第二類的第134位氨基酸為天冬氨酸殘基(Asp),屬于Asp型DFR,可催化二氫櫟皮黃酮(DHQ)和二氫楊梅黃酮(DHM),但不能有效催化二氫堪非醇(DHK);第三類的第134位氨基酸殘基既不是天冬酰胺也不是天冬氨酸。此外,還有研究指出,雖然第134位氨基酸在底物選擇中具有重要作用,但不能單獨決定DFR底物的選擇性,其催化效率還受其他氨基酸位阻效應影響(Yan et al.,2014;Chu et al.,2015)。本研究結果表明,番茄DFR氨基酸序列第134位氨基酸為纈氨酸(Val),為非Asn/Asp型DFR,但其作用底物的特異性及催化效率有待進一步探討。
類黃酮參與植物防御的方式分為通過調節植物生理特性提高植物對病原菌的抵抗能力和直接抑制病原菌侵害2種類型。某些黃酮類物質不會在植物的根部累積,而是通過根系分泌到土壤中發揮作用(Akifumi and Yazaki,2014),此類抑菌物質可在病原菌與植物根系接觸前分泌到土壤中從而抑制病原菌對根系的侵害。本研究結果表明,進行Fol4287處理后,番茄根、莖、葉中的DFR基因表達量均顯著增加,說明其受Fol4287誘導參與了脅迫響應過程。此外,雖然DFR基因表達具有明顯的組織特異性,在葉中的表達量顯著高于根和莖,但在根中DFR基因受Fol4287的誘導表達量快速、大量升高,其響應的劇烈程度高于莖和葉,推測SlDFR基因可通過調控番茄根系類黃酮合成提高根系黃酮類物質的含量,從而調控番茄對枯萎病的抗性。但根部合成的黃酮類物質是作物信號物質參與番茄對病原菌的應答提高番茄根部對番茄枯萎病菌的抵抗能力,還是通過根系分泌物的形式提高根際環境中類黃酮的含量,抑制病原菌生長和定殖,抑或是二者兼有,目前還不清楚。因此,DFR基因對植物根部及根系分泌物中黃酮類物質的調控及對其抑菌活性的影響將是下一步的研究方向。
4 結論
SlDFR基因表達量受Fol4287的誘導,可能參與番茄枯萎病脅迫響應過程,且對番茄枯萎病菌的響應在番茄根部更強烈,并通過調控番茄根部黃酮類物質合成提高根部對病原菌的抵抗力或根系分泌物的抑菌活性從而增強番茄對枯萎病的抗性。
參考文獻:
杜建峰,吳偉,張曉英,李洋,丁新華. 2020. 番茄頸腐根腐病的發生及其防治研究進展[J]. 生物技術通報,36(10):200-206. [Du J F,Wu W,Zhang X Y,Li Y,Ding X H. 2020. Research progress on the occurrence and control of Fusarium crown and root rot of tomato[J]. Biotechno-logy Bulletin,36(10):200-206.] doi:10.13560/j.cnki.biotech.bull.1985.2020-0260.
馮猜,周娜娜,孫世宇,周潔羽,孫威. 2021. 日本蛇根草DFR3基因的克隆分析及其編碼蛋白的分離純化[J]. 西北植物學報,41(6):926-932. [Feng C,Zhou N N,Sun S Y,Zhou J Y,Sun W. 2021. Cloning and analysis of DFR3 gene from Ophiorrhiza japonicus(OJDFR3) and isolation and purification of its coding protein[J]. Acta Bota-nica Boreali Occidentalia Sinica,41(6):926-932.] doi:10.7606/j.issn.1000-4025.2021.06.0926.
賴呈純,黃賢貴,甘煌燦,潘紅,范麗華. 2016. 刺葡萄DFR基因克隆及生物信息學分析[J]. 福建農業學報,31(7):683-689. [Lai C C,Huang X G,Gan H C,Pan H,Fan L H. 2016. Cloning and bioinformatics of DFR gene in Vitis davidii foex[J]. Journal of Fujian Agriculture,31(7):683-689.] doi:10.19303/j.issn.1008-0384.2016.07.003.
李煥玲. 2014. 番茄青枯病的發生與綜合防治技術[J]. 北方園藝,(5):54-56. [Li H L. 2014. Occurrence and integra-ted control techniques of tomato bacterial wilt[J]. Nor-thern Horticulture,(5):54-56.]
李玉霞,曲延英,艾海提·艾合買提,王慧敏,黃啟秀,陳琴,陳全家. 2020. 通過GbF3'H基因單獨沉默及其與GbCHI和GbDFR基因共沉默研究其在海島棉中抗枯萎病功能[J]. 棉花學報,32(1):1-10. [Li Y X,Qu Y Y,Aihaiti A H M T,Wang H M,Huang Q X,Chen Q,Chen Q J. 2020. Through single silencing GbF3'H gene and its co-silencing with GbCHI and GbDFR genes to study their function in resistance to Fusarium wilt in Gossypiu barbadense[J]. Cotton Science,32(1):1-10.]
李云琴,原曉龍,陳中華,王毅. 2020. 滇牡丹(Paeonia delavayi)二氫黃酮醇4-還原酶基因的鑒定及表達[J]. 分子植物育種,18(4):59-63. [Li Y Q,Yuan X L,Chen Z H,Wang Y. 2020. Identification and expression of dihydroflavonol 4-reductase gene in Paeonia delavayi[J]. Mole-cular Plant Breeding,18(4):59-63.] doi:10.13271/j.mpb. 018.001083.
王鴻雪,劉天宇,莊維兵,王忠,朱林,渠慎春,翟恒華. 2020. 花青素苷在植物逆境響應中的功能研究進展[J]. 農業生物技術學報,28(1):174-183. [Wang H X,Liu T Y,Zhuang W B,Wang Z,Zhu L,Qu S C,Zhai H H. 2020. Research advances in the function of anthocyanin in plant stress response[J]. Journal of Agricultural Biotechnology,28(1):174-183.] doi:10.3969/j.issn.1674-7968. 2020.01.018.
王疆然,王玉芬,王舒婷,張芳娟,牛顏冰,王德富. 2021. 不同花色黃芩中dfr基因的克隆及時空表達分析[J]. 生物工程學報,37(4):1312-1323. [Wang J R,Wang Y F,Wang S T,Zhang F J,Niu Y B,Wang D F. 2021. Cloning and temporal-spatial expression analysis of dfr gene from Scutellaria baicalensis with different colors[J]. Journal of Bioengineering,37(4):1312-1323.] doi:10.13345/j.cjb.200 466.
肖向文,朱奇朗,劉海峰,王俊鐸,羅城,曾聞,梁亞軍,龔兆龍,李曉波. 2014. 棕色棉DFR基因的克隆與生物信息學分析[J]. 生物技術通報,30(5):88-95. [Xiao X W,Zhu Q L,Liu H F,Wang J D,Luo C,Zeng W,Liang Y J,Gong Z L,Li X B. 2014. Cloning and bioinformatics analysis of DFR gene from brown cotton[J]. Biotechno-logy Bulletin,(5):88-95.] doi:10.13560/j.cnki.biotech.bull.1985.2014.05.021.
嚴朋飛,張瑩欣,賈維嘉,劉建,郭小雪,江元祺,屈燕. 2021. 威氏綠絨蒿二氫黃酮醇4-還原酶DFR基因克隆與表達分析[J]. 分子植物育種,19(24):8064-8070. [Yan P F,Zhang Y X,Jia W J,Liu J,Guo X X,Jiang Y Q,Qu Y. 2021. Cloning and expression analysis of dihydroflavonol 4-reductase gene from Meconopsis wilsonii[J]. Molecular Plant Breeding,19(24):8064-8070] doi:10.13271/ j.mpb.019.008064.
楊才瓊,楊文鈺,劉江. 2018. 植物類黃酮的化學生態學意義[J]. 天然產物研究與開發,30(11):2009-2016. [Yang C Q,Yang W Y,Liu J. 2018. Advances on chemical ecology of plant flavonoids[J]. Natural Product Research and Development,30(11):2009-2016.] doi:10.16333/j.1001-6880.2018.11.025.
于婷婷,倪秀珍,高立宏,韓國軍,朱長甫,盛彥敏. 2018. 高等植物二氫黃酮醇4-還原酶基因研究進展[J]. 植物研究,38(4):632-640. [Yu T T,Ni X Z,Gao L H,Han G J,Zhu C F,Sheng Y M. 2018. Advances in study of dihydroflavonol 4-reductase(DFR) genes of higher plants[J]. Bulletin of Botanical Research,38(4):632-640.] doi:10. 7525/j.issn.1673-5102.2018.04.020.
祝海燕,李婷婷. 2020. 過量施肥對設施番茄影響的調查分析[J]. 中國瓜菜,33(1):55-58. [Zhu H Y,Li T T. 2020. Effect of excessive fertilization on facilities tomato[J]. Chinese Cucurbits and Vegetables,33(1):55-58.] doi:10.16861/j.cnki.zggc.2020.0011.
左濤,趙樹堂,盧孟柱,孫愛東,王延偉,賀偉. 2016. 楊樹二氫黃酮醇-4-還原酶基因(DFR)的克隆及反義表達對兒茶素合成的影響[J]. 東北林業大學學報,44(10):49-55. [Zuo T,Zhao S T,Lu M Z,Sun A D,Wang Y W,He W. 2016. Cloning dihydroflavonol-4-reductase gene(DFR) of Poplar and its antisense expression effects on catechin[J]. Journal of Northeast Forestry University,44(10):49-55.] doi:10.13759/j.cnki.dlxb.2016.10.010.
Adriana G F,Armando V M D,Elvira O R,Luis F J. 2019. Photoprotective and antigenotoxic effects of the flavonoids apigenin,naringenin and pinocembrin[J]. Photochemistry and Photobiology,95(4):1010-1018. doi:10. 1111/php.13085.
Akifumi S,Yazaki K. 2014. Flavonoids in plant rhizospheres:Secretion,fate and their effects on biological communication[J]. Plant Biotechnology,31(5):431-443. doi:10.5511/ plantbiotechnology.14.0917a.
Bongue-Bartelsman M,O'Neill S,Tong Y,Yoder J. 1994. Characterization of the gene encoding dihydroflavonol 4-reductase in tomato[J]. Gene,138(1-2):153-157. doi:10. 1016/0378-1119(94)90799-4.
Chu Y X,Chen H R,Wu A Z,Cai R,Pan J S,Research M. 2015. Expression analysis of dihydroflavonol 4-reductase genes in Petunia hybrida[J]. Genetics and Molecular Research,14(2):5010-5021. doi:10.4238/2015.May.12.4.
Cunmin Q,Zhao H Y,Fu F Y,Wang Z,Zhang K,Zhou Y,Wang X,Wang R,Xu X F,Tang Z L,Lu K,Li J N. 2016. Genome-wide survey of flavonoid biosynthesis genes and gene expression analysis between black- and yellow-seeded Brassica napus[J]. Frontiers in Plant Scien-ce,7:1755. doi:10.3389/fpls.2016.01755.
Gould K S,Jay-Allemand C,Logan B A,Baissac Y,Bide L P R. 2018. When are foliar anthocyanins useful to plants? Re-evaluation of the photoprotection hypothesis using Arabidopsis thaliana mutants that differ in anthocyanin accumulation[J]. Environmental and Experimental Botany,154:11-22. doi:10.1016/j.envexpbot.2018.02.006.
Gutierrez-Gonzalez J,Guttikonda S,Tran L,Aldrich D,Zhong R,Yu O,Nguyen H,Sleper D. 2010. Differential expression of isoflavone biosynthetic genes in soybean during water deficits[J]. Plant Cell Physiology,51(6):936-948. doi:10.1093/pcp/pcq065.
Hong M,Kim D,Ahn J,Kang S,Seo Y,Kim J. 2018. Comparison of radiosensitivity response to acute and chronic gamma irradiation in colored wheat[J]. Genetics and Molecular Biology,41(3):611-623. doi:10.1590/1678-4685-GMB-2017-0189.
Inagaki Y,Johzuka-Hisatomi Y,Mori T,Takahashi S,Hayakawa Y,Peyachoknagul S,Ozeki Y,Iida S. 1999. Genomic organization of the genes encoding dihydroflavonol 4-reductase for flower pigmentation in the Japanese and common morning glories[J]. Gene,226(2):181-188. doi:10. 1016/s0378-1119(98)00571-x.
Johnson E T,Ryu S,Yi H,Shin B,Cheong H,Choi G. 2001. Alteration of a single amino acid changes the substrate specificity of dihydroflavonol 4-reductase[J]. The Plant Journal,25(3):325-333. doi:10.1046/j.1365-313x.2001. 00962.x.
Kubasek W,Shirley B,McKillop A,Goodman H,Briggs W,Ausubel F. 1992. Regulation of flavonoid biosynthetic genes in germinating arabidopsis seedlings[J]. Plant Cell,4(10):1229-1236. doi:10.1105/tpc.4.10.1229.
Li H,Qiu J,Chen F,Lü X,Fu C,Zhao D,Hua X,Zhao Q. 2012. Molecular characterization and expression analysis of dihydroflavonol-4-reductase(DFR) gene in Saussurea medusa[J]. Molecular Biology Reports,39(3):2991-2999. doi:10.1007/s11033-011-1061-2.
O'reilly C,Shepherd N S,Pereira A,Schwarz-Sommer Z,Bertram I,Robertson D S,Peterson P A,Saedler H. 1985. Molecular cloning of the a1 locus of Zea mays using the transposable elements En and Mu1[J]. The EMBO Journal,4(4):877-882.
Yan F,Di S,Rodas F,Torrico T,Murai Y,Iwashina T,Anai T,Takahashi R. 2014. Allelic variation of soybean flower color gene W4 encoding dihydroflavonol 4-reductase 2[J]. BMC Plant Biology,14(1):58. doi:10.1186/1471-2229-14-58.
Zhang L,Sun X,Wilson I W,Shao F,Qiu D. 2019. Identification of the genes involved in anthocyanin biosynthesis and accumulation in Taxus chinensis[J]. Genes,10(12):982. doi:10.3390/genes10120982.
Zhao Y, Zhou W J, Chen Y, Li Z J, Song X Q, Wang J, Tian D K, Niu J. 2021. Metabolite analysis in Nymphaea ‘Blue bird’ petals reveal the roles of flavonoids in color formation,stress amelioration,and bee orientation[J]. Plant Science,312:111025.
Zhuang H,Lou Q,Liu H,Han H,Wang Q,Tang Z,Ma Y,Wang H. 2019. Differential regulation of anthocyanins in green and purple turnips revealed by combined de novo transcriptome and metabolome analysis[J]. International Journal of Molecular Sciences,20(18):4387. doi:10.3390/ ijms20184387.
Zuo L,Trisha L,Moira G,Shirley J,Tom E,Jeffrey P. 2019. Assessing anthocyanin biosynthesis in Solanaceae as a model pathway for Secondary metabolism[J]. Genes(Basel),10(8):559. doi:10.3390/genes10080559.
(責任編輯 思利華)

