帚狀江蘺質(zhì)體UPA和線粒體CO I 基因的序列比較及其系統(tǒng)進(jìn)化分析
徐 瑞,陳素文,段亞飛,張文文,王 珺,周傳朋,王 蕓
(1.上海海洋大學(xué)水產(chǎn)與生命學(xué)院,上海 201306;2.中國(guó)水產(chǎn)科學(xué)研究院南海水產(chǎn)研究所,農(nóng)業(yè)農(nóng)村部水產(chǎn)品加工重點(diǎn)實(shí)驗(yàn)室,廣州 510300)
帚狀江蘺(Gracilariaedulis),隸屬于紅藻門(mén)(Rhodophyta),江蘺目(Gracilariales),江蘺科(Gracilariaceae),江蘺屬,是一種主要分布于海南省和廣東省沿海的大型海藻[1-2]。帚狀江蘺不僅具有改善水體環(huán)境、修復(fù)生態(tài)系統(tǒng)的功能[3-4],且富含海藻多糖、藻膠、多種氨基酸和微量元素,是生產(chǎn)工業(yè)瓊膠和制作水產(chǎn)動(dòng)物餌料的重要原料[5-7]。最新研究表明,帚狀江蘺提取物在抗菌和抑制腫瘤細(xì)胞增殖等醫(yī)學(xué)領(lǐng)域亦發(fā)揮作用[8-10]。目前獲得帚狀江蘺的途徑主要依靠捕撈野生資源,因此,為了實(shí)現(xiàn)帚狀江蘺種質(zhì)資源的可持續(xù)利用,需要開(kāi)展帚狀江蘺種質(zhì)資源的鑒定評(píng)價(jià)與遺傳多樣性分析。
質(zhì)體基因組和線粒體基因組具有細(xì)胞質(zhì)基質(zhì)基因組單系遺傳和克隆進(jìn)化的特征,在植物群體遺傳學(xué)研究中應(yīng)用廣泛[11]。其中,質(zhì)體UPA基因(質(zhì)體23S rRNA V區(qū)域)作為通用擴(kuò)增子,具有通用性強(qiáng)、擴(kuò)增率高等特點(diǎn),在大型海藻的分子鑒定中常被選為候選標(biāo)記[12-14]。線粒體COⅠ基因片段具有母系遺傳、進(jìn)化速度快的特點(diǎn)[15],已被公認(rèn)為是有效區(qū)分不同動(dòng)物物種的DNA條形碼標(biāo)準(zhǔn)區(qū)域[16],作為海洋紅藻的DNA條形碼,可以用于區(qū)分親緣關(guān)系相近的物種和種內(nèi)群體的生物地理亞群[17-18]。本研究采集了海南省文昌和鶯歌海潮間帶的野生帚狀江蘺,對(duì)其質(zhì)體UPA基因片段和線粒體COⅠ基因片段進(jìn)行了序列分析,并結(jié)合GenBank數(shù)據(jù)庫(kù)中紅藻門(mén)其他藻類(lèi)的UPA和COⅠ序列,從分子水平上對(duì)其遺傳距離與系統(tǒng)進(jìn)化進(jìn)行分析,以期為帚狀江蘺種質(zhì)鑒定和系統(tǒng)進(jìn)化研究提供基礎(chǔ)數(shù)據(jù)。
1 材料與方法
1.1 實(shí)驗(yàn)材料
帚狀江蘺樣品于2020年7月采自海南文昌和鶯歌海近海潮間帶,采集30株整株藻體,活體運(yùn)回實(shí)驗(yàn)室,取藻體幼嫩莖葉組織置于95%乙醇,-20℃保存,以待后續(xù)提取DNA。
1.2 DNA的提取與PCR擴(kuò)增測(cè)序
取出95%乙醇中保存的帚狀江蘺莖葉組織吸干水分(約20 mg),采用液氮研磨和吸附柱法提取樣品DNA,試劑盒選用廣州邁寶瑞生物科技有限公司的磁珠法植物DNA提取試劑盒。提取的DNA經(jīng)1%瓊脂糖凝膠電泳和核酸定量?jī)x檢測(cè)后于-80℃保存。
以帚狀江蘺基因組DNA為模板,進(jìn)行UPA基因片段和COⅠ基因片段的擴(kuò)增,引物的選擇參照文獻(xiàn)[12]和文獻(xiàn)[18](表1)。引物p23SrV_F和p23SrV_R在紅藻門(mén)中具有較好的擴(kuò)增效果,目前已在紅藻門(mén)和綠藻門(mén)中成功擴(kuò)增多個(gè)物種[12,19-22];COⅠ基因選用的引物GazF1和GazR1是目前紅藻門(mén)、褐藻門(mén)藻類(lèi)最常用的引物[18-22]。引物購(gòu)自上海生工生物工程股份有限公司,PCR試劑購(gòu)自艾科瑞生物工程有限公司,反應(yīng)體系參照試劑說(shuō)明。

表1 本實(shí)驗(yàn)所用引物序列及反應(yīng)程序Tab.1 Primer sequences and reaction procedure used in this study
將經(jīng)瓊脂糖凝膠電泳檢驗(yàn)過(guò)有明亮清晰條帶的產(chǎn)物送往上海生工生物工程股份有限公司進(jìn)行純化回收測(cè)序。為避免測(cè)序機(jī)器測(cè)量誤差及確保PCR產(chǎn)物為目的基因擴(kuò)增產(chǎn)物,每個(gè)樣品做兩個(gè)平行,送兩管PCR產(chǎn)物進(jìn)行測(cè)序。
1.3 序列分析
使用SeqMan程序?qū)y(cè)序數(shù)據(jù)進(jìn)行峰圖校正和序列拼接,通過(guò)BLAST比對(duì)確定所獲得序列為目的基因片段,利用MEGA 11進(jìn)行序列比對(duì)并去除引物兩端序列,獲得完整目的基因序列。利用DNAsp 6.0計(jì)算序列核苷酸多樣性指數(shù)和單倍型多樣性指數(shù),并用MEGA 11計(jì)算序列堿基組成,基于Kimura-2-parameter模型計(jì)算帚狀江蘺種內(nèi)和種間遺傳距離,利用鄰接法(neighbor joining method)構(gòu)建系統(tǒng)進(jìn)化樹(shù),Bootstrap value設(shè)置為1 000次重復(fù)[23]。
2 結(jié)果與分析
2.1 序列組成分析
帚狀江蘺UPA和COⅠ基因片段PCR產(chǎn)物經(jīng)測(cè)序拼接后,通過(guò)與NCBI數(shù)據(jù)庫(kù)進(jìn)行BLAST比對(duì),確認(rèn)所得序列為江蘺的UPA和COⅠ基因片段。利用MEGA 11軟件進(jìn)行序列比對(duì),刪去測(cè)序不準(zhǔn)確的序列,分別得到370 bp的UPA基因片段和664 bp的COⅠ基因片段。
30個(gè)帚狀江蘺樣品的UPA基因片段共檢測(cè)到1種單倍型,無(wú)多態(tài)性位點(diǎn),堿基T、C、A、G和A+T的平均含量分別為26.2%、16.2%、30.3%、27.3%和56.5%。30個(gè)帚狀江蘺樣品的COⅠ基因片段共檢測(cè)到2種單倍型(hap1、hap2),3個(gè)多態(tài)性位點(diǎn),均為簡(jiǎn)約信息位點(diǎn),其中轉(zhuǎn)換位點(diǎn)2個(gè),均為A/G轉(zhuǎn)換,分別在第325和第379位點(diǎn),顛換位點(diǎn)1個(gè),為A/C顛換,位于第532位點(diǎn),轉(zhuǎn)換顛換比值為2.0(表2)。序列無(wú)缺失和插入位點(diǎn);堿基T、C、A、G和A+T的平均含量分別為39.2%、15.1%、27.6%、18.1%和66.8%,與其他藻類(lèi)的堿基組成研究結(jié)果一致[24-25]。

表2 帚狀江蘺不同單倍型CO I 基因序列的變異位點(diǎn)分布Tab.2 Distribution of variab le sites of CO I gene sequence from different hap lotypes of G.edu lis
利用DNAsp 6.0軟件對(duì)帚狀江蘺UPA和COⅠ基因片段的遺傳多樣性參數(shù)進(jìn)行統(tǒng)計(jì)(表3)。其中,UPA基因只有1種單倍型,各項(xiàng)遺傳多樣性參數(shù)均為0,UPA基因片段的遺傳多樣性參數(shù)均低于COⅠ基因片段,說(shuō)明UPA基因片段比COⅠ基因片段更保守。

表3 帚狀江蘺UPA和CO I 基因片段的遺傳多樣性參數(shù)Tab.3 Genetic diversity parameters of UPA and CO I gene fragments of G.edulis
2.2 基于UPA基因的遺傳距離與系統(tǒng)進(jìn)化分析
從GenBank中選擇15種紅藻的UPA序列作為外群物種的UPA序列,包含江蘺屬、角叉菜屬(Chondrus)、海頭紅屬(Plocamium)、沙菜屬(Hypnea)、蜈蚣藻屬(Grateloupia)、石花菜屬(Gelidium)和仙菜屬(Ceramium)共7個(gè)屬。外群物種的序列信息見(jiàn)表4,15個(gè)外群物種的UPA基因序列堿基含量差異不大,相同屬的堿基含量則更為接近。
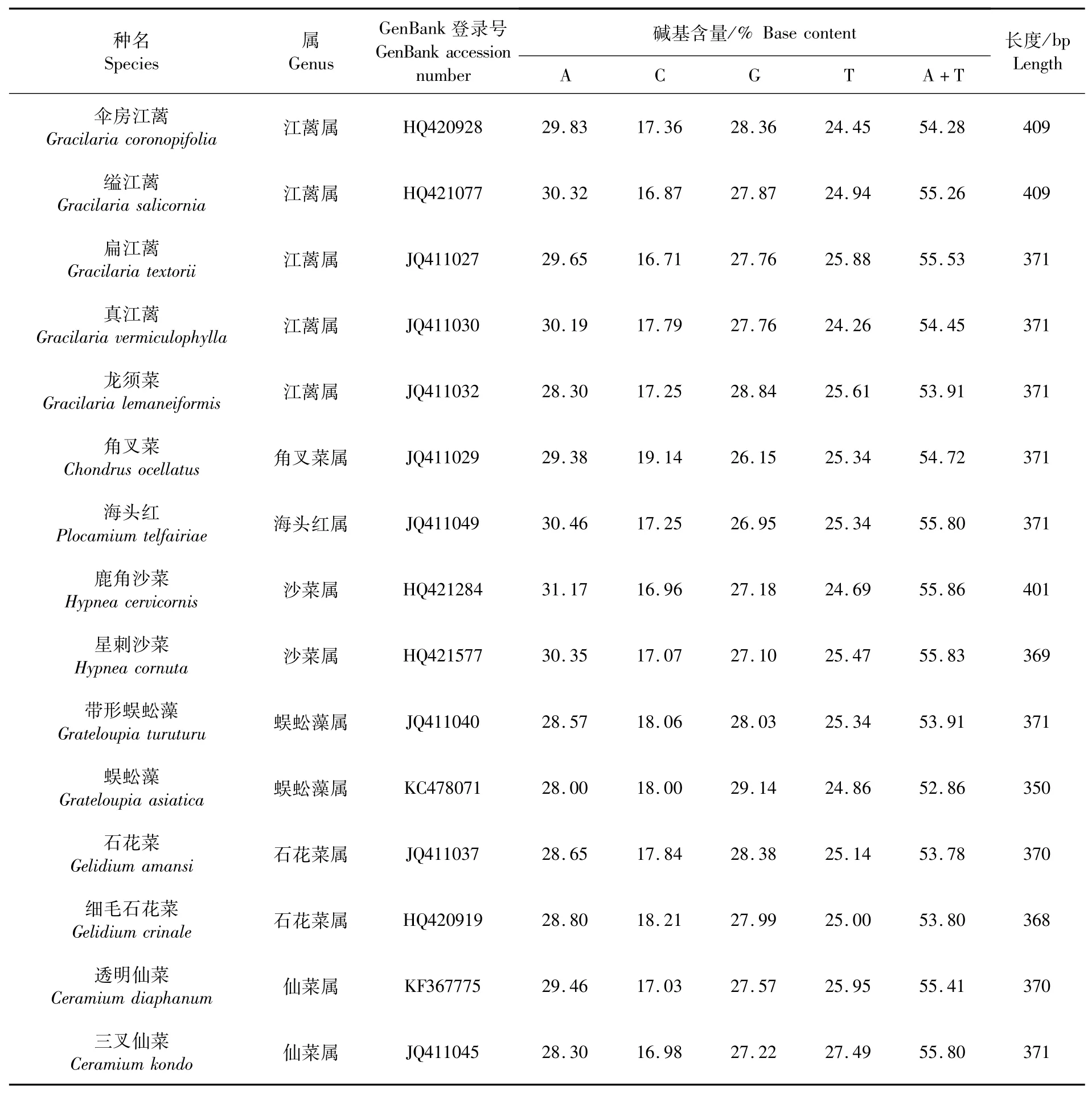
表4 外群物種UPA基因序列基本信息Tab.4 Basic data of UPA gene sequences of outgroup species
基于Kimura-2-parameter模型,計(jì)算得到PCR擴(kuò)增帚狀江蘺UPA基因序列的1種單倍型與15種外群物種UPA序列的遺傳距離(表5)。江蘺屬中,傘房江蘺(Gracilariacoronopifolia)與扁江蘺(Gracilariatextorii)遺傳距離最近,為0.025;帚狀江蘺與真江蘺(Gracilariavermiculophylla)遺傳距離最遠(yuǎn),為 0.089。16 種藻類(lèi)中,石花菜(Gelidium amansi)和細(xì)毛石花菜(Gelidium crinale)遺傳距離最近,為0.005,真江蘺與細(xì)毛石花菜遺傳距離最遠(yuǎn),為0.152。不同屬間,海頭紅屬與沙菜屬間遺傳距離最近,江蘺屬和石花菜屬間遺傳距離最遠(yuǎn)。

表5 基于UPA基因片段的Kimura-2-parameter遺傳距離(對(duì)角線左下)Tab.5 K imura-2-parameter genetic distances(lower left of the diagonal)based on UPA gene fragments
鄰接法構(gòu)建的16種紅藻的UPA基因系統(tǒng)進(jìn)化樹(shù)(圖1)顯示,傘房江蘺與扁江蘺先匯為一支,真江蘺和縊江蘺(Gracilariasalicornia)先匯為一支,這二支匯聚后再與帚狀江蘺匯聚,最后再與龍須菜(Gracilarialemaneiformis)匯聚為江蘺屬。沙菜屬、仙菜屬和石花菜屬首先分別聚為一支,隨后,石花菜屬與仙菜屬匯為一支,沙菜屬與海頭紅匯為一支,蜈蚣藻屬和角叉菜匯為一支,最后與江蘺屬匯聚。
2.3 基于CO I 基因的遺傳距離與系統(tǒng)進(jìn)化分析
從GenBank中選擇15種紅藻的COⅠ序列作為外群物種的COⅠ序列,包含江蘺屬、角叉菜屬、海頭紅屬、沙菜屬、蜈蚣藻屬、石花菜屬和仙菜屬共7個(gè)屬。外群物種的序列信息見(jiàn)表6,15個(gè)外群物種的COⅠ基因序列堿基含量差異不大。A+T含量顯著高于C+G,相同屬藻類(lèi)的堿基含量更為接近。
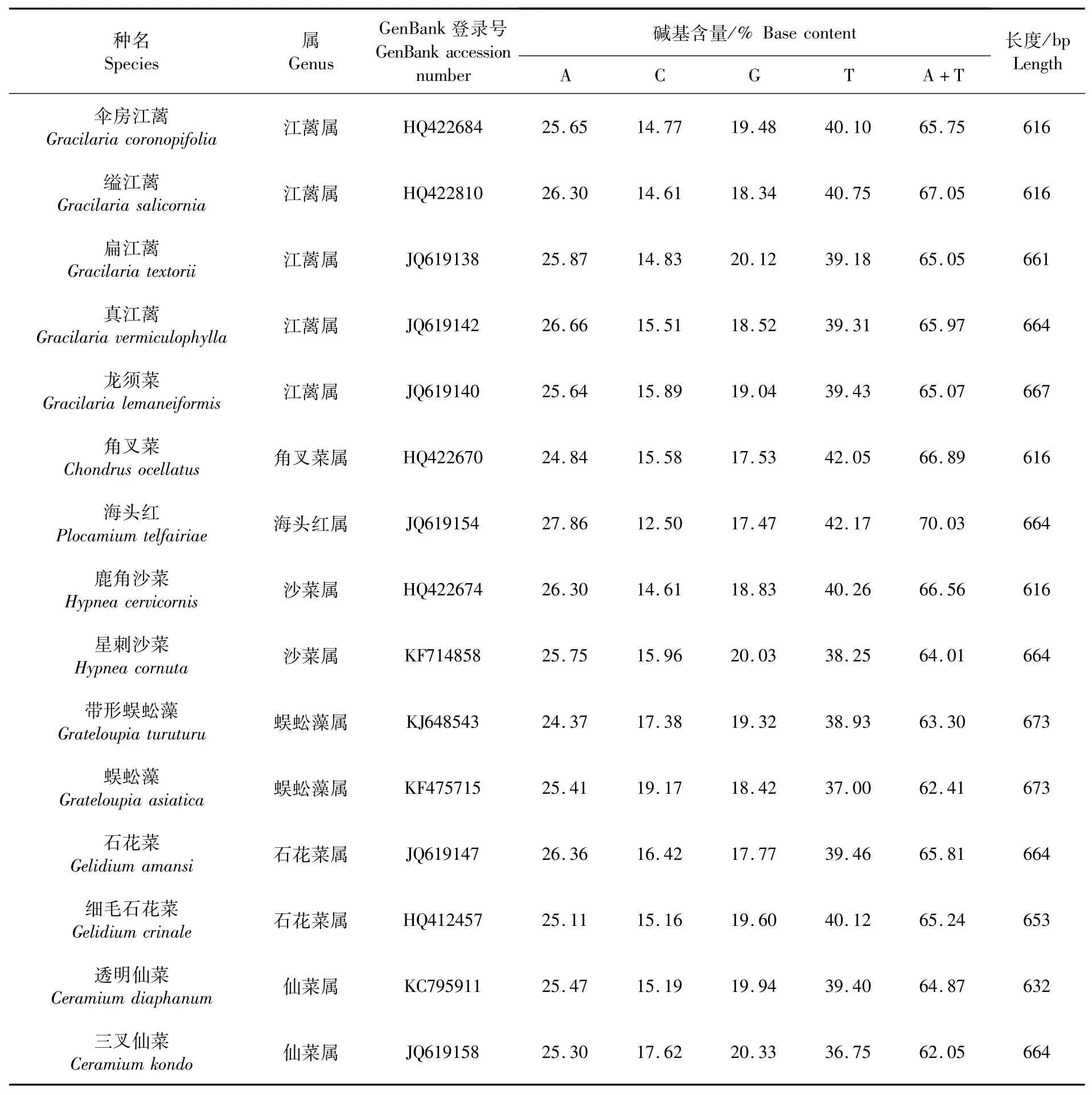
表6 外群物種CO I 基因序列信息Tab.6 Data of CO I gene sequences of outgroup species
基于Kimura-2-parameter模型,計(jì)算得到PCR擴(kuò)增的帚狀江蘺COⅠ基因序列的2種單倍型(hap1、hap2)與15種外群物種COⅠ序列的遺傳距離(表7),帚狀江蘺2種單倍型的遺傳距離為0.005。江蘺屬中,縊江蘺和傘房江蘺遺傳距離最近,為0.127,扁江蘺和龍須菜遺傳距離最遠(yuǎn),為0.175。16種藻類(lèi)中,帶型蜈蚣藻和蜈蚣藻間遺傳距離最近,為0.120;扁江蘺和三叉仙菜(Ceramiumkondo)遺傳距離最遠(yuǎn),為0.275。不同屬間,江蘺屬與仙菜屬遺傳距離最遠(yuǎn),海頭紅屬和角叉菜屬遺傳距離最近。

表7 基于CO I 基因片段的K imura-2-parameter遺傳距離(對(duì)角線左下)Tab.7 K imura-2-parameter genetic distances(lower left of the diagonal)based on CO I gene fragments
鄰接法構(gòu)建的16種紅藻的COⅠ基因系統(tǒng)進(jìn)化樹(shù)(圖2)顯示,傘房江蘺和扁江蘺先匯為一支,真江蘺和縊江蘺分別獨(dú)立為一支,帚狀江蘺的2種單倍型聚在一起成一支,這5種江蘺匯聚后再與龍須菜匯為江蘺屬。石花菜屬、蜈蚣藻屬、海頭紅、角叉菜、沙菜屬和仙菜屬先各自分別匯為一支,隨后,沙菜屬與角叉菜和海頭紅匯為一支,然后再與蜈蚣藻屬和江蘺屬匯聚,最后與石花菜屬和仙菜屬匯聚。

圖2 基于CO I 基因片段構(gòu)建的NJ進(jìn)化樹(shù)Fig.2 NJ phylogenetic tree based on CO I gene fragments
3 討論
3.1 帚狀江蘺UPA和CO I 基因片段的序列比較
本研究采用PCR技術(shù)對(duì)帚狀江蘺的UPA和COⅠ基因序列進(jìn)行擴(kuò)增,分別得到370 bp和664 bp的基因序列,序列分析結(jié)果表明,帚狀江蘺UPA基因和COⅠ基因的A+T含量(分別為56.5%和66.8%)均高于G+C。SHERWOOD等[25]研究發(fā)現(xiàn),紅藻門(mén)藻類(lèi)COⅠ基因的A+T含量大于60%,而UPA基因的堿基含量更為均衡,A+T和G+C含量通常各約占50%。相關(guān)研究表明,相對(duì)于COⅠ基因,UPA基因進(jìn)化速度更慢,更為保守;COⅠ基因比UPA基因擁有更高的變異度[14]。
本研究中,帚狀江蘺的野生群體30個(gè)樣本中,UPA基因只檢測(cè)出1個(gè)單倍型,COⅠ基因則檢測(cè)出2個(gè)單倍型和3個(gè)多態(tài)性位點(diǎn),COⅠ基因片段的各項(xiàng)遺傳參數(shù)均高于UPA基因片段。結(jié)果表明,與COⅠ基因序列相比,UPA基因序列的遺傳變異更小,序列更保守。本研究中,UPA片段只檢測(cè)到一種單倍型,推測(cè)與UPA基因的保守性相關(guān)。SHERWOOD等[25]的研究表明,由于COⅠ基因是一個(gè)編碼基因,密碼子的第3個(gè)堿基位點(diǎn)的差異是大部分變異的來(lái)源,COⅠ基因片段顯示出最大的置換飽和度,而UPA基因片段則沒(méi)有顯示出置換飽和度,這也驗(yàn)證了UPA基因更加保守。對(duì)沙菜屬的研究結(jié)果表明,COⅠ基因在6個(gè)沙菜種間的差異為10.1%~16.3%,而UPA基因只有2.5%~4.4%的種間差異,也證明了UPA基因的保守性[26]。本研究中,帚狀江蘺UPA基因片段與傘房江蘺、縊江蘺、扁江蘺、真江蘺和龍須菜的序列差異分別為4.5%、7.1%、5.0%、8.9%和8.6%,而帚狀江蘺COⅠ基因片段與傘房江蘺、縊江蘺、扁江蘺、真江蘺和龍須菜的序列差異均大于10.0%。UPA和COⅠ基因均能夠區(qū)分江蘺屬內(nèi)不同種間的物種,本研究表明,UPA基因不適合帚狀江蘺種內(nèi)的遺傳多樣性分析,但仍能用于屬內(nèi)種間的物種鑒定;與UPA基因相比較,COⅠ基因適用于帚狀江蘺種內(nèi)遺傳多樣性分析,在物種鑒定上也更具優(yōu)勢(shì)。但本研究中,UPA基因只檢測(cè)到1種單倍型,COⅠ基因也只檢測(cè)到2種單倍型,且COⅠ基因的3個(gè)變異位點(diǎn)中包含2個(gè)轉(zhuǎn)換位點(diǎn)和1個(gè)顛換位點(diǎn),轉(zhuǎn)換顛換比值高,COⅠ基因變異尚未達(dá)到飽和,也反映了海南海域的帚狀江蘺種質(zhì)資源相對(duì)單一。
3.2 帚狀江蘺的系統(tǒng)進(jìn)化
本研究中,基于UPA基因的江蘺屬內(nèi)的遺傳距離為0.025~0.089,基于COⅠ基因的江蘺屬內(nèi)遺傳距離為0.136~0.175,帚狀江蘺種內(nèi)遺傳距離為0.005,符合相關(guān)研究中提出的種間差異大于種內(nèi)差異的10倍的標(biāo)準(zhǔn)[27]。COⅠ基因的種間差異度高,已經(jīng)作為DNA條形碼成功鑒定了許多紅藻物種[28-29]。
對(duì)于傳統(tǒng)形態(tài)學(xué)難以鑒定的生物,DNA序列分析提供了一個(gè)分類(lèi)新工具,同時(shí)也被廣泛應(yīng)用于系統(tǒng)進(jìn)化關(guān)系的研究[30]。基于COⅠ基因構(gòu)建的NJ系統(tǒng)進(jìn)化樹(shù)表明,帚狀江蘺與傘房江蘺、縊江蘺、扁江蘺、真江蘺、龍須菜匯聚為一支,江蘺屬、沙菜屬、仙菜屬、石花菜屬和海頭紅屬各自匯成獨(dú)立的一支,這與形態(tài)學(xué)分類(lèi)結(jié)果一致[1,31]。基于UPA基因構(gòu)建的NJ進(jìn)化樹(shù)在江蘺屬內(nèi)和蜈蚣藻屬的劃分和COⅠ基因有些不一致:UPA構(gòu)建的進(jìn)化樹(shù)中,縊江蘺和真江蘺、傘房江蘺和扁江蘺分別匯為一支,而COⅠ構(gòu)建的進(jìn)化樹(shù)中,縊江蘺和真江蘺被分為獨(dú)立的兩支,傘房江蘺和扁江蘺匯為一支;UPA構(gòu)建的進(jìn)化樹(shù)中,蜈蚣藻被單獨(dú)分為一支,帶形蜈蚣藻與角叉菜匯為一支,而COⅠ構(gòu)建的進(jìn)化樹(shù)中,蜈蚣藻屬的兩個(gè)種匯聚到一起,角叉菜單獨(dú)一支。黃艷等[20]的研究中,同樣也出現(xiàn)UPA基因無(wú)法區(qū)分親緣關(guān)系較近的種的現(xiàn)象。相較于UPA基因,COⅠ更能區(qū)分親緣關(guān)系更近的物種。結(jié)合形態(tài)學(xué)分類(lèi)特征,COⅠ基因比UPA基因更適合構(gòu)建紅藻的系統(tǒng)進(jìn)化關(guān)系;COⅠ基因適合進(jìn)行屬內(nèi)種間的系統(tǒng)進(jìn)化分析,UPA基因則適合在更高階的分類(lèi)單元應(yīng)用。
大型海洋藻類(lèi)種類(lèi)繁多,形態(tài)復(fù)雜,采用單一的形態(tài)鑒定方法確定物種較為困難。DNA條形碼技術(shù)多應(yīng)用于獲取未鑒定生物的分類(lèi)學(xué)信息[32],在大型海藻的鑒定和遺傳分析中也被廣泛應(yīng)用[33],本研究所選用的UPA和COⅠ基因片段在紅藻門(mén)藻類(lèi)的分子鑒定中具有較高的適用性[34]。UPA基因在分析帚狀江蘺的遺傳多樣性時(shí),其保守性可能會(huì)導(dǎo)致對(duì)南海海區(qū)帚狀江蘺遺傳多樣性的低估,但UPA序列易于獲取,通用性強(qiáng),仍可作為紅藻門(mén)DNA條形碼的一個(gè)備選。COⅠ基因在本研究和其他學(xué)者的研究中,均表現(xiàn)出較強(qiáng)的區(qū)分物種的能力,適合作為紅藻門(mén)藻類(lèi)的DNA條形碼,但也有研究表明,COⅠ基因在某些藻類(lèi)中存在擴(kuò)增和測(cè)序方面的問(wèn)題[35]。
用于研究海洋藻類(lèi)的DNA條形碼還有許多,本研究?jī)H選擇了UPA和COⅠ基因?qū)χ銧罱y進(jìn)行評(píng)估,未來(lái)將選擇更多DNA條形碼進(jìn)行海洋藻類(lèi)種質(zhì)資源及遺傳多樣性研究。本研究結(jié)果顯示,南海海區(qū)帚狀江蘺種質(zhì)資源相對(duì)單一,未來(lái)應(yīng)著手開(kāi)展江蘺資源保護(hù)工作。

