秦嶺細鱗鮭人工繁育群體與野生群體遺傳變異分析
張艷萍 王 太 杜巖巖 虎永彪 婁忠玉 焦文龍
(甘肅省水產研究所, 甘肅省冷水性魚類種質資源與遺傳育種重點實驗室, 蘭州 730030)
秦嶺細鱗鮭人工繁育群體與野生群體遺傳變異分析
張艷萍 王 太 杜巖巖 虎永彪 婁忠玉 焦文龍
(甘肅省水產研究所, 甘肅省冷水性魚類種質資源與遺傳育種重點實驗室, 蘭州 730030)
研究利用線粒體DNA(細胞色素b基因序列和D-loop區序列)序列對秦嶺細鱗鮭(Brachymystax lenok tsinlingensis)野生群體和人工繁育群體的種群遺傳結構進行了分析。結果表明, 在86個個體擴增出的線粒體D-loop區730 bp片段中, A+T含量(63.5%)明顯高于G+C含量(36.5%)。Cyt b基因序列擴增1141 bp, A+T含量(52.8%)明顯高于G+C含量(47.2%)。野生群體43個個體共檢測到18個單倍型, 繁育群體43個個體中共檢測到 24個單倍型, 兩個群體共享 8個單倍型; 秦嶺細鱗鮭野生群體的單倍型多樣性和核苷酸多樣性(h=0.907±0.026; π=0.00287±0.00074)低于繁育群體(h=0.917±0.035; π=0.00349±0.00083), AMOVA分析顯示, 98.37%的分子差異位于群體內, 1.63%的分子差異位于群體間, 兩群體之間的遺傳分化水平較低(Fst=0.01631, P=0.1075; Nm=30.16)。采用鄰接法構建的系統發育樹和單倍型網絡圖分析表明, 各群體內的個體不形成單系群, 兩者之間互有交叉。總之, 秦嶺細鱗鮭野生群體與繁育群體之間基因交流充分, 未出現遺傳分化。
秦嶺細鱗鮭; 線粒體D-loop區; 線粒體細胞色素b基因; 遺傳多樣性
細鱗鮭(Brachymystax lenok)隸屬于鮭形目鮭科鮭亞科。在我國主要分布在東北地區黑龍江流域、綏芬河、圖們江、鴨綠江, 新疆的額爾齊斯河, 河北省北部白河及灤河上游以及秦嶺北麓渭河流域[1,2]。李思忠[3]根據幽門盲囊、側線鱗和最小性成熟年齡等形態學和生理學特征, 把分布在秦嶺地區的細鱗鮭定名為細鱗鮭的一個新亞種-秦嶺亞種(Brachymystax lenok tsinlingensis Li), 為我國特有種。由于其肉質鮮美、營養價值高, 早在1938年就被人工引入到 湑水河中進行人工養殖[4,5]。近年來環境污染加劇、不當的開發和過度捕撈等原因的影響,秦嶺細鱗鮭資源量急劇減少, 呈點狀分布在渭河上游部分支流中。1998年秦嶺細鱗鮭被收錄于《中國瀕危動物紅皮書-魚類》中, 屬瀕危物種, 國家Ⅱ級保護水生野生動物[6]。目前, 針對秦嶺細鱗鮭的資源調查[7]、生物學[8—10]、胚胎發育[11]和人工繁殖[12]等方面的研究已有大量的報道, 然而對其遺傳背景的研究較少, 僅見原居林等采用RAPD技術對黑河種群和 湑水河種群的遺傳多樣性進行了分析[13]。為了逐步恢復和保護秦嶺細鱗鮭的種質資源, 對其自然種群數量進行合理的補充, 了解人工繁育群體和野生群體的遺傳背景是十分重要的。
線粒體DNA (mtDNA)由于結構簡單、進化速度快和幾乎不發生重組等特點, 使其成為研究物種起源、系統發生和種內遺傳結構的有效遺傳標記[14],其中一些基因被廣泛應用在魚類的種群遺傳變異和系統發育分析。王培欣等[15]利用線粒體D-loop區分析得出8個流域叉尾斗魚種群遺傳多樣性很低且存在地理差異; 高天翔等[16]利用線粒體Cytb基因分析得出松江鱸8個群體的遺傳多樣性較高; 張迪等[17]利用線粒體COⅠ基因序列分析太湖新銀魚的遺傳多樣性, 得出有人工移植歷史種群遺傳多樣性較高。本研究利用線粒體D-loop區和Cytb基因序列對秦嶺細鱗鮭人工繁育群體和野生群體的遺傳多樣性進行比較分析, 以期為秦嶺細鱗鮭放流效果的跟蹤監測、種質資源遺傳保護提供重要依據。
1 材料與方法
1.1 樣品采集和DNA提取
收集自渭河上游支流馬鹿河野生秦嶺細鱗鮭為野生群體, 將收集自馬鹿河和渭河另一支流西河的秦嶺細鱗鮭人工馴化后, 繁殖的子一代為繁育群體,各采集43個尾鰭樣品, 用無水乙醇固定帶回實驗室進行分析, 采用酚/氯仿法提取基因組DNA[18]。
1.2 PCR擴增和序列測定
擴增 mtDNA控制區序列的引物: 正向引物為: LRBT-25: 5′-AGAGCGCCGGTGTTGTAATC-3′; 反向引物為: LRBY-1195:5′-GCTAGCGGGACTTTC TAGGGT-3′[19]。PCR反應體系為25 μL, 其中包括1 U TaqDNA聚合酶(TaKaRa), 1 μL dNTPs (2.5 mmol/L), 5 μL 10×Taq buffer (TaKaRa, 含 Mg2+), 兩條引物(10 mmol/L)各1 μL, 3 μL DNA模板, 其余雙蒸水補足。PCR反應程序為: 94℃預變性3min; 94℃變性45s, 55℃退火45s, 72℃延伸45s, 共30個循環; 反應結束后在 72℃再延伸8min。PCR產物經瓊脂糖凝膠電泳檢測后送上海美吉生物工程公司純化并測序, 測序引物為擴增引物。
擴增線粒體 Cytb基因序列的引物: L14724 (5′-GACTTGAAAAACCACCGTTG-3′); H15915 (5′-CTCCGATCTCCGGATTACAAGAC-3′)[20]。PCR反應體系為 25 μL, 其中包括 1 U TaqDNA聚合酶(TaKaRa), 1 μL dNTPs (2.5 mmol/L), 5 μL 10×Taq buffer (TaKaRa, 含Mg2+), 兩條引物(10 mmol/L)各1 μL, 3 μL DNA模板, 其余雙蒸水補足。PCR反應程序為: 94℃預變性5min; 94℃變性45s, 50℃退火45s, 72℃延伸 45s, 共 35個循環;反應結束后在72℃再延伸 10min。PCR產物經瓊脂糖凝膠電泳檢測后送上海美吉生物工程公司純化并測序, 測序引物為擴增引物。
1.3 數據分析
測序獲得的序列通過Chromas 1.45軟件獲得原始序列數據; 利用CLUSTAL X2軟件對所有序列進行比對, 參照測序圖進行人工校正。利用PAUP*V4.0軟件進行同質性檢驗(Parition homogeneity test)序列片段聯合分析的可靠性; 用 DnaSP 5.0軟件計算單倍型數、單倍型多樣性和核苷酸多樣性等; 運用Arlequin 3.1軟件中的分子變異(AMOVA)方法估算遺傳變異在群體內和群體間的分布及遺傳分化指數Fst值及其P值(用排列測驗法, 1000次重排后的顯著性檢驗), 根據 Nm=(1–Fst)/2Fst得到種群間的基因流值; 用Mega 4.0軟件統計堿基組成, 并基于Kimura 2-papamter模型計算單倍型及群體間的遺傳距離, 用鄰接法(Neighbor-joining, NJ)構建系統進化樹, 系統樹中節點的自舉置信水平應用自引導估計, 循環次數為1000次。Network軟件構建單倍型網絡圖, 用以檢測單倍型之間的進化關系。
2 結果
2.1 序列分析
對野生群體和繁育群體的線粒體控制區序列進行比對排序后, 得到730 bp的同源序列。43尾繁育群體所得序列共包含20個核苷酸變異位點, 其中簡約信息位點15個, 單突變位點5個。所有序列間沒有出現缺失與插入, 4個轉換位點, 1個顛換位點, 平均轉換與顛換數比值為4.3。在野生群體中, 43個個體共檢測到 26個變異位點, 其中簡約信息位點 21個, 單突變位點 5個, 平均轉換與顛換數比值為3.3。在秦嶺細鱗鮭養殖群體與野生群體中, 86個個體共檢測到 27個變異位點, 其中簡約信息位點 26個, 單突變位點 1個, 平均轉換與顛換數比值為3.4。堿基組成分析顯示, A、T、C和G堿基平均含量分別為31.9%、31.6%、20.8%和15.7%, 其中A+T含量(63.5%)明顯高于 G+C含量(36.5%), 表現出明顯的AT偏好和反G偏倚, 與其他脊椎動物線粒體控制區核苷酸的組成特點相一致[21]。
獲得 86尾個體線粒體 Cytb基因全序列共1141 bp。所得的序列共包含25個變異位點, 其中簡約信息位點24個, 單突變位點1個。A、T、C和G堿基平均含量分別為24.6%、28.2%、31.6%和15.6%,其中A+T含量(52.8%)明顯高于G+C含量(47.2%)。43尾野生群體所含序列共有 23個變異位點, 其中簡約信息位點16個, 單突變位點7個。43尾繁育群體所含序列共有10個變異位點, 其中簡約信息位點9個, 單突變位點1個。
2.2 遺傳多樣性
對86尾個體的控制區片段和Cytb基因片段進行同質性檢驗, 結果顯示兩者之間是一致的(P=0.13)。基于1871 bp線粒體基因聯合片段分析秦嶺細鱗鮭野生群體與繁育群體的遺傳多樣性信息見表1, 由表1中可以看出86尾個體共檢測出34個單倍型, 顯示出較高的單倍型多樣性和較低的核苷酸多樣性(h=0.919±0.022; π=0.00321±0.00077)。繁育群體與野生群體相比較, 繁育群體的單倍型多樣性和核苷酸多樣性(h=0.917±0.035; π=0.00349±0.00083)都 高 于 野 生 群 體 (h=0.907±0.026; π=0.00287± 0.00074)。在秦嶺細鱗鮭繁育群體43尾個體中共檢測出24個單倍型, 野生群體43尾個體中共檢測出18個單倍型, 其中兩群體共享 8個單倍型, 占總單倍型個數的23.5%。
2.3 群體遺傳分化
通過計算兩群體間的遺傳距離得出, 繁育群體和野生群體內的遺傳距離分別為0.004和0.003,繁育群體和野生群體之間的遺傳距離為 0.003, 略低于繁育群體內的遺傳距離, 與野生群體的遺傳距離相近。分子變異(AMOVA)結果顯示(表 2), 秦嶺細鱗鮭群體內的存在較高的遺傳變異, 占98.37%, 而群體間的變異僅占 1.63%, 表明分子之間遺傳變異主要來自于群體內的個體之間。兩群體之間的 Fst=0.01631(P=0.1075), Nm=30.16, 也顯示出秦嶺細鱗鮭繁育群體和養殖群體之間的遺傳分化不顯著。

表1 秦嶺細鱗鮭野生與繁育群體遺傳多樣性參數Tab. 1 Parameters of genetic diversity in cultured and wild Brachymystax lenok tsinlingensis populations

表2 秦嶺細鱗鮭群體AMOVA分析結果Tab. 2 Results of AMOVA analysis of Brachymystax lenok tsinlingensis
2.4 系統發育樹
由秦嶺細鱗鮭繁育群體24個單倍型和野生群體18個單倍型構建的系統發育樹(圖1)可以看出, 各野生群體和繁育群體的個體均為形成單系群, 兩者之間互有交叉, 表明兩群體的遺傳相似性較高, 親緣關系較近。由 network軟件形成秦嶺細鱗鮭群體34個單倍型的簡約網絡圖(圖2)也顯示出發散狀態勢,兩群體未形成各自的單系群。單倍型H3位于網絡圖的中心, 且享有該單倍型的個體數量在種群中所占的比例明顯高于其他單倍型所占比例, 表明H3可能是原始單倍型。
3 討論
3.1 群體的遺傳多樣性
物種遺傳多樣性的高低是評判物種能否長期存在的依據, 核苷酸多樣性是衡量一個種群 mtDNA的遺傳多樣性的重要指標, 表示各種線粒體 DNA單倍型在群體中所占的比例[22]。由實驗結果可知,秦嶺細鱗鮭 86尾個體的單倍型多樣性(h=0.919± 0.022)較高, 但核苷酸多樣性(π=0.00321±0.00077)較低, 在銀鯧[23]、鲇魚[24]和松江鱸[16]等魚類中也存在這種現象, 這種單倍型多樣性較高核苷酸多樣性較低的現象表明秦嶺細鱗鮭群體可能是由一個較小種群經歷奠基者效應或瓶頸效應后迅速擴張, 隨著個體數量的增多, 導致單倍型多樣性提高, 但缺少足夠的時間來積累核苷酸序列的變異[25], 這種推測與秦嶺細鱗鮭的起源歷程相一致[2]。但本文中得到的秦嶺細鱗鮭單倍型多樣性較高的結論與夏穎哲等[26]分析黃河地區細鱗鮭的單倍型多樣性(0.622)的結果不符, 這可能由于夏穎哲等[26]采集樣本數量(n=10)較少影響了遺傳多樣性的正確評估。
在本研究中繁育群體的單倍型多樣性和核苷酸遺傳多樣性(h=0.917±0.035; π=0.00349±0.00083)都高于野生群體(h=0.907±0.026; π=0.00287±0.00074),與原居林等[13]湑對黑河種群和 水河種群的遺傳多樣性進行分析得出秦嶺細鱗鮭繁殖群體后代遺傳多樣性降低的結論不相符, 這可能是由于本實驗繁殖群體親本來源分布較廣, 且每年都會補充一定數量的親本, 有效避免了近親繁殖和瓶頸效應, 保持了秦嶺細鱗鮭人工繁育群體的遺傳多樣性。而原居林等所采集樣本為20世紀30 年代引入到 湑水河中進行馴養的群體, 在長期的人工繁殖過程中, 由于基礎繁育群體數量較少、近親繁殖和遺傳漂變等因素,使得養殖群體喪失一些多態等位基因造成遺傳多樣性水平降低。
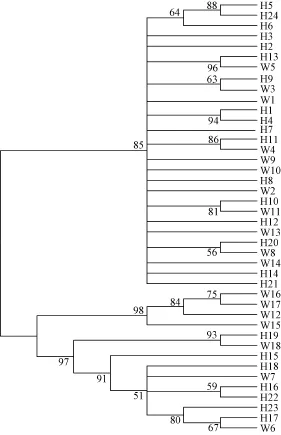
圖1 基于線粒體基因聯合片段構建秦嶺細鱗鮭的NJ樹(繁育群體H、野生群體W)Fig. 1 The neighbor-joining tree obtained by combining the control region and cytochrome b sequences (1871 bp) of Brachymystax lenok tsinlingensis population (H. Cultured population; W. Wild population)
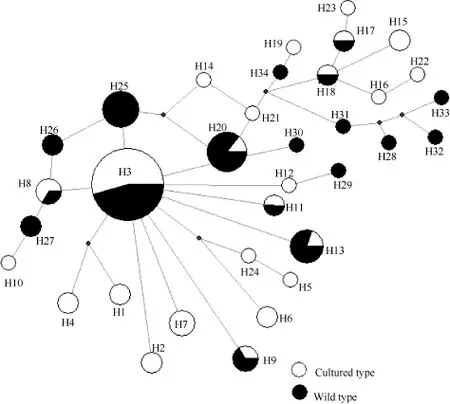
圖2 基于線粒體基因聯合片段構建秦嶺細鱗鮭34個單倍型的簡約網絡圖Fig. 2 The statistical parsimony network based on the combined sequence data for the 34 haplotypes of Brachymystax lenok tsinlingensis population
3.2 群體的遺傳結構分析
群體間的遺傳距離和遺傳分化指數是評價一個群體多態程度的重要指標。種群間遺傳距離D值的范圍是 0—0.05, 亞種間的遺傳距離 D值范圍是0.02—0.2[26]。本研究結果表明, 秦嶺細鱗鮭 2個種群內的遺傳距離為(0.003—0.004), 繁育群體與野生群體之間的遺傳距離為 0.003, 表明秦嶺細鱗鮭繁育群體與野生群體之間的遺傳變異程度低, 分化程度不明顯。秦嶺細鱗鮭群體單倍型之間的系統發育樹和網絡進化圖分析結果表明, 繁育群體和野生群體之間無明顯的遺傳分化, 兩者的遺傳相似程度較高。根據 Wright關于遺傳分化程度的理論認為 Fst值在 0—0.05表示低度遺傳分化[27], 秦嶺細鱗鮭繁育群體和野生群體之間的遺傳分化指數(Fst)為0.01631, 表明兩群體之間存在低度遺傳分化, 分子變異(AMOVA)的分析結果顯示, 98.37%的遺傳變異來源與群體內, 僅有 1.63%的變異來源與兩群體之間。由基因流Nm值來看, 基因流是指基因從一個群體遷移至另一個群體時產生的基因流動, 一般認為Nm>1, 表明群體間的基因流水平較高, 遺傳分化較小。秦嶺細鱗鮭野生群體與繁育群體之間的基因流Nm值達到30.16, 遠大于1, 也同樣表明了兩群體之間的遺傳分化較小, 這可能是由于兩者之間共享單倍型較多有關。秦嶺細鱗鮭資源量的減少可以通過人工增殖手段來恢復, 但如果其種群遺傳多樣性的降低卻難以彌補。目前秦嶺細鱗鮭的繁育群體主要用于增殖放流, 保持其較高的種群遺傳多樣性具有重要意義。
[1] Qin S Z, Wang S A. Studies on the subspecies of Brachymystax lenok [J]. Salmon Fishery, 1989, 2(1): 52—61 [秦樹臻, 王所安. 細鱗魚亞種問題的研究. 鮭鱒漁業, 1989, 2(1): 52—61]
[2] Li S Z. Discussed the geographical distribution of China salmonidae fish [J]. Chinese Journal of Zoology, 1984, (1): 34—37 [李思忠. 中國鮭科魚類地理分布的探討. 動物學雜志, 1984, (1): 34—37]
[3] Li S Z. On a new subspecies of fresh-water trout, Brachymystax lenok tsinlingensis, from taipaishan, Shanxi, China [J]. Acta Zootaxonomica Sinica, 1966, 3(1): 92—94 [李思忠. 陜西太白山細鱗鮭的一新亞種. 動物分類學報, 1966, 3(1): 92—94]
[4] Shaanxi Institute of Zoology. Ichthyography of Qinling Mountains [M]. Beijing: Science Press. 1987, 14—15 [陜西省動物研究所. 秦嶺魚類志. 北京: 科學出版社. 1987, 14—15]
[5] Du H B, Wu J X, Wang L Z. Story behind Brachymystax lenok tsinlingensis in Xushui river valleys [J]. China Fisheries, 2006, 373(12): 79—80 [杜漢斌, 武金星, 王綠洲.湑水河流域秦嶺細鱗鮭背后的故事. 中國水產, 2006, 373(12): 79—80]
[6] Wang S, Yue P Q, Chen Y Y. China Red Data Book of Endangered Animals: Pisces [M]. Beijing: Science Press. 1998, 35—37 [汪松, 樂佩琪, 陳宜瑜. 中國瀕危動物紅皮書(魚類). 北京: 科學出版社. 1998, 35—37]
[7] Ren J, Liang G. Resource survey report of Brachymystax lenok tsinlingensis in Qianhe river valleys of Qinling Mountains [J]. Journal of Shaanxi Normal University (Natural Science Edition), 2004, 32(9): 165—168 [任健, 梁剛. 千河流域秦嶺細鱗鮭資源調查報告. 陜西師范大學學報(自然科學版), 2004, 32(9): 165—168]
[8] Yang J Y, Zhong L, Wang K F, et al. Biological studies and protection proposes of Brachymstax lenok in Heihe River Shaanxi province [J]. Journal of Shaanxi Normal University (Nature Science Edition), 2006, 34(S1): 67—69 [楊軍嚴, 鐘林, 王開鋒, 等. 陜西黑河細鱗鮭生物學研究及資源保護.陜西師范大學學報(自然科學版), 2006, 34(S1): 67—69]
[9] Wang G X, Zhou J S, Qian X M. Preliminary studies on oxygen consumption rate and suffocated point of Brachymystax lenok tsinlingensis [J]. Chinese Journal of Zoology, 2006, 41(2): 72—75 [王高學, 周繼術, 強曉明.秦嶺細鱗鮭耗氧率和窒息點的初步研究. 動物學雜志, 2006, 41(2): 72—75]
[10] Zheng X L, Duan M, Bu S H, et al. Analysis of the Nutritional Components of Muscle of Brachymystax lenok from Qinling Mountains [J]. Acta Nutrimenta Sinica, 2010, 32(5): 516—520 [鄭雪莉, 段梅,卜書海, 等. 秦嶺細鱗鮭肌肉營養成分的分析. 營養學報, 2010, 32(5): 516—520]
[11] Shi D L, Wei Q W, Sun Q L, et al. Early ontogenesis of Brachymystax lenok tsinlingensis [J]. Journal of Fishery Sciences of China, 2012, 19(4): 557—567 [施德亮, 危起偉,孫慶亮, 等.秦嶺細鱗鮭早期發育觀察. 中國水產科學, 2012, 19(4): 557—567]
[12] Xue C J. Technology of breeding and cultivation for Brachymystax lenok tsinlingensi [J]. China Fisheries, 2011, (10): 32—33 [薛成杰. 秦嶺細鱗鮭繁育與養殖技術. 中國水產, 2011, (10): 32—33]
[13] Yuan J L, Zhu J J, Wang G X. Analysis of the genetic diversity in Heihe River and Xushuihe River populations of Qinling Brachymystax lenok [J]. South China Fisheries Science, 2009, 5(3): 63—66 [原居林, 朱俊杰, 王高學. 秦嶺細鱗鮭黑河種群和 湑水河種群的遺傳多樣性分析. 南方水產, 2009, 5(3): 63—66]
[14] Avise J C, Arnold J, Ball R M, et al. Intraspecific phylogeography: the mitochondrial DNA Bridge between population genetics and systematics [J]. Annual Review of Ecology and Systematics, 1987, 18: 489—522
[15] Wang P X, Bai J J, Hu Y C, et al. Population genetic variations and phylogeography of Macropodus opercularis [J]. Acta Ecologica Sinica, 2011, 31(2): 441—448 [王培欣,白俊杰, 胡隱昌, 等. 叉尾斗魚種群遺傳變異與親緣地理.生態學報, 2011, 31(2): 441—448]
[16] Gao T X, Bi X X, Zhao L L, et al. Population genetic structure of roughskin sculpin Trachidermus fasciatus based on the mitochondrial Cytb sequence [J]. Acta Hydrobiologica Sinica, 2013, 37(2): 199—207 [高天翔, 畢瀟瀟, 趙林林,等. 基于線粒體 Cytb 基因全序列的松江鱸群體遺傳結構分析. 水生生物學報, 2013, 37(2): 199—207]
[17] Zhang D, Lei G C, Gong C, et al. Genetic diversity of Neosalanx taihuensis based on mitochondrial CO Ⅰsequences [J]. Journal of Lake Sciences, 2012, 24(2): 299—306 [張迪, 雷光春, 龔成, 等. 基于 COⅠ基因序列的太湖新銀魚遺傳多樣性. 湖泊科學, 2012, 24(2): 299—306]
[18] Sambrook J, Russell D W. Molecular Cloning: a Laboratory Manual [M]. Cold Spring Harbor Laboratories Press. 2001, 463—470
[19] Ma B, Jiang Z F, Huo T B. Study on the taxonomic status of species of brachymystax in Heilongjiang River and Tumen River systems based on mitochondrial control region sequence [J]. Acta Zootaxonomica Sinica, 2009, 34(3): 499—506 [馬波, 姜作發, 霍堂斌. 基于線粒體DNA控制區序列變異探討黑龍江和圖們江細鱗鮭屬魚類的分類地位. 動物分類學報, 2009, 34(3): 499—506]
[20] Xiao W H, Zhang Y P, Liu H Z. Molecular systematics of Xenocyprinae (Teleostei: Cyprinidae): taxonomy, biogeography, and coevolution of a special group restricted in East Asia [J]. Molecular Phylogenetics and Evolution, 2001, 18(2): 163—173
[21] Brown G G, Gadaleta G, Pepe G, et al. Structural conservation and variation in the D-loop containing region of vertebrate mitochondrial DNA [J]. Journal of Molecular Biology, 1986, 192: 503—511
[22] Liu Y H, Zhang M H. Population genetic diversity of Roe Deer (Capreolus pygargus) in mountains of Heilongjiang province [J]. Zoological Research, 2009, 30(2): 113—120 [劉艷華,張明海. 黑龍江省不同山系狍種群遺傳多樣性分析. 動物學研究, 2009, 30(2): 113—120]
[23] Peng S M, Shi Z H, Hou J L. Comparative analysis on the genetic diversity of cultured and wild silver pomfret populations based on mt D-loop and CO Ⅰ gene [J].Journal of Fisheries of China, 2010, 34(1): 19—25 [彭士明, 施兆鴻,侯俊利. 基于線粒體D-Loop區與 COⅠ基因序列比較分析養殖與野生銀鯧群體遺傳多樣性. 水產學報, 2010, 34(1): 19—25]
[24] Xiao M S, Cui F, Kang J, et al. Genetic structure and variation of wild Chinese catfish from Huaihe River based on Cytb gene sequence [J]. Chinese Journal of Zoology, 2013, 48(1): 75—86 [肖明松, 崔峰, 康健, 等. 淮河野生鲇魚線粒體 Cytb基因的序列變異與遺傳結構分析. 動物學雜志, 2013, 48(1):75—86]
[25] Bowen B W, Bass A L, Rocha L A, et al. Phylogeography of the trumpetfishes (Aulostomus): ring species complex on a global scale [J]. Evolution, 2001, 55(5): 1029—1039
[26] Nei, Masatoshi. Molecular Population Genetics and Evolution [M]. American Elsevier Pub. Co. 1975, 128—132
[27] Wright S. The gentical structure of population [J]. Annals of Eugenics, 1949, 15(1): 323—334
ANALYSIS OF THE GENETIC DIVERSITY OF CULTURED AND WILD BRACHYMYSTAX LENOK TSINLINGENSIS POPULATIONS BASED ON MTDNA D-LOOP AND CYT B
ZHANG Yan-Ping, WANG Tai, DU Yan-Yan, HU Yong-Biao, LOU Zhong-Yu and JIAO Wen-Long
(Gansu Key Laboratory of Cold Water Fishes Germplasm Resources and Genetics Breeding, Gansu Fishers Research Institute, Lanzhou 730030, China)
Brachymystax lenok tsinlingensis is one type of endemic fishes distributed in Qinling Mountains. Due to the environmental deterioration and overfishing, the size of its population has decreased sharply. To rescue this species it is necessary to study its genetic structure and phylogeography and hereby obtain better understanding of the population. In this study, we determined the genetic diversity of cultured and wild Brachymystax lenok tsinlingensis populations by analyzing their mtDNA Cyt b and D-loop genes. The results showed that the average contents of A, T, C and G in D-loop were 31.9%, 31.6%, 20.8% and 15.7%, respectively. The contents of A+T (63.5%) were higher than those of C+G (36.5%). In the Cyt b gene, the average contents of A, T, C and G were 24.6%, 28.2%, 31.6% and 15.6%, respectively. The contents of A+T (52.8%) were also higher than those of G+C (47.2%). We observed that 43 wild individuals had 18 haplotypes, and that 43 cultured individuals had 24 haplotypes. The two populations shared 8 haplotypes in common. The average haplotype diversity and nucleotide diversity of the wild population (h=0.907±0.026; π=0.00287±0.00074) were lower than those of the cultured population (h=0.917±0.035; π=0.00349±0.00083). The AMOVA analysis showed that the molecular variation between the two populations was 98.37%, and the variation within a population was 1.63%. The level of genetic differentiation was low (Fst=0.01631, P=0.1075; Nm=30.16). Phylogenetic tree based on NJ and minimum spanning network for Brachymystax lenok tsinlingensis showed that individuals within the two populations did not form a monophyletic clade. Our results suggested that there was an efficient gene flow between the cultured and the wild populations, and there was no significant genetic differentiation between the two populations.
Brachymystax lenok tsinlingensis; mtDNA D-loop; mtDNA Cyt b; Genetic diversity
Q346
A
1000-3207(2014)05-0828-06
10.7541/2014.124
2013-07-01;
2014-01-26
國家自然科學基金(31160529); 甘肅省自然科學基金(1208RJYA033)資助
張艷萍(1966—), 女, 甘肅武威人; 博士; 主要從事冷水魚類養殖。E-mail: zypfish@sina.com
王太, E-mail: aqhongqi@qq.com
- 水生生物學報的其它文章
- GILL MEDIATES IMMUNE RESPONSES AFTER GRASS CARP REOVIRUS CHALLENGE IN GRASS CARP (CTENOPHARYNGODON IDELLA)
- MORPHOLOGICAL OBSERVATION AND RBCL SEQUENCE ANALYSIS OF A NEW SPECIES FROM CHINA, GRATELOUPIA BOAOENSIS WANG ET LUAN SP. NOV.(HALYMENIACEAE, RHODOPHYTA)
- GILL MEDIATES IMMUNE RESPONSES AFTER GRASS CARP REOVIRUS CHALLENGE IN GRASS CARP (CTENOPHARYNGODON IDELLA)
- 養殖密度對俄羅斯鱘幼魚的生長、生理和免疫指標的影響
- 一種快速構建集胞藻6803 petBD必需基因定點突變株的方法
- 大通湖環棱螺的次級生產力

