脊椎動物NF-κB1/2基因亞家族分子進化和功能分歧分析
甘 翔,王繼文,劉賀賀,李 亮,孫文強,王郁石,張 濤,陳 達,黃惠蘭
(四川農業大學,畜禽遺傳資源發掘與創新利用四川省重點實驗室,成都 611130)
NF-κB1與 NF-κB2共同隸屬于 NF-κB基因家族,分別編碼p50與p52的前體蛋白p105和p100。p105與p100是核轉錄因子,在二聚體化后能與免疫球蛋白輕鏈(Immunoglobulin light chain,MYLC)基因增強子cDNA序列(5′-GGGACTTTCC-3′)特異性結合并調控其轉錄,從而啟動和調節眾多免疫和炎癥反應[1-2]。NF-κB1/2擁有Rel homology domain(RHD)、IPT domain(IPT)、ankyrin repeats(ANK)和 Death domain(DD)4個結構域[3]。RHD由大約200個氨基酸殘基組成,擁有核定位信號序列,是與DNA結合的關鍵區域,也是與抑制劑作用的重要區域;ANK可作為NF-κB家族的抑制劑,通過與RHD結合來使其滯留在細胞質并保持靜息態,ANK蛋白的磷酸化、泛素化、降解釋放RHD的過程也就是NF-κB蛋白的激活過程[4];而IPT和DD則與NF-κB蛋白二聚體的穩定性與活性有著密切的聯系[5]。
研究表明,NF-κB基因的原始結構起源于后生動物以前,在進化過程中分化為 NF-κB1和 NF-κB2[6]。利用模式脊椎動物的 NF-κB1/2氨基酸序列構建進化樹,發現它們分成兩支,且完全沒有交叉的跡象,說明兩者在進化上出現了明顯的分歧,暗示它們在結構上存在一定差異。另外,在脊椎動物中,NF-κB1/2蛋白的功能也表現出了一定的差異。有文獻報道[7-8],不同的 NF-κB1/2蛋白二聚體對于相應的κB位點會顯示出不同的親和力與激活能力。不僅如此,兩者的ANK抑制結構對于不同的二聚體也可能顯示出不同的抑制強度。還有報告[7-9]稱,許多刺激信號如 TNF-α、IL-1、LPS等對 NF-κB1和NF-κB2氨基酸序列的刺激能力與刺激途徑也有所差異。在小鼠中,敲除NF-κB1會導致B細胞的多種功能缺陷,而敲除NF-κB2則會引起淋巴結構改變,影響上皮發育。另外,兩者的敲除反應都會一定程度上導致胃黏膜增生,但NF-κB2對胃黏膜的影響程度要大于NF-κB1[4]。當前的研究已經基本定義了NF-κB1/2基因的起源,也明確了 NF-κB家族在脊椎動物中的功能差異,但對造成這些差異的原因還沒有明確的定義。不過可以推斷,NF-κB1/2的 RHD、IPT、ANK 與 DD 在 NF-κB1與 NF-κB2基因亞家族分子進化特征的形成和分子功能分歧的產生方面扮演了重要的角色。
本研究選擇模式脊椎動物的NF-κB1/2基因與蛋白質序列,針對NF-κB1/2的RHD、IPT、ANK和DD 4個結構域進行生物信息學分析,旨在揭示引起NF-κB1/2功能分化的部分原因,并闡述 NF-κB1/2在脊椎動物中進化、變遷的基本趨勢。
1 材料與方法
1.1 序列數據的收集與下載
序列比對與核苷酸替代率分析所用的NF-κB1/2氨基酸、核苷酸序列均下載自NCBI數據庫(http://www.ncbi.nlm.nih.gov/)。序列比對使用了包括人類(Homo sapiens)、大鼠(Rattus norvegicus)、小鼠(Mus musculus)、原雞(gallus gallus)、非洲爪蟾(Xenopus(Silurana)tropicalis)、美國短吻鱷 (Alligator mississippiensis)、二 色熱帶魚(Stegastes partitus)7種具有代表性的模式動物的NF-κB1/2的氨基酸序列。而核苷酸替代率分析則選用了魚類、兩棲類、爬行類、鳥類和海陸哺乳類共計20余種脊椎動物的 NF-κB1/2核苷酸序列[10]。
1.2 序列比對與系統發育樹的構建
使用ClustalW將下載序列對齊,使用DAMBE等軟件進行格式處理,得到的結果輸入MEGA 6.0軟件,使用鄰接法(Neighbor-Joining,NJ),經過自展法(Bootstrap)1000次重復驗證,以保證樹拓撲結構的可靠性,分別構建NF-κB1/2氨基酸全序列及其各個結構域的氨基酸序列系統發育樹[11-12]。
1.3 NF-κB1/2蛋白的結構域預測
使用Pfam 在線數據庫(http://pfam.sanger.ac.uk/)對 NF-κB1/2蛋白進行結構預測。
1.4 進化速率計算檢驗與分析
使用DAMBE等軟件處理序列文本格式,使用MEGA6.0,ClustalW 進行向導樹的構建[13]。將處理結果文件輸入paml軟件包,codeml工具[14-15],分別選取模型A:所有的分支有一個ω,模型B:所有的分支有相同的ω且等于1,模型H:每一支都有自己的ω,選擇最優模型從而得出各個結構域的整體ω值。每個位點ω的計算也使用codeml工具,NS-site參數為0、1、2、7、8,在生成結果中優先選用BEB模型,從而得到 NF-κB1/2的 RHD、ANK 和DD 中各個位點的 ω值[16-17]。
2 結 果
2.1 基于 NF-κB1/2與結構域 RHD、IPT、ANK和DD氨基酸序列的系統發育樹
如圖1a所示,進化樹中 NF-κB1/2分為兩大支,進化趨勢與物種進化趨勢一致。由魚類至兩棲類之后,系統發育樹再分為兩支,其中一支為爬行類與鳥類,另一支為哺乳類。樹中NF-κB1/2兩個成員在整個脊椎動物進化歷程中并沒有出現任何的交織,這表明NF-κB基因家族早在脊椎動物與非脊椎動物分歧時,就已經分化成為 NF-κB1和 NF-κB2,然后開始獨立進化。
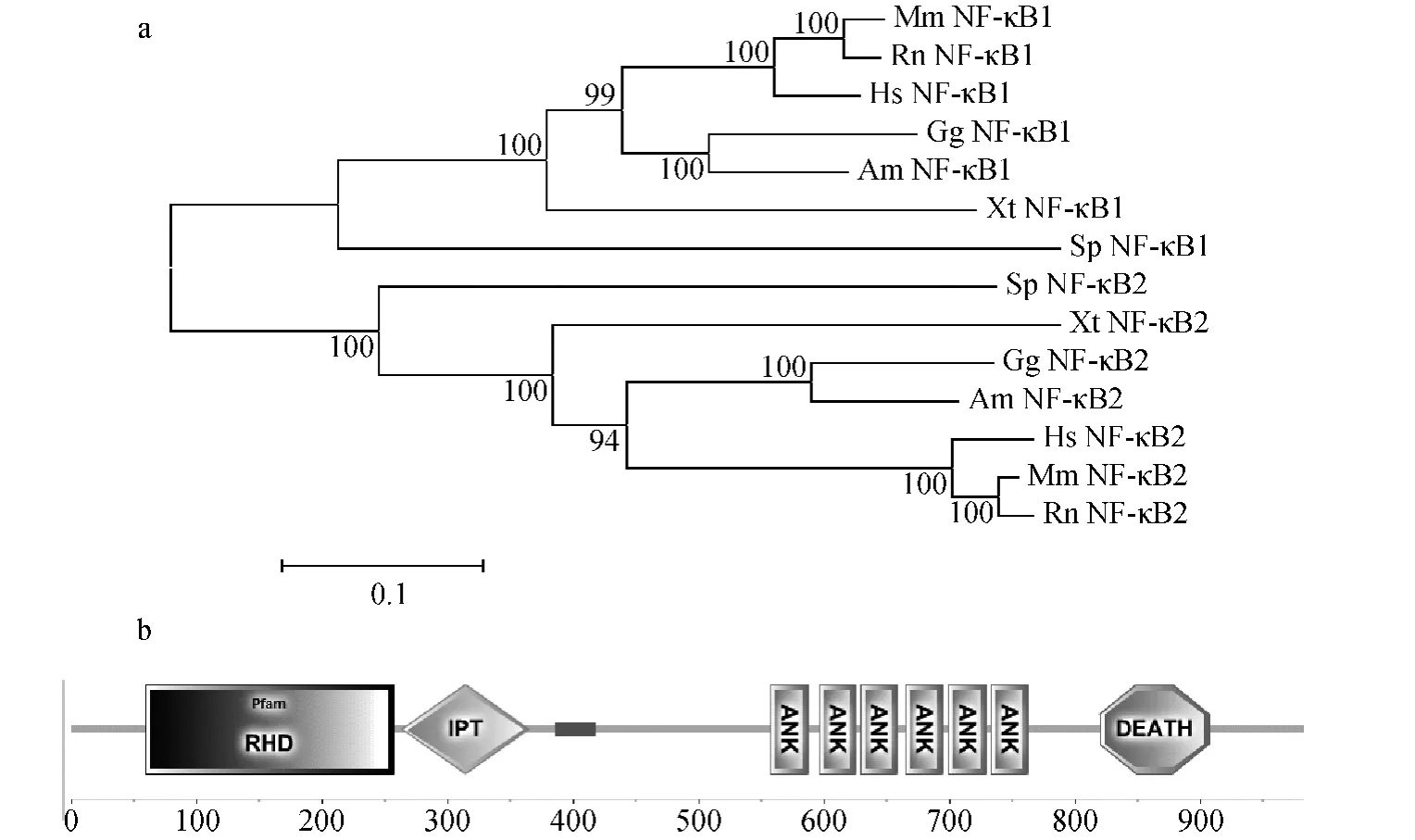
圖1 NF-κB1/2氨基酸序列的系統發育樹與保守結構域Fig.1 Phylogenetic tree of NF-κB1/2and their conserved domains
脊椎動物 NF-κB1/2兩個成員都包含 RHD、ANK、IPT和DD 4個結構域(圖1b),由它們的氨基酸序列所構建的系統發育樹(圖2)與基于全序列構建的發育樹基本一致。
2.2 基于 NF-κB1/2 結構域(RND、IPT、ANK 和DD)的序列分析
圖3中,NF-κB1/2之間在RHD上存在較多保守區域,但在序列的60~66、108~117、157~164位氨基酸區段(圖中方框標出)也發現了它們各自的特征序列。在IPT區域上,兩個基因在相應物種間都表現出較高的同源性。而在ANK區域上,無論在直系同源還是旁系同源結構中,該區域都出現了較大差異。另外,相對于其他3個結構域,DD區域的旁系同源結構之間存在很大的差異,而直系同源結構則表現出較高的同源性。
2.3 NF-κB1/2各保守結構域選擇壓力比較
Codeml中各模型比對結果顯示,NF-κB1的ANK、RHD和 DD,NF-κB2的 ANK 與 RHD都更適用于H模型,檢測結果為極顯著;而NF-κB1/2的IPT,NF-κB2的DD更適用于A模型,檢測結果也極顯著。
分別比較了 NF-κB1/2的 RHD、ANK、IPT與DD區域的選擇壓力,結果(表1)表明,在魚類及兩棲動物上,NF-κB1/2的 RHD,NF-κB1的 ANK 顯示出較高的ω值;在爬行動物與鳥類上,NF-κB1/2的ANK與NF-κB1的DDω值較大;而在哺乳動物中,大多數結構域的ω值均低于0.1。
而對NF-κB1/2氨基酸各位點選擇壓力(圖4)分析表明,RHD、IPT、ANK與DD序列的ω值均小于1.2,且在所分析脊椎動物中,4個結構域均沒有出現處于顯著水平的正選擇位點。NF-κB1/2的RHD區域大多數位點ω值在0.1以下。相對于RHD、IPT與DD區域,ANK區域則擁有較高的進化速率;NF-κB1的IPT絕大多數位點ω值較低,而NF-κB2的IPT所有位點的ω值均在0.01以下;NF-κB1/2的DDω曲線存在較大差異,NF-κB1的DD各個位點的ω值顯示出較大的波動。
3 討 論
NF-κB1/2屬于 NF-κB基因家族中的亞家族,作為轉錄因子,能夠誘導機體多種正向調控基因的轉錄,在動物機體免疫反應、骨骼肌發育中發揮重要作用[1]。研究表明,NF-κB基因的原始結構起源于后生動物以前,在進化過程中分化為NF-κB 1和NF-κB2[6]。通過構建NF-κB1/2 的進化樹,發現NF-κB基因家族早在脊椎動物與非脊椎動物發生分歧前,就已經分化成為 NF-κB1和 NF-κB2,然后開始獨立進化,這與其他報道[18]得出的結論一致。
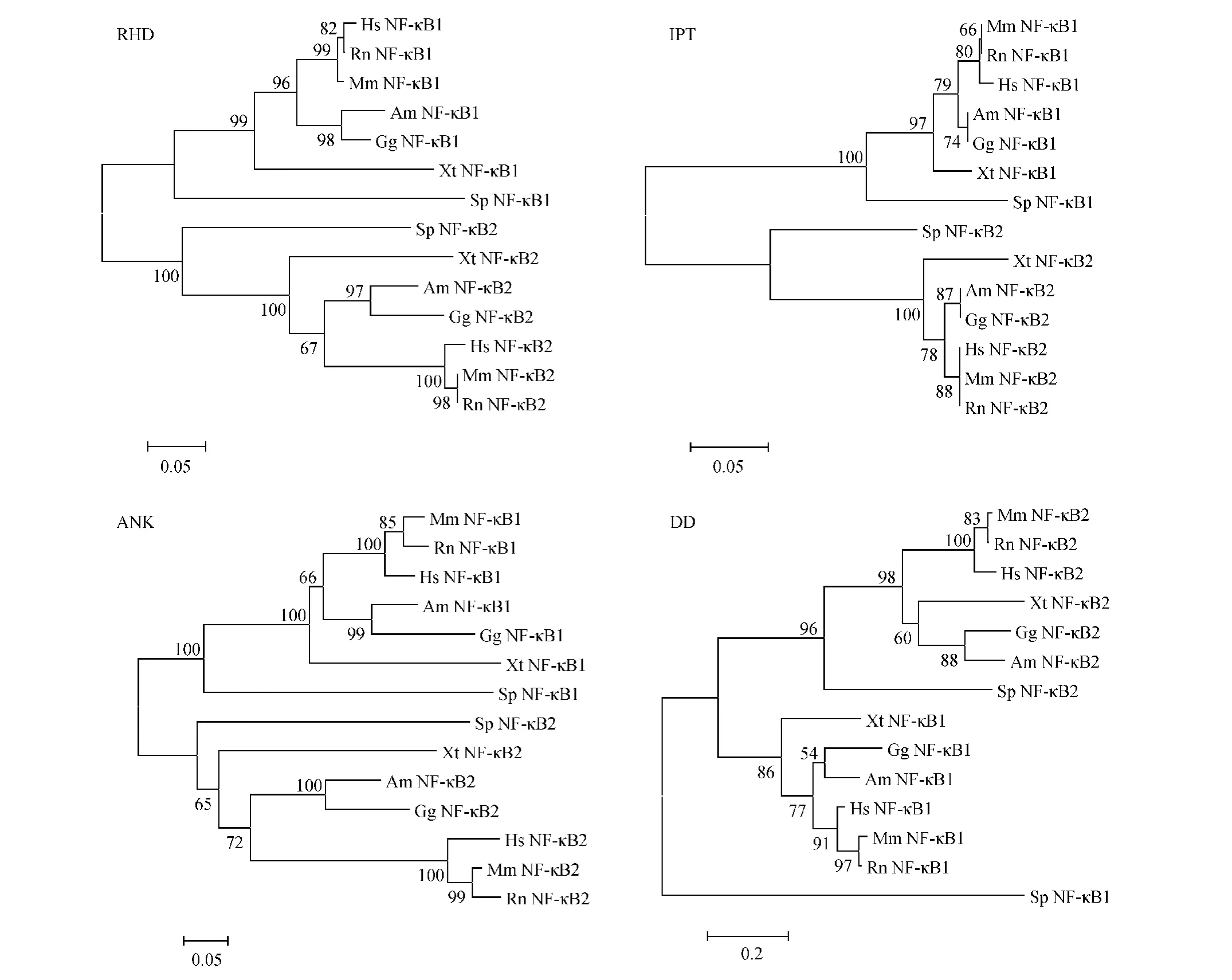
圖2 NF-κB1/24個結構域RHD、IPT、ANK與DD氨基酸序列的系統發育樹Fig.2 The phylogenetic trees of RHD,IPT,ANK and DD of NF-κB1/2based on their amino acid sequences
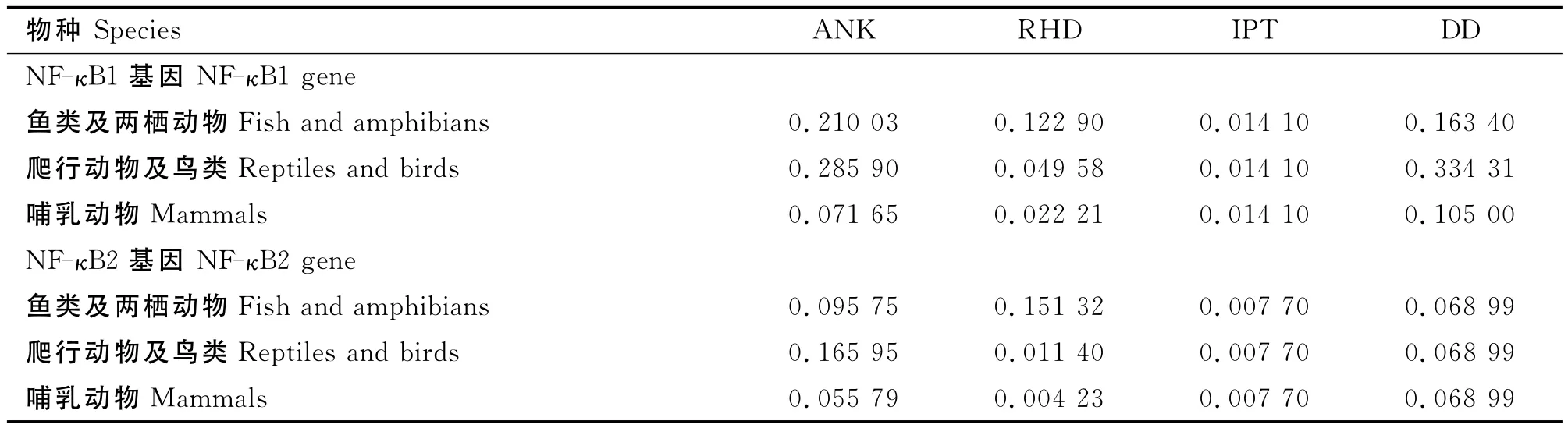
表1 NF-κB1/2基因各結構域在脊椎動物各個群類中的ω均值Table 1 The average value ofωof domains of NF-κB1/2genes in different vertebrate groups

圖3 NF-κB1/2的RHD、IPT、ANK和DD保守結構域區域比對Fig.3 Alignment of RHD,IPT,ANK and DD conserved domains of NF-κB1/2
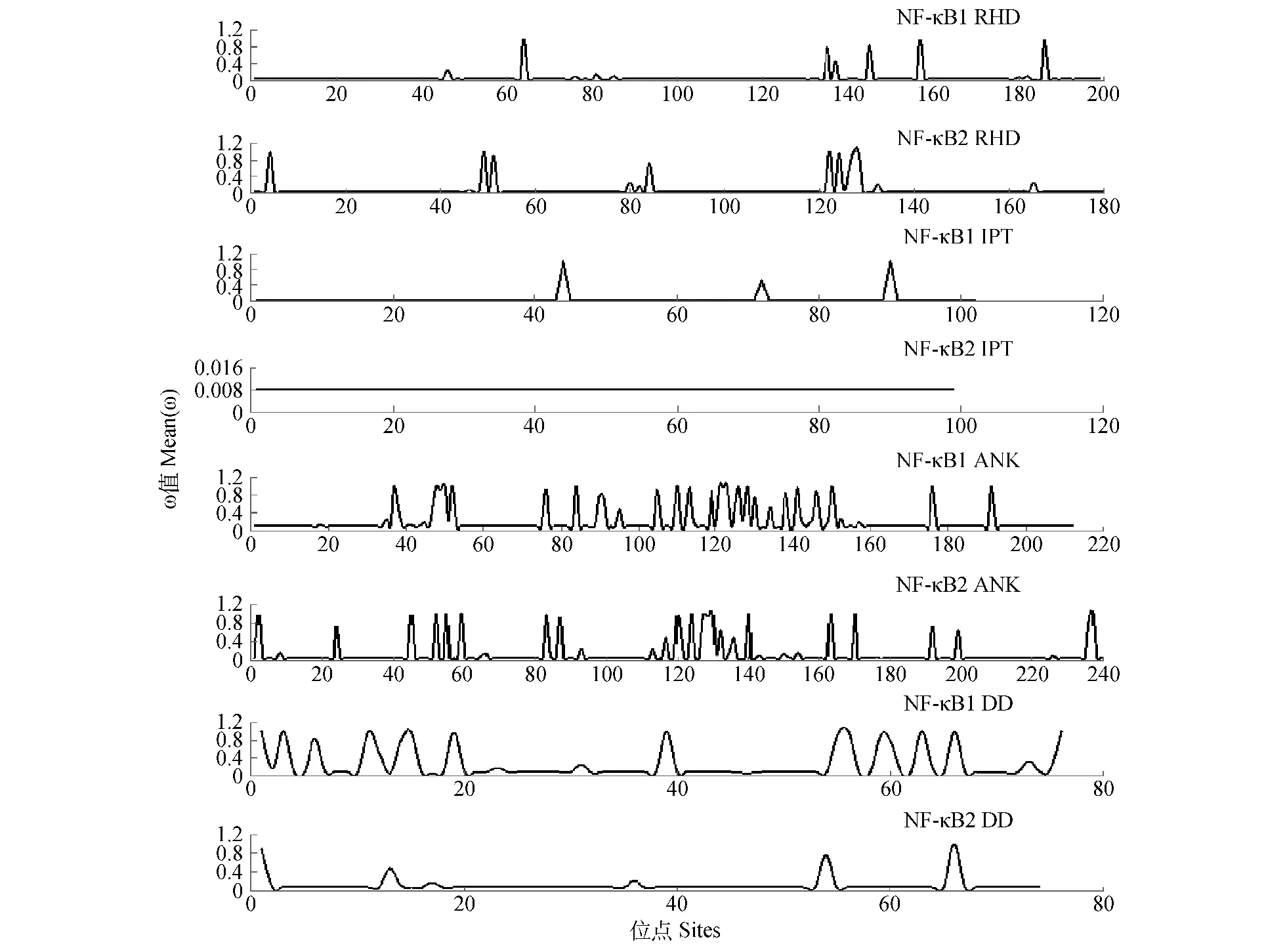
圖4 NF-κB1/2RHD、IPT、ANK與DD結構域各位點選擇壓力Fig.4 The selection pressure of RHD,IPT,ANK and DD conserved domains of NF-κB1/2
RHD、IPT、ANK 與 DD 是 NF-κB1/2亞家族成員重要的典型結構域,早在兩側對稱動物時期4個結構域就已經形成[8],且這樣的序列結構一直持續到了哺乳動物[8,18]。可以推斷,RHD、IPT、ANK與DD在NF-κB1與NF-κB2基因亞家族分子進化特征的形成和分子功能分歧的產生方面扮演了重要的角色。本研究構建了各個結構域氨基酸系統發育樹,發現由它們的氨基酸序列構建的系統發育樹與基于全序列構建的發育樹形態基本相同,說明NF-κB1和 NF-κB2分歧后,NF-κB1和 NF-κB2各個結構域的進化趨勢與其整體序列基本一致。
選擇壓力分析能使人們對NF-κB1/2在進化中所受到的環境阻力與其序列位點的變異情況有更深入的認識。因此,為了更進一步探索NF-κB1/2在脊椎動物階段的進化歷程,筆者又分別分析了NF-κB1/2各個結構域在不同動物類群中(魚類、鳥類、哺乳動物)的選擇壓力,發現不同種類動物NF-κB1/2保守結構域 ω值存在差異,說明 NF-κB1/2各個結構域在不同的進化階段存在著明顯不同的進化歷程。而在對NF-κB1/2各個結構域序列位點的分析中,發現NF-κB1/2整體序列相對保守,不存在顯著的正選擇位點。不過NF-κB2的DD所承受的選擇壓力卻明顯大于NF-κB1的DD,這很可能是由于NF-κB2的DD所含有的水解抑制區(Processing inhibitory domain,PID)在生理過程中的重要作用所導致[19]。
另外,對脊椎動物 NF-κB1/2 的 RHD、IPT、ANK和DD與直系、旁系同源結構的同源性分析顯示,NF-κB1/2的序列發生了各自獨立的進化,且這樣的獨立進化在RHD中表現的尤為顯著,暗示NF-κB1/2在功能上的分工越來越明確。而IPT表現的高保守性與它在生理過程中的重要功能相吻合[5,20]。ANK相對于其他3個結構域在脊椎動物的NF-κB1/2間擁有顯著的差異,推測它可能是導致NF-κB1/2在脊椎動物階段序列、功能差異形成的重要因素。而DD僅在NF-κB1/2之間存在較大的差異,且這樣的差異在魚類中就已經表現出來了,這不僅說明了它在脊椎動物階段中的保守性,也暗示了NF-κB1/2的DD分歧的年代較為久遠,甚至可能與NF-κB1/2基因的分歧有一定關聯,但是因為NF-κB1/2的分化早于脊椎動物而晚于兩側對稱動物,期間相關的動物序列素材較少,因此人們無法進行確切的論證。
綜上,在脊椎動物的各個類群中,NF-κB1/2承受著不同的選擇壓力,它們的4個結構域也表現出了不同的變異程度與特點。NF-κB1/2在脊椎動物中的進化與功能分歧主要由ANK的序列變異造成,而NF-κB1/2在脊椎動物之前的分歧很可能與DD有著密切的聯系。
(References):
[1]VALLABHAPURAPU S,KARIN M.Regulation and function of NF-κB transcription factors in the immune system[J].Annu Rev Immunol,2009,27(1):693-733.
[2]IWANASZKO M,BRASIER A R,KIMMEL M.The dependence of expression of NF-κB-dependent genes:statistics and evolutionary conservation of control sequences in the promoter and in the 3′UTR[J].BMC Genomics,2012,13:182.
[3]GUTIERREZ H,DAVIES A M.Regulation of neural process growth,elaboration and structural plasticity by NF-kB[J].Cell,2011,34(6):316-325.
[4]BAEUERLE P A,BALTIMORE D.NF-κB:ten years after[J].Cell,1996,87(1):13-20.
[5]BAKKAR N,GUTTRIDGE D C.NF-κB signaling:a tale of two pathways in skeletal myogenesis[J].Physiol Rev,2010,90(2):495-511.
[6]GAUTHIER M,DEGNAN B M.The transcription factor NF-κB in the demosponge Amphimedon queenslandica:insights on the evolutionary origin of the Rel homology domain[J].Dev Genes Evol,2008,218(1):23-32.
[7]SIMEONIDIS S,STAUBER D,CHEN G,et al.Mechanisms by which IκB proteins control NF-κB activity[J].Proc Natl Acad Sci U S A,1999,96(1):49-54.
[8]SAVINOVA O V,HOFFMANN A,GHOSH G.The Nfkb1and Nfkb2proteins p105and p100function as the core of high-molecular-weight heterogeneous complexes[J].Mol Cell,2009,34(5):591-602.
[9]WHITESIDE S T,ISRAEL A.IκB proteins:structure,function and regulation[J].Semin Cancer Biol,1997,8(2):75-82.
[10]HUANG Y H,TEMPERLEY N D,REN L M,et al.Molecular evolution of the vertebrate TLR1gene family-a complex history of gene duplication,gene conver-sion,positive selection and co-evolution[J].BMC Evol Biol,2011,11(1):149.
[11]LU M X,HUA J,CUI Y D,et al.Five small heat shock protein genes from Chilo suppressalis:characteristics of gene,genomic organization,structural analysis,and transcription profiles[J].Cell Stress Chaperones,2014,19(1):91-104.
[12]QIAN Y H,WU H Y,JI X Y,et al.Mitochondrial genome of the stonefly kamimuria wangi(Plecoptera:Perlidae)and phylogenetic position of plecoptera based on mitogenomes[J].PLoS ONE,2014,9(1):e86328.
[13]徐懷亮.7個靈長類物種PRSS12基因編碼區序列測定與進化分析[J].東北林業大學學報,2010,38(4):85-88.XU H L.Sequencing and phylogenetic analysis of PRSS12coding region of seven primate[J].Journal of Northeast Forestry University,2010,38(4):85-88.(in Chinese)
[14]PICONE B,CHRISTOFFELS A.Molecular evolution of key receptor genes in primates and non-human primates[J].J Genet Genomics,2014,2(4):57-61.
[15]ARENAS M,POSADA D.Simulation of genome-wide evolution under heterogeneous substitution models and complex multispecies coalescent histories[J].Mol Biol Evol,2014,31(5):1295-1301.
[16]ZHAO H,ZHOU Y,PINTO C M,et al.Evolution of the sweet taste receptor gene Tas1r2in bats[J].Mol Biol Evol,2010,27(11):2642-2650.
[17]YU L,JIN W,ZHANG X,et al.Evidence for positive selection on the leptin gene in Cetacea and Pinnipedia[J].PloS ONE,2011,6(10):e26579.
[18]HUGUET C,CREPIEUX P,LAUDET V.Rel/NF-kappa B transcription factors and I kappa B inhibitors:evolution from a unique common ancestor[J].Oncogene,1997,15(24):2965-2974.
[19]李 賢,刑 達,陳小佳.核因子KB抑制蛋白家族的研究進展[J].中國病理生理雜志,2006,22(12):2480-2484.LI X,XING D,CHEN X J.Advances of nuclear factor KB of inhibit protein family[J].Chinese Journal of Pathophysiology,2006,22(12):2480-2484.(in Chinese)
[20]CRAMER P,MüLLER C W.A firm hand on NFκB:structures of the IκBα-NFκB complex[J].Structure,1999,7(1):R1-R6.

