MC1R基因編碼區(qū)的系統(tǒng)發(fā)育分析和正選擇位點(diǎn)檢測
李麗莎+李祥龍+周榮艷+李蘭會+張永改+馬夢云+張秀玲


摘要: 黑素皮質(zhì)素受體1(melanocortin 1 receptor,MC1R)基因在黑色素細(xì)胞的表達(dá)上發(fā)揮重要作用,并與皮膚色素沉積密切相關(guān)。MC1R基因的選擇壓力分析對識別重要的功能位點(diǎn)具有深遠(yuǎn)影響。為研究不同動物MC1R基因在進(jìn)化過程中是否受到正選擇作用,基于位點(diǎn)模型對MC1R基因進(jìn)行研究。結(jié)果表明,動物MC1R基因主要經(jīng)歷中性漂變和純化選擇作用,并且發(fā)現(xiàn)MC1R基因受到正選擇作用的是編碼29、191、253、304氨基酸的位點(diǎn)。本研究從分子進(jìn)化的角度為MC1R基因調(diào)控黑色素的形成提供了一個新的思路。
關(guān)鍵詞: MC1R;分子進(jìn)化;親緣關(guān)系;系統(tǒng)發(fā)育;正選擇
中圖分類號: Q756 文獻(xiàn)標(biāo)志碼: A 文章編號:1002-1302(2016)03-0044-04
黑素皮質(zhì)素受體1(melanocortin 1 receptor,MC1R)基因,也稱為促黑素細(xì)胞激素受體(MSHR)基因,該基因只有1個編碼區(qū),由擴(kuò)展位點(diǎn)(extension locus,E)編碼,是控制動物黑色素合成的一個重要基因。哺乳動物的MC1R一般由310個氨基酸組成,有7個跨膜結(jié)構(gòu)域,是G蛋白耦合受體-黑素皮質(zhì)素受體(melanocortin receptor,MCRs)的家族成員之一[1],該基因在黑色素細(xì)胞的表達(dá)上發(fā)揮重要作用,并與皮膚色素沉積密切相關(guān)。MC1R與α-促黑素(α-melanocyte stimulating hormone,α-MSH)和腎上腺皮質(zhì)激素(ACTH)結(jié)合,增強(qiáng)了腺苷酸環(huán)化酶的活性,使環(huán)腺苷酸水平提高,進(jìn)而提高酪氨酸激酶(TYR)表達(dá),從而形成黑色素[2]。它們之間的結(jié)合使動物毛色或羽色的調(diào)控得以正常進(jìn)行。目前,已知一些MC1R基因變異引起腺苷酸環(huán)化酶活化能力不同,并且與小鼠、牛、馬、狐貍、家雞等動物中的皮毛差異有關(guān)[3-4]。許多哺乳動物有著同源特征的MC1R基因已被描述,而對于鳥類來講,MC1R基因色素性狀的調(diào)控機(jī)理與哺乳動物相同[5],因此MC1R基因通過控制真黑色素的數(shù)量來控制哺乳動物毛色及鳥類羽色,某些動物疾病的發(fā)生也與MC1R基因有關(guān)[6]。
正選擇(positive selection)也稱為達(dá)爾文選擇(Darwinian selection),是指將具有提高個體適合度的有利突變的等位基因在某個群體中固定下來的選擇作用,從而適應(yīng)不同的生存環(huán)境[7]。對正選擇的研究能更好地理解生物物種的進(jìn)化過程。從基因水平上來檢測適應(yīng)性進(jìn)化,這既有利于揭示生物的進(jìn)化史,同時加深對該基因的結(jié)構(gòu)和功能變異的理解[8]。
隨著對MC1R基因的進(jìn)一步深入研究,全面檢測MCIR基因位點(diǎn)將對動物品種多樣性的保護(hù)和利用提供依據(jù)。對MC1R基因的研究已經(jīng)數(shù)年,傳統(tǒng)研究大多集中在MC1R基因的結(jié)構(gòu)、生物學(xué)功能和作用機(jī)理,往往忽略對其結(jié)構(gòu)、功能和作用機(jī)理起決定作用的基因序列的研究。在這些序列中蘊(yùn)藏著大量的生物信息,對今后MC1R基因的深入研究提供重要依據(jù)和參考。本研究對21種動物MC1R基因編碼區(qū)進(jìn)行分子進(jìn)化分析,以期明確該基因在動物演化過程中是否發(fā)生了正選擇作用,從而更加深入了解MC1R基因。
1 材料與方法
1.1 序列數(shù)據(jù)
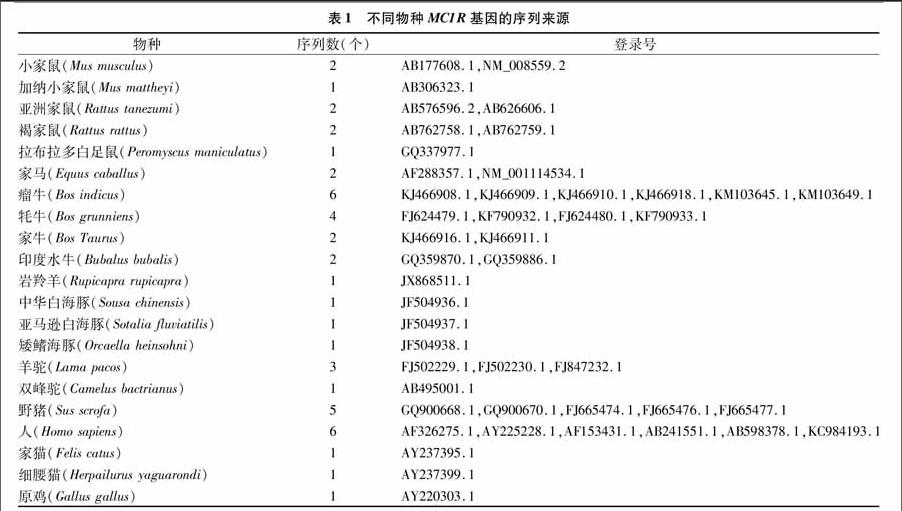
本研究利用已有的MC1R基因序列數(shù)據(jù)進(jìn)行研究,所有的數(shù)據(jù)來源于NCBI網(wǎng)站(http://www.ncbi.nlm.nih.gov/)GenBank數(shù)據(jù)庫,下載20種哺乳動物45條MC1R基因的編碼區(qū)(963 bp),再加上1條原雞(AY220303.1 Gallus gallus)序列作為外群,總共21個物種46條MC1R基因序列(表1)。
1.2 方法
1.2.1 序列分析 利用Clustal W 2.1軟件對MC1R基因的蛋白序列進(jìn)行聯(lián)配,再通過Pal2nal[9]在線工具生成密碼子多序列比對,生成序列文件。使用Bioedit 7.0軟件[10]對序列進(jìn)行編輯并分別保存成FASTA格式和PHY格式的文件。用MEGA 6.0軟件[11]將比對序列轉(zhuǎn)化成NEXUS格式用于貝葉斯算法來構(gòu)建系統(tǒng)發(fā)育樹。利用DAMBE軟件[12]進(jìn)行堿基替代飽和度檢驗(test of substitution saturation),以確定序列是否適合建樹,若建樹所用的序列沒有達(dá)到飽和,則可以建樹并進(jìn)行系統(tǒng)發(fā)育分析,若達(dá)到飽和則無建樹的必要。通過該軟件將比對后序列轉(zhuǎn)化成PAML格式用于選擇壓力分析。
1.2.2 系統(tǒng)發(fā)育樹的構(gòu)建 通過PAUP4.0[13]和Modeltest3.7[14]計算出符合該序列的核苷酸最佳替換模型。基于赤池信息量準(zhǔn)則(Akailke Information Criterion,AIC)選出的模型為TIM3+I+G,其參數(shù)結(jié)果用于MrBayes軟件[15]的計算,利用貝葉斯算法來構(gòu)建MC1R基因的系統(tǒng)發(fā)育樹。貝葉斯算法是基于最大似然法(Maximum Likelihood,ML)和貝葉斯推理法(Bayesian Inference,BI)的系統(tǒng)發(fā)生分析程序,其后驗概率(posterior probabilities)通過3條熱鏈(heated chain)和1條冷鏈(cols chain)運(yùn)行1 000 000代估計,MCMC(Markov Chain Monte Carlo)分析中命令mcmc Samplefreq=100,其含義為每100代保存1棵樹,直至average standard deviation of split frequencies值小于0.01(該值代表2個獨(dú)立分析當(dāng)前的相似程度)可認(rèn)為達(dá)到平衡。丟棄老化樣本(sump burnin=2 500)后由剩余樣本來構(gòu)建合意樹(Majority consensus tree,Bayesian tree)。獲得的系統(tǒng)發(fā)育樹可通過Treeview軟件[16]來觀看。
1.2.3 正選擇位點(diǎn)的檢測 Codeml程序在估算蛋白質(zhì)編碼序列同義替換和非同義替換速率以及檢測序列是否經(jīng)受正選方面被廣泛使用。本研究利用Codeml程序來進(jìn)行位點(diǎn)模型(site models)分析,以檢測基因在進(jìn)化過程中所經(jīng)受的選擇壓力的變化[13]。位點(diǎn)模型都是基于選擇壓力參數(shù)ω(編碼蛋白質(zhì)的核苷酸的非同義突變dN與同義突變dS的比值)來衡量分子進(jìn)化受到選擇壓力的方向和量度。若ω>1,即非同義突變被固定的速率遠(yuǎn)遠(yuǎn)大于同義突變,表明該位點(diǎn)受到正選擇壓力作用,位于正選擇壓力作用下的變異有利于新變異體的生存,同時該密碼子被稱為正選擇位點(diǎn)[17-19],而ω=1和 ω<1 分別表示基因在進(jìn)化過程中經(jīng)歷了中性選擇和負(fù)選擇。其中,位點(diǎn)模型[20-21]假設(shè)不同位點(diǎn)的進(jìn)化速率不同,但在系統(tǒng)發(fā)育樹的不同分枝上沒有差別。參考以下6種模型:(1)模型M0(單一速率模型)假設(shè)不同位點(diǎn)進(jìn)化速率相同;(2)模型M1a(中性選擇模型)假設(shè)存在一部分保守位點(diǎn),此時ω<1且其在序列中所占比例為p0,另一部分為中性選擇位點(diǎn),此時ω=1且其在序列中所占比例為p1=1-p0;(3)模型M2a(正選擇模型)是在M1a模型的基礎(chǔ)上加入正選擇位點(diǎn)的比例即p2=1-p1-p0;(4)模型M3(離散模型)假設(shè)p0、p1和p2分別表示負(fù)選擇、中性選擇和正選擇,其對應(yīng)的選擇壓力參數(shù)分別是ω0、ω1和ω2;(5)模型M7(Beta分布模型)假設(shè)0<ω<1;(6)模型M8(Beta-ω分布模型)假設(shè)一部分位點(diǎn)的ω>1。利用似然比檢驗(Likelihood ratio test,LRT)來比較零假設(shè)和備擇假設(shè)模型:M0與M3、M1a與M2a 和M7 與M8的最大似然值對數(shù)差的2倍(2ΔlnL),再由改良后的χ2分布進(jìn)行似然比檢驗,由P值來判斷備擇假設(shè)是否成立。
2 結(jié)果與分析
2.1 不同物種MC1R基因的堿基替代飽和度檢驗
因為進(jìn)化中轉(zhuǎn)換發(fā)生的頻率要高于顛換,更容易經(jīng)受替換和飽和效應(yīng)的影響,并且飽和效應(yīng)會直接影響到系統(tǒng)發(fā)育分析結(jié)果的可信度[22],所以在系統(tǒng)發(fā)育分析中檢測堿基替代的飽和度是至關(guān)重要的。因為編碼序列中的三聯(lián)體密碼子第2個編碼位置通常是保守的,而第3個密碼子位置具有兼并性且對核苷酸同義替換有很大的貢獻(xiàn)。普遍認(rèn)為這是中性理論的微觀證據(jù)。如果第3個密碼子位置處替代達(dá)到飽和度,那么序列將會失去進(jìn)化信號,則以此編碼序列來研究基于進(jìn)化機(jī)制的結(jié)論可信度不高[23]。本研究使用DAMBE軟件在F84模型下檢測堿基替代的飽和性,分別利用密碼子3個位置處核苷酸轉(zhuǎn)化數(shù)(s)和顛換數(shù)(v)對遺傳距離作圖,從圖1可以看出,結(jié)果均接近線性回歸。表明堿基替換未達(dá)到飽和,因此可以進(jìn)行系統(tǒng)發(fā)育分析。
2.2 不同物種MC1R基因的系統(tǒng)發(fā)育分析
本研究在GenBank數(shù)據(jù)庫進(jìn)行搜索和篩選,共獲得21種動物46條MC1R基因的編碼區(qū)序列:小家鼠、牦牛、人、野豬、家馬和家馬等等。利用貝葉斯方法構(gòu)建系統(tǒng)發(fā)育樹,利用原雞的MC1R基因編碼區(qū)序列作為外類群,建樹結(jié)果見圖2。
由MC1R基因構(gòu)建的系統(tǒng)發(fā)育樹主要分成2大分支。一支為牦牛、瘤牛、家牛、印度水牛、野豬、家馬、巖羚羊、羊駝、雙峰駝、中華白海豚、亞馬遜白海豚、矮鰭海豚、家貓、細(xì)腰貓14種物種,其中瘤牛、牦牛、家牛、印度水牛、巖羚羊、中華白海豚、亞馬遜白海豚和矮鰭海豚8個物種之間親緣關(guān)系較近,而家馬、羊駝、雙峰駝、野豬、家貓和細(xì)腰貓6個物種間親緣關(guān)系較近;另一支為小家鼠、加納小家鼠、亞洲家鼠、褐家鼠、拉布
拉多白足鼠、人6種物種,其中小家鼠、加納小家鼠、亞洲家鼠、褐家鼠和拉布拉多白足鼠5個物種之間親緣關(guān)系較近。原雞與哺乳動物之間區(qū)別明顯。由此可見,動物MC1R基因構(gòu)建的系統(tǒng)發(fā)育樹能很好的反應(yīng)不同物種之間的親緣關(guān)系。
2.3 正選擇位點(diǎn)分析
通過MrBayes軟件構(gòu)建動物MC1R基因的系統(tǒng)發(fā)育樹后,利用PAML 4軟件分析MC1R基因在進(jìn)化過程中所經(jīng)受的選擇壓力(表2)。第1對模型M0和M3似然比檢驗結(jié)果顯示2ΔlnL=169.42,df=4,P<0.01。因此模型M3顯著優(yōu)于模型M0,說明位點(diǎn)間承受的選擇壓力具有異質(zhì)性。模型M3的3類密碼子位點(diǎn)所對應(yīng)的ω值分別為0.035 30,0.279 60和31.853 85,由于ω2對應(yīng)的p2為0,因此不存在正選擇位點(diǎn)。第2對模型M1a和M2a似然比檢驗結(jié)果顯示 2ΔlnL=0,df=2,P=1.00。因此備擇假設(shè)模型M2a不成立,但并不推薦該模型為參考標(biāo)準(zhǔn)。第3對模型M7和M8似然比檢驗結(jié)果顯示2ΔlnL=6.18,df=2,P=0.045。因此備擇假設(shè)模型M8成立,其ω=1.501 4>1,表明MC1R基因受到選擇壓力,存在正選擇位點(diǎn)(29W,191L,253L,304L)。
本研究用于檢測正選擇位點(diǎn)的3對模型發(fā)現(xiàn)MC1R基因編碼的氨基酸位點(diǎn)在進(jìn)化過程中所經(jīng)受中性選擇和純化選擇作用比例較高,但有4個氨基酸進(jìn)化受到正選擇作用的驅(qū)動。
3 討論與結(jié)論
在進(jìn)化過程中,基因的復(fù)制過程所產(chǎn)生的遺傳變異會造成功能分歧,隨后純化選擇將功能固定下來。少數(shù)位點(diǎn)甚至單個位點(diǎn)的核苷酸替代都能改變其編碼的蛋白質(zhì)功能。而整個基因大多數(shù)位點(diǎn)都處于純化選擇或中性選擇的進(jìn)化狀態(tài),以至于少數(shù)位點(diǎn)的正選擇信息會被大多數(shù)位點(diǎn)所稀釋,從而導(dǎo)致正選擇信息被整體湮沒[24]。現(xiàn)代分子適應(yīng)性進(jìn)化分析多以dN/dS的比值來衡量選擇壓力。若ω>1,且兩兩模型之間差異顯著,則表明編碼序列在對應(yīng)的位點(diǎn)經(jīng)受正選擇作用。與傳統(tǒng)方法相比,這種基于最大似然法所估計的正選擇檢測方法,可把長期由純化選擇和中性選擇作用掩蓋下的正選擇位點(diǎn)識別出來,反應(yīng)出更高的靈敏度[25]。
本研究采用位點(diǎn)模型來檢測選擇壓力,結(jié)果表明,在21種動物中只檢測到了4個正選擇位點(diǎn),可見MC1R基因編碼的蛋白從整體水平上主要受中性漂變和純化選擇的作用。推測可能是由以下2個原因:(1)MC1R基因所編碼的蛋白功能重要,氨基酸序列較為保守。(2)MC1R基因序列進(jìn)化歷史久遠(yuǎn),且其較短的序列只能提供較少的可檢測位點(diǎn),這樣也難以檢測出適應(yīng)性進(jìn)化信號[26]。
適應(yīng)性進(jìn)化從整體水平上了解了動物MC1R基因在進(jìn)化過程中所經(jīng)受的選擇作用,同時也分析了不同物種之間親緣關(guān)系的遠(yuǎn)近。對于親緣關(guān)系較近的物種,選擇壓力小;而親緣關(guān)系較遠(yuǎn)的物種選擇壓力較大且基因序列較保守。MC1R基因作為控制動物毛色形成的主效基因,經(jīng)證實其變異可作為許多哺乳動物黑、紅毛色性狀的變化的主要原因[27],該基因功能改變會表現(xiàn)出褐黑色素的紅色或黃色性狀,反之會表現(xiàn)出真黑色素的黑色或棕色性狀[28]。
本研究針對MC1R基因編碼區(qū)進(jìn)行分子進(jìn)化分析,發(fā)現(xiàn)MC1R基因編碼的蛋白從整體水平上主要受中性漂變和純化選擇的作用,對于正選擇作用的分析,共檢測到4個正選擇位點(diǎn),這些位點(diǎn)對探討MC1R基因編碼蛋白功能的改變提供了重要依據(jù),從分子進(jìn)化的角度為MC1R基因調(diào)控黑色素的形成提供了一個新的思路。
參考文獻(xiàn):
[1]甘海云,李建斌,王紅梅,等. 黑素皮質(zhì)激素受體1基因與牛的毛色[J]. 家畜生態(tài)學(xué)報,2007,28(3):99-102.
[2]楊永升,李 寧,鄧學(xué)梅,等. 黑素皮質(zhì)素受體1——哺乳動物黑色素形成中的關(guān)鍵基因[J]. 遺傳,2004,26(4):544-550.
[3]Sazanov A,Masabanda J,Ewald D,et al. Evolutionarily conserved telomeric location of BBC1 and MC1R on a microchromosome questions the identity of MC1R and a pigmentation locus on chromosome 1 in chicken[J]. Res Dec,1998,8:651-654.
[4]Hunt G,Rot H J,van Oost B A. Identification of a premature stop codon in the melanocyte-stimulating hormone receptor gene(MC1R) in Labrador and Golden ret rievers with yellow coat color[J]. Animal Genetics,2000,31(3):194-199.
[5]Boissy R E,Nordlund J J,Rheins L A. Molecular basis of congenital hypopigmentary disorders in humans:a review[J]. Pigment Cell Research,1997,10:21-24.
[6]Leal-Klevezas D S,Martínez-Vázquez I O,López-Merino A,et al. Single-step PCR for detection of Brucella spp. from blood and milk of infected animals[J]. Journal of Clinical Microbiology,1995,33(12):3087-3090.
[7]Shimizu K K,Purugganan M D. Evolutionary and ecological genomics of arabidopsis[J]. Plant Physiology,2005,138(2):578-584.
[8]Nei M,Kumar S. Molecular evolution and phylogenetics[M]. New York:Oxford University Press Inc,2000.
[9]Suyama M,Torrents D,Bork P. PAL2NAL:robust conversion of protein sequence alignments into the corresponding codon alignments[J]. Nucleic Acids Research,2006,34:W609-W612.
[10]Hall T A. Bioedit:a user-friendly biological sequence alignment editor and analysis program for Windows 95/98/NT[J]. Nucleic Acids Symp Ser,1999,41:95-98.
[11]Tamura K,Dudley J,Nei M,et al. MEGA4:molecular evolutionary genetics analysis(MEGA)software version 4.0[J]. Molecular Biology and Evolution, 2007,24:1596-1599.
[12]Xia X,Xie Z. DAMBE:data analysis in molecular biology and evolution[J]. Journal of Heredity,2001,92:371-373.
[13]Yang Z H. PAML 4:phylogenetic analysis by maximum likelihood[J]. Molecular Biology and Evolution,2007,24(8):1586-1591.
[14]Posada D,Crandall K A. MODELTEST:testing the model of DNA substitution[J]. Bioinformatics,1998,14(9):817-818.
[15]Ronquist F,Huelsenbeck J P. MrBayes 3:bayesian phylogenetic inference under mixed models[J]. Bioinformatics,2003,19(12):1572-1574.
[16]Page M R D. TreeView:an application to display phylogenetic trees on personal computers[J]. Computer Applications in the Biosciences,1996,12(4):357-358.
[17]Choisy M,Woelk C H,Gue G J,et al. Comparative study of adaptive molecular evolution in different human immunodeficiency virus groups and subtype[J]. Journal of Virology,2004,78(4):1962-1970.
[18]Zhang C Y,Ding N,Chen K P,et al. Complex positive selection pressures drive the evolution of HIV-1 with different co-receptor tropisms[J]. Science China:Life Sciences,2010,53(10):1204-1214.
[19]許慧琳,張文彤,趙耐青,等. H2N2亞型人甲型流感病毒HA1序列進(jìn)化正選擇位點(diǎn)研究[J]. 中華流行病學(xué)雜志,2007,28(4):385-389.
[20]Nielsen R,Yang Z. Likelihood models for detecting positively selected amino acid sites and application to the HIV-1 envelope gene[J]. Genetics,1998,148(3):929-936.
[21]Yang Z. Maximum likelihood estimation on large phylogenies and analysis of adaptive evolution in human influenza virus A[J]. Journal of Molecular Evolution,2000,51(5):423-432.
[22]呂雪梅,王應(yīng)祥,張亞平. 蜂猴線粒體細(xì)胞色素b基因變異特點(diǎn)及系統(tǒng)發(fā)育分析[J]. 動物學(xué)研究,2001,22(2):93-98.
[23]梁國明,劉桂瓊,姜勛平. 反芻動物PRNP基因進(jìn)化機(jī)制研究[C]//中國畜牧獸醫(yī)學(xué)會養(yǎng)羊?qū)W分會全國養(yǎng)羊生產(chǎn)與學(xué)術(shù)研討會議論文集,2010.
[24]姬廣超,王明輝,高會江,等. 哺乳動物MT基因的進(jìn)化選擇與功能分歧[J]. 東北農(nóng)業(yè)大學(xué)學(xué)報,2010(9):82-88.
[25]Yang Z H. Inference of selection from multiple species alignments[J]. Current Opinion in Genetics & Development,2002,12(6):688-694.
[26]Yang Z. Computational molecular evolution[M]. New York:Oxford University Press,2006.
[27]Schmutz S M,Moker J S,Berryere T G,et al. An SNP is used to map MC1R to dog chromosome 5[J]. Animal Genetics,2001,32(1):43-44.
[28]Newton J M,Wilkie A L,He L,et al. Melanocortin 1 receptor variation in the domestic dog[J]. Mammalian Genome,2000,11(1):24-30.

