擴增子測序技術分析紅茶菌中優勢微生物的研究
張澤生,王春龍,劉清岱,*,王寶林(.天津科技大學食品工程與生物技術學院,天津300457;.天津豈均生物科技有限公司,天津300480)
擴增子測序技術分析紅茶菌中優勢微生物的研究
張澤生1,王春龍1,劉清岱1,*,王寶林2
(1.天津科技大學食品工程與生物技術學院,天津300457;2.天津豈均生物科技有限公司,天津300480)
紅茶菌作為一種傳統健康保健飲品,由于發酵過程中需要多種微生物的參與,因此需要對混合菌種進行高效的分離鑒定。本文通過提取紅茶菌中的基因組DNA,采用高通量測序的方法對16S rDNA和ITS的擴增子進行測序,實現對紅茶菌中優勢微生物的分析鑒定。通過對可操作分類單元進行豐度分析和物種分類樹統計,最終得到主要的細菌組成為:醋酸菌89.11%,擬桿菌5.56%,顫螺旋桿菌1.77%;優勢真菌組成為:酵母菌為93.48%,其中嗜酒假絲酵母61.76%,酵母菌Blastobotrys adeninivorans 30.97%;α多樣性分析結果顯示:測序數據較為合理,測序數據量大,可以反映樣品中絕大多數的微生物物種信息。
紅茶菌;擴增子測序;16S;ITS
紅茶菌是一種以糖茶水為原料,由醋酸菌、酵母菌等微生物共同發酵而制成的功能飲料,是一種純天然的健康保健飲品[1-2]。目前對于紅茶菌中混合菌種研究主要依靠傳統的微生物平板培養方法,這限制了很多微生物物種的分離鑒定,并且依賴表觀性狀對物種進行鑒定也可能導致誤認[3]。
擴增子測序就是通過PCR擴增,將目標區域DNA富集后進行高通量測序的研究策略。16S rDNA是最適于細菌系統發育和分類鑒定的指標,采用16S rDNA擴增子測序是利用保守區設計通用引物進行PCR擴增,然后對高變區進行測序分析和菌種鑒定,成為研究環境樣品中微生物組成結構的重要手段[4-5]。而對ITS擴增子進行測序,可以實現環境微生物中真菌多樣性分析。MiSeq測序系統采用邊合成邊測序的技術,每次運行最多能產生超過7 Gb的數據。目前采用MiSeq平臺對16S rDNA和ITS的一個或多個高變區測序,具有測序深度高、利于鑒定低豐度群落物種以及費用低的特點,已成為研究微生物群落多樣性的首選之策[6-7]。
本文通過提取紅茶菌中的基因組DNA,采用高通量測序的方法對16S rDNA和ITS的擴增子進行測序,對紅茶菌中微生物組成、種屬關系、相對豐富度以及微生物的多樣性進行了分析鑒定。
1 材料和方法
1.1原料
紅茶菌:天津豈均生物科技有限公司。
1.2方法
1.2.1細菌和真菌基因組DNA提取
CTAB法[8]:取1.5 mL紅茶菌,離心收集菌體,加入567μL的TE緩沖液,震蕩重懸細菌。然后,加入30 μL 10%SDS和15μL20mg/mL蛋白酶K,于37℃溫育1h,直至細菌裂解完全。加入100 μL 5mol/L NaCl和80 μL CTAB NaCl溶液,65℃溫育10 min。采用Tris飽和酚/氯仿/異戊醇(25∶24∶1,體積比)抽提,異丙醇沉淀DNA。70%乙醇洗滌沉淀1次后,將DNA溶于50 μL TE緩沖液,加入1 μL RNase A(10 mg/mL),4℃保存備用。采用瓊脂糖凝膠電泳檢測基因組DNA的純度和濃度,取適量的樣品于離心管中,使用無菌水稀釋樣品至1 ng/μL。
1.2.2PCR擴增和高通量測序
稀釋后的基因組DNA為模板;根據測序區域的選擇,使用帶Barcode的特異引物;使用New England Biolabs公司的使用高效和高保真的酶進行PCR,確保擴增效率和準確性。細菌的引物對應區域:16S V4區引物為515F-806R;ITS1區引物為ITS1F-ITS2。真菌的引物對應區域:16S V4區引物為515F-806R;ITS1區引物為ITS1F-ITS2。在30 μL的PCR反應體系中加入15 μL的PhusionRHigh-Fidelity PCR Master Mix with GC Buffer、0.2 μmol/L的正向和反向引物和10 ng模板DNA進行反應。PCR反應程序:98℃預變性1 min,30個循環98℃變性10 s,50℃退火30 s,72℃延伸60 s,最后72℃5 min。
PCR產物使用2%濃度的瓊脂糖凝膠進行電泳檢測,對主帶在400 bp~450 bp之間的樣品進行進一步的實驗研究。使用切膠回收試劑盒回收產物。使用建庫試劑盒進行文庫的構建,構建好的文庫經過Qubit定量和文庫檢測,合格后,使用MiSeq進行上機測序。
1.2.3生物信息學分析
采用Illumina MiSeq/HiSeq測序平臺得到的下機數據存在一定的低質量數據,會干擾分析的結果,因此在進一步分析前,需要對下機數據進行預處理,去除低質量數據去除切除引物序列,再次去除低質量數據引物不匹配、含、過短序列,最終得到的有效序列。
提取出每個操作分類單元(OUT)的代表序列后,用Uparse軟件進行物種的分類。最后,用Qiime軟件對樣品復雜度指數進行分析,并繪制相應的曲線。
2 結果與分析
2.1紅茶菌16srDNA和ITS序列的擴增
紅茶菌16s rDNA和ITS序列的擴增見圖1。
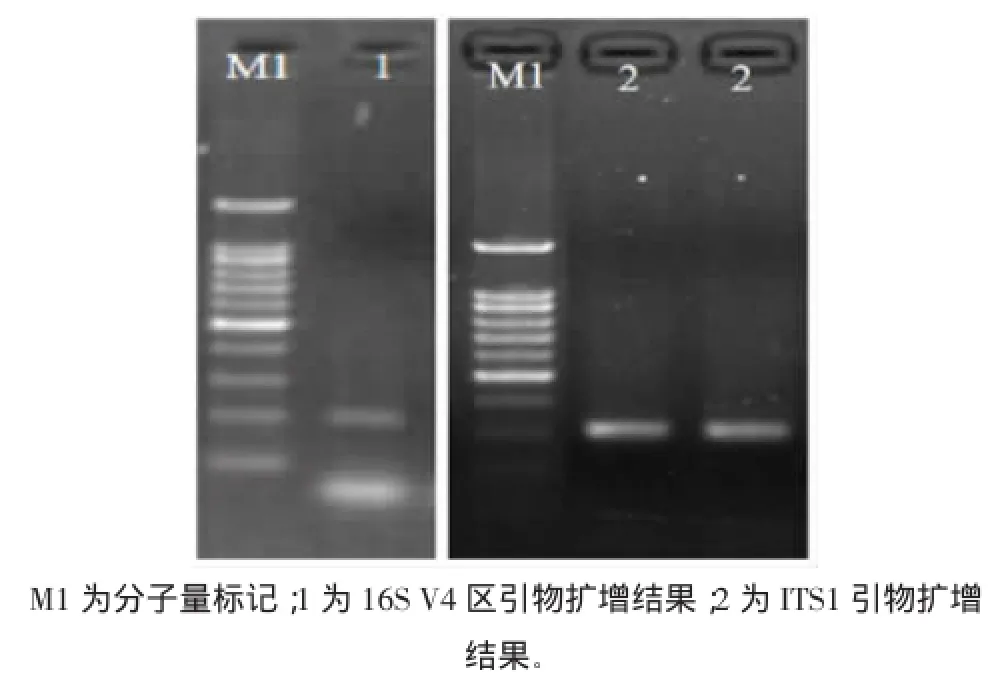
圖1 紅茶菌16s rDNA和ITS序列的擴增Fig.1 The amplified sequences of 16S rDNA and ITS of Kombucha
采用CTAB法提取紅茶菌中微生物基因組DNA,以其為模板進行PCR擴增,瓊脂糖電泳結果表明采用16S V4區引物和ITS1引物擴增都得到了目的條帶,目的條帶分子量約0.5 kb,表明16S V4區和ITS1區都能得到很好的擴增。
2.2測序信息OUT分析及物種注釋
2.2.1OUT分析
為了研究樣品的物種組成多樣性信息,用Uparse軟件[9]對所有樣品的全部序列聚類,默認提供以97% 和95%的一致性將序列聚類成為可操作分類單元結果。在操作分類單元(OUT)構建過程中,對不同樣品的有效序列數據,低頻數的序列和序列注釋數據等信息進行初步統計,16s rDNA擴增子序列總數為72 223;用于構建OTUs并且獲得分類信息的Tags數目為69 092;ITS擴增子序列總數為16 790;用于構建操作分類單元并且獲得分類信息的序列數目為16 217;兩類微生物可操作分類單元數據量較大,滿足發酵產物菌群物種注釋的要求。
2.2.2物種注釋
同一操作分類單元中的序列被視為是來源于某一個相同分類單元的序列,作為一個假定的分類單元。Uparse構建操作分類單元時會選取代表性序列(依據其算法原則,篩選的是操作分類單元中出現頻數最高的序列),將這些代表性序列集合用RDP Classifier[10]與GreenGene數據庫[11]對細菌進行物種注釋分析,用Qiime中的Blast方法與Unite-INSDC數據庫[12]對真菌進行物種注釋分析。
根據物種注釋結果,選取在門分類水平上最大相對豐度排名前十的門,生成的物種相對豐度分布柱形圖,見圖2。

圖2 細菌和真菌的物種相對豐度圖Fig.2 The chart of species relative abundance of fungus and bacteria
從圖2(a)可以看出,細菌門水平上物種的相對豐度從上往下依次為:其他,脫鐵桿菌門,梭桿菌門,醋桿菌門,放線菌,藍菌,疣微菌門,柔膜菌門,擬桿菌門,變形菌,厚壁菌門。從圖(b)可以看出,真菌門水平上物種的相對豐度從上往下依次為:其他,未分類,接合菌門,擔子菌,子囊菌。
2.2.3特定物種分類樹
基于樣品的物種分類結果,篩選特別關注的物種進行物種分類樹統計[13],見圖3。

圖3 細菌和真菌的特定物種分類樹Fig.3 The classification tree of specific species of fungus and bacteria
從圖3中,可以看出,紅茶菌中主要優勢細菌組成為:醋酸菌89.11%,擬桿菌5.56%,顫螺旋桿菌1.77%,沃氏嗜膽菌0.84%,腸道細菌Akkermansia muciniphila 0.55%,脫硫弧菌0.54%,瘤胃球菌0.45%。優勢真菌組成為:酵母菌為93.48%,其中嗜酒假絲酵母為61.76%,酵母菌Blastobotrys adeninivorans為30.97%;
2.3樣品α多樣性分析
α多樣性用于分析樣品內的群落多樣性[14],主要包含3個指標:稀釋曲線,物種豐富度和群落多樣性。用Qiime軟件對樣品復雜度指數進行計算并繪制的相應的曲線,以紅茶菌中細菌為例,如圖4。
從細菌和真菌的稀釋曲線、Chao1指數曲線、香農指數曲線可以明顯的看出,各曲線數值升高直至平滑說明測序數據較為合理,測序數據量足夠大,可以反映樣品中絕大多數的微生物物種信息。
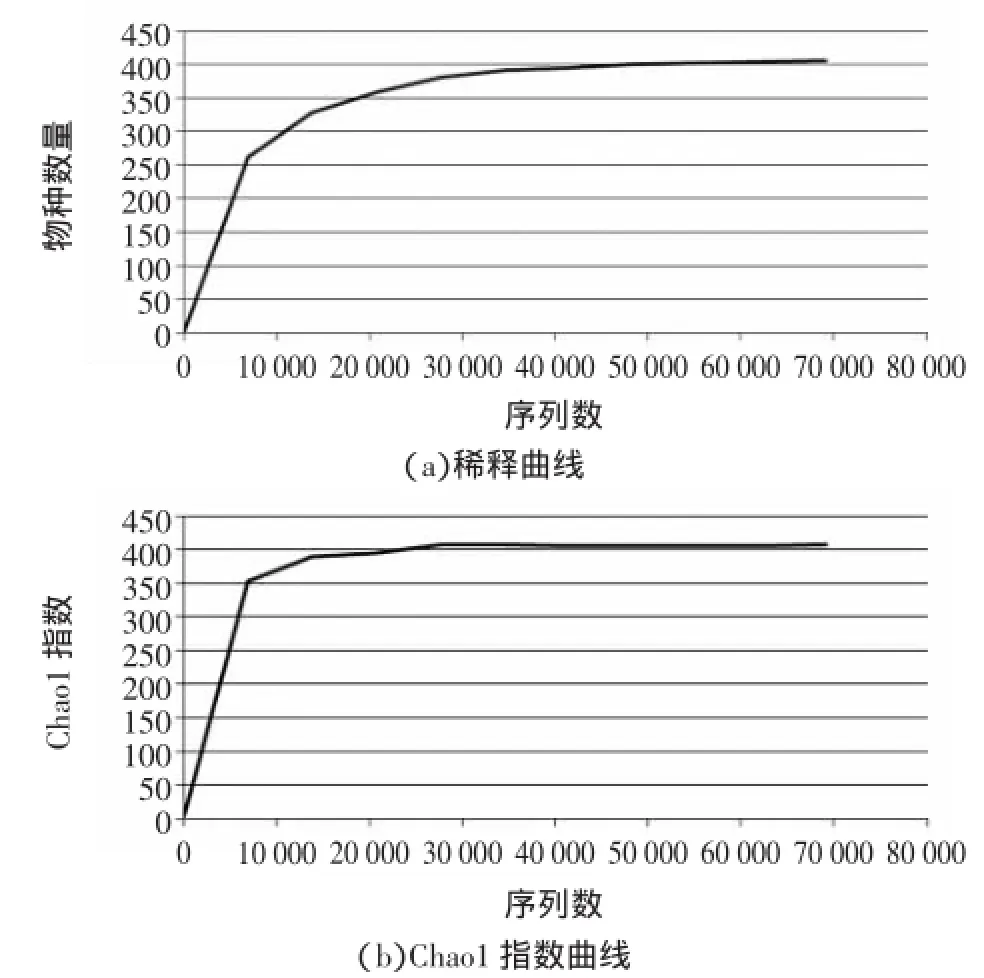
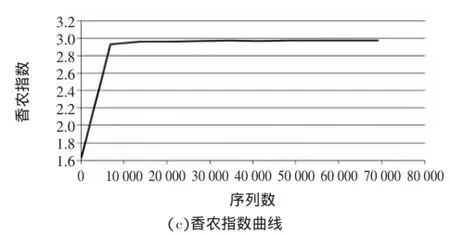
圖4 樣品中細菌的α多樣性分析Fig.4 Alpha diversity analysis of bacteria in the sample
3 結論
紅茶菌是由醋酸菌、酵母菌等有益微生物共同自然發酵而成,難以實現工業化的大規模生產。由于紅茶菌是多菌種發酵,因此優勢菌群以及相關的含量等還沒有系統全面的研究報道。隨著分子生物技術的發展,尤其是第二代測序技術的出現,使得微生物組學的研究更加全面和準確,可獲得全面、系統、結構化的微生物群落結構信息,為紅茶菌的工業化生產應用奠定基礎。
通過對紅茶菌中細菌16S rDNA、ITS的擴增子進行測序分析,確定了樣品中主要優勢細菌組成為:醋酸菌89.11%,擬桿菌5.56%,顫螺旋菌1.77%;通過ITS的擴增子測序,結果表明主要優勢真菌組成為:酵母菌為93.48%,其中嗜酒假絲酵母61.76%,酵母菌Blastobotrys adeninivorans 30.97%。從樣品復雜度分析可以看出,測序數據較為合理,測序數據量足夠大,可以反映樣品中絕大多數的微生物物種信息。
本文采用擴增子測序技術方法對紅茶菌中微生物的組成、種屬關系、物種相對豐富度、群落多樣性進行了鑒定分析,與傳統的方法相比準確性高,穩定性好,應用范圍廣泛,可以為研究復合益生菌發酵飲料及發酵過程中優勢菌群變化的方法提供參考。
[1]趙平,范鐵男,鄒積宏.紅茶菌的研究概況[J].黑龍江醫藥,2011,24(3):367-370
[2]吳燕,阮暉,何國慶.紅茶菌的研究和應用進展[J].食品工業科技,2012(8):436-438
[3]Marsh A J,O'Sullivan O,Hill C,et al.Sequence-based analysis of the bacterial and fungal compositions of multiple kombucha(tea fungus)samples[J].Food Microbiol,2014,38:171-178
[4] Youssef N,Sheik C S,Krumholz L R,et al.Comparison of species richness estimates obtained using nearly complete fragments and simulated pyrosequencing-generated fragments in 16S rRNA genebased environmental surveys[J].Applied and environmental microbiology,2009,75(16):5227-5236
[5]Hess M,Sczyrba A,Egan R,et al.Metagenomic discovery of biomassdegrading genes and genomes from cow rumen[J].Science,2011,331 (6016):463-467
[6] Degnan P H,Ochman H.Illumina-based analysis of microbial community diversity[J].The ISME journal,2013,6(1):183-194
[7]Caporaso J G,Lauber C L,Walters W A,et al.Ultra-high-throughput microbial community analysis on the Illumina HiSeq and MiSeq platforms[J].The ISME journal,2012,6(8):1621-1624
[8]朱飛舟,陳利玉,陳漢春.16S rRNA基因序列分析法鑒定病原細菌[J].中南大學學報(醫學版),2013,38(10):1035-1041
[9]Edgar R C.UPARSE:highly accurate OTU sequences from microbial amplicon reads[J].Nature methods,2013,10(10):996-998
[10]Wang Q,Garrity G M,Tiedje J M,et al.Naive Bayesian classifier for rapid assignment of rRNA sequences into the new bacterial taxonomy[J].Applied and environmental microbiology,2007,73(16):5261-5267
[11]Desantis T Z,Hugenholtz P,Larsen N,et al.Greengenes,a chimerachecked 16S rRNA gene database and workbench compatible with ARB[J].Applied and environmental microbiology,2006,72(7):5069-5072
[12]K?ljalg U,Nilsson R H,Abarenkov K,et al.Towards a unified paradigm for sequence-based identification of fungi[J].Molecular ecology,2013,22(21):5271-5277
[13]Li B,Zhang X,Guo F,et al.Characterization of tetracycline resistant bacterial community in saline activated sludge using batch stress incubation with high-throughput sequencing analysis[J].Water research,2013,47(13):4207-4216
[14]Whittaker R H.Evolution and measurement of species diversity[J]. Taxon,1972,21(2/3):213-251
Study on Analysis of the Dominant Microorganisms in Kombucha by the Technology of Amplicon Sequencing
ZHANG Ze-sheng1,WANG Chun-long1,LIU Qing-dai1,*,WANG Bao-lin2
(1.Institute of Food Engineering and Biotechnology,Tianjin University of Science and Technology,Tianjin 300457,China;2.Tianjin Qijun Biotechnology Co.,Ltd.,Tianjin 300480,China)
Study on the application of the amplification sequencing technology in the research of compound bacteria fermented beverage.Taking the Kombucha beverage as an example,throught the genomic DNA extraction in oral liquid of Kombucha,amplicon sequencing of 16S rDNA and ITS using the method of high-throughput sequencing of amplicons of sequencing to analysis and identification the dominant microbial in oral liquid of Kombucha.The classification and statistics of the species by the special species classification tree,finally got the main bacteria composition:Acetobacter was 89.11%,Bacteroides was 5.56%,Oscillospira was 1.77%.The main fungus composition:Yeast was 93.48%,of which Candida ethanolica was 61.76%,Blastobotrys adeninivorans was 30.97%.The result of Alpha Diversity analysis showed that:the sequencing data was more reasonable,the sequencing data amount was large enough,can reflect most of the microbial species information in the sample.The the application of the amplification sequencing technology has advantages in the analysis of the advantages of the compound bacteria fermented beverage and the detection of the content of probiotics.
Kombucha;amplicon sequencing;16S;ITS
2015-09-01
張澤生(1956—),男(漢),教授,博士,研究方向:天然產物活性成分。
劉清岱(1975—),男(漢),副教授,博士,研究方向:生物化學與分子生物學。

